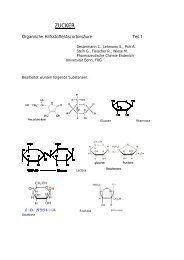
DNA Replikation
DNA Replikation
DNA Replikation
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
<strong>DNA</strong> <strong>Replikation</strong><br />
Beginn der <strong>DNA</strong> <strong>Replikation</strong> (am Beispiel der E.coli)<br />
Die <strong>Replikation</strong> beginnt nicht an jeder Stelle der <strong>DNA</strong> Strang sondern an einer<br />
einzigen Stelle (<strong>Replikation</strong>sursprung = Origin) der als OriC bezeichnet wird.<br />
Die <strong>Replikation</strong> verläuft dann in etwa gleiche Geschwindigkeit gleichzeitig in<br />
beide Richtungen –Uhrzeigersinn und entgegen.<br />
Die <strong>Replikation</strong>sgabeln treffen sich am Terminationsort gegenüber der<br />
<strong>Replikation</strong>sursprung.<br />
Mechanismus der <strong>Replikation</strong><br />
Die beide Stränge der Eltern-<strong>DNA</strong> dienen als Matrize für die Synthese neue<br />
<strong>DNA</strong>.<br />
Da die Elternstränge anti-parallel verlaufen und die <strong>DNA</strong> <strong>Replikation</strong><br />
semikonservativ ist ,muss die Gesamtrichtung der <strong>DNA</strong> Synthese einer<br />
Tochterstrang 5´ 3´ und der andere 3´ 5´sein.<br />
Problem. Alle <strong>DNA</strong> Polymerasen synthetisieren nur in 5´ 3´Richtung<br />
Lösung :Okazaki Fragmente für die 3´ 5´ Folgestrang!!!!<br />
Der OriC ist ein Sequenz von 245 Basenpaare auf dem E.coli Chromosom. Er<br />
enthält eine Tandemanordnung von 3 Oligonucleotiden aus 13 Basenpaare mit<br />
nahezu identischen Sequenzen und vier Bindungsstellen für das DnaA Protein
Die Bindung des DnaA Protein führt zur Entwindung der Matrize <strong>DNA</strong> und<br />
Synthese eines Primers(aber <strong>DNA</strong> muss superspiralisiert sein).<br />
Ein Komplex der DnaB und DnaC Proteine vereinigt sich mit der DnaA und<br />
führt zur Biegung und Öffnung der <strong>DNA</strong> Helix.<br />
DnaB ist ein Helicase und katalysiert die ATP getriebene Entwindung der<br />
<strong>DNA</strong> Helix.<br />
Single strang binding protein SSB, stabilisiert die entwundene <strong>DNA</strong>.<br />
Die <strong>DNA</strong> kann jetzt nur zuerst nach dem Aufbau eines Primers synthetisiert<br />
werden.<br />
Der Primer ist ein RNA und wird von der Primase synthetisiert,indem die<br />
Primase sich mit dem pre priming Komplex verbindet um ein Primosom zu<br />
bilden.<br />
Die Primer RNA wird am Ende der <strong>Replikation</strong> durch 5´ 3´<br />
Exonucleaseaktivität der DANN Polymerease 1 entfernt.<br />
Rolle der <strong>DNA</strong> Polymerase 3 Holoenzym<br />
Charakterisiert durch :<br />
Sehr hohe Reaktionsfolge<br />
Großes Katalytisches Potential<br />
Hohe Genauigkeit<br />
Die <strong>DNA</strong> Polymerase 3 hat einige Untereinheiten die das Zentrum bilden:<br />
α-Untereinheit –katalytische Aktivität<br />
ε-Untereinheit- die Exonucleaseaktivität<br />
β-Untereinheit – schnelle Ablauf der Reaktionen.<br />
Im Überblick<br />
<strong>DNA</strong> Polymerase synthetisiert am <strong>Replikation</strong>sgabel der Leitstrang unter<br />
Verwendung des Primers,nachdem es durch eine Helicase entwunden wurde<br />
unter ATP Verbrauch.<br />
Die <strong>DNA</strong> Gyrase führt dann gleichzeitig negative Superhelices ein um eine<br />
topologische Krise zu verhüten.
Am Folgestrang:<br />
Die Matrize bildet eine Schleife.die Matrize des Folgestranges würde sich<br />
dann in der gleiche Richtung bewegen wie die Matrize des Leitstranges.<br />
Nachdem 1000 Nucleotiden gebildet sind,gibt <strong>DNA</strong> Polymerase 3 die Matrize<br />
ab.<br />
Neue Schleife und Matrize werden gebildet und ein weiteres Okazaki<br />
Fragment synthetisiert..<br />
Die Lücken werden dann mit <strong>DNA</strong> polymerase 1 gefüllt und ihre<br />
Exonucleaseaktivität entfernt die Primer.<br />
Die <strong>DNA</strong> Ligase verbindet schließlich die einzelne Stücke.