- Page 1: Contrôle de la stabilité des ARNm
- Page 4 and 5: I. Diversité fonctionnelle des ARN
- Page 6 and 7: L’ARN catalyse des réactions enz
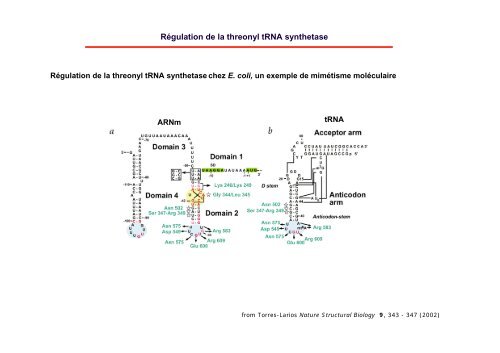
- Page 10 and 11: Régulation de la threonyl tRNA syn
- Page 12 and 13: Les ARNs régulant l’expression g
- Page 14 and 15: Le tmRNA
- Page 16 and 17: Les ARNs régulant l’expression g
- Page 18 and 19: Les ARNs régulant l’expression g
- Page 20 and 21: II. Dégradation des ARN chez les p
- Page 22 and 23: Les différents types de RNases imp
- Page 24 and 25: La RNase E La RNase E est sensible
- Page 26 and 27: La RNase E RraA et RraB interagisse
- Page 28 and 29: Les autres endoribonucléases... L
- Page 30 and 31: Les principales exoribonucléases U
- Page 32 and 33: Régulation de l’activité des RN
- Page 34 and 35: La dégradation des ARNm précoces
- Page 36 and 37: La dégradation des ARNm précoces
- Page 38 and 39: Régulation de la dégradation des
- Page 40 and 41: Exemple de l’ARN régulateur micA
- Page 42 and 43: La traduction inhibe la dégradatio
- Page 44 and 45: La dégradation des ARN chez E. col
- Page 46 and 47: Régulation de la dégradation de l
- Page 48 and 49: Conclusions
- Page 50 and 51: Dégradation des ARNm 3 activités
- Page 52 and 53: Tarun SZ Jr, Sachs AB, Genes Dev. 1
- Page 54 and 55: Mechanisms of deadenylationdependen
- Page 56 and 57: Voies “générales” de dégrada
- Page 58 and 59:
Dégradation des ARNm eucaryotes R
- Page 60 and 61:
Dégradation des ARNm eucaryotes In
- Page 62 and 63:
Voies “générales” de dégrada
- Page 64 and 65:
Dégradation des ARNm eucaryotes La
- Page 66 and 67:
Dégradation des ARNm eucaryotes L
- Page 68 and 69:
Parallèle entre la dégradation eu
- Page 70 and 71:
Localisation de la dégradation des
- Page 72 and 73:
Localisation de la dégradation des
- Page 74 and 75:
En résumé : La structure en close
- Page 76 and 77:
Ciblage de l’ARN vers les granule
- Page 78 and 79:
Voies “spécifiques” de dégrad
- Page 80 and 81:
Nonsense-mediated mRNA decay (NMD)
- Page 82 and 83:
leu2-2 Identification des facteurs
- Page 84 and 85:
UPF1 : 109 kDa, activité de liaiso
- Page 86 and 87:
La phosphorylation de hUPF1 D’aut
- Page 88 and 89:
Mise en évidence de la présence d
- Page 90 and 91:
La NMD chez l’Homme SURF complex
- Page 92 and 93:
La NMD chez l’Homme Chez l’homm
- Page 94 and 95:
http://www.med.hokudai.ac.jp/en/dep
- Page 96 and 97:
Les mutations affectant l’ubiquit
- Page 98 and 99:
Dégradation de la protéine corres
- Page 100 and 101:
Chen L. et al. Nature Structural &
- Page 102 and 103:
Dégradation des ARNm eucaryotes Da
- Page 104 and 105:
l’ARN interférence Mise en évid
- Page 106 and 107:
l’ARN interférence S14 Dicer : d
- Page 108 and 109:
l’ARN interférence Structure de
- Page 110 and 111:
Recrutement d’une enzyme spécifi
- Page 112 and 113:
Contrôle de la stabilité des ARNm
- Page 114 and 115:
Au cours de la phase S : AUG 4F SLI
- Page 116 and 117:
Contrôle de la stabilité des ARNm
- Page 118 and 119:
Contrôle de la stabilité des ARNm
- Page 120 and 121:
Très important dans les mécanisme
- Page 122 and 123:
TNFα miR16 Bail S and Kiledjian M
- Page 124 and 125:
Les miRNA Etude du développement d
- Page 126 and 127:
Diapositive 124 SK6 a, Northern blo
- Page 128 and 129:
Régulation de LIN-14 par le mi-RNA
- Page 130 and 131:
Les miRNA affectent aussi la stabil
- Page 132 and 133:
Dégradation des ARNm cibles des mi
- Page 134 and 135:
mi-RNA chez les plantes Huntzinger
- Page 136 and 137:
Les miRNA Mise en évidence simulta
- Page 138 and 139:
Contrôle de la stabilité d’ARNm
- Page 140 and 141:
Conclusions 138
- Page 142 and 143:
Contrôle de la stabilité des ARNm
- Page 144 and 145:
From D. Gautheret 142
- Page 146:
144