Stärkespaltung Amylase - Adam Vollmer
Stärkespaltung Amylase - Adam Vollmer
Stärkespaltung Amylase - Adam Vollmer
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
Hinweise und Lösungen für den Lehrer<br />
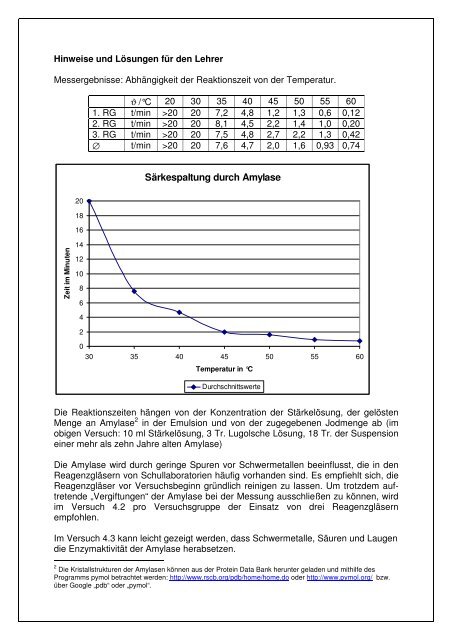
Messergebnisse: Abhängigkeit der Reaktionszeit von der Temperatur.<br />
Zeit im Minuten<br />
20<br />
18<br />
16<br />
14<br />
12<br />
10<br />
8<br />
6<br />
4<br />
2<br />
ϑ /°C 20 30 35 40 45 50 55 60<br />
1. RG t/min >20 20 7,2 4,8 1,2 1,3 0,6 0,12<br />
2. RG t/min >20 20 8,1 4,5 2,2 1,4 1,0 0,20<br />
3. RG t/min >20 20 7,5 4,8 2,7 2,2 1,3 0,42<br />
∅ t/min >20 20 7,6 4,7 2,0 1,6 0,93 0,74<br />
Särkespaltung durch <strong>Amylase</strong><br />
0<br />
30 35 40 45 50 55 60<br />
Temperatur in °C<br />
Durchschnittswerte<br />
Die Reaktionszeiten hängen von der Konzentration der Stärkelösung, der gelösten<br />
Menge an <strong>Amylase</strong> 2 in der Emulsion und von der zugegebenen Jodmenge ab (im<br />
obigen Versuch: 10 ml Stärkelösung, 3 Tr. Lugolsche Lösung, 18 Tr. der Suspension<br />
einer mehr als zehn Jahre alten <strong>Amylase</strong>)<br />
Die <strong>Amylase</strong> wird durch geringe Spuren vor Schwermetallen beeinflusst, die in den<br />
Reagenzgläsern von Schullaboratorien häufig vorhanden sind. Es empfiehlt sich, die<br />
Reagenzgläser vor Versuchsbeginn gründlich reinigen zu lassen. Um trotzdem auftretende<br />
„Vergiftungen“ der <strong>Amylase</strong> bei der Messung ausschließen zu können, wird<br />
im Versuch 4.2 pro Versuchsgruppe der Einsatz von drei Reagenzgläsern<br />
empfohlen.<br />
Im Versuch 4.3 kann leicht gezeigt werden, dass Schwermetalle, Säuren und Laugen<br />
die Enzymaktivität der <strong>Amylase</strong> herabsetzen.<br />
2 Die Kristallstrukturen der <strong>Amylase</strong>n können aus der Protein Data Bank herunter geladen und mithilfe des<br />
Programms pymol betrachtet werden: http://www.rscb.org/pdb/home/home.do oder http://www.pymol.org/ bzw.<br />
über Google „pdb“ oder „pymol“.