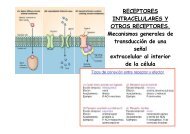
Historia y desarrollo del concepto de cuasiespecies ... - Severo Ochoa
Historia y desarrollo del concepto de cuasiespecies ... - Severo Ochoa
Historia y desarrollo del concepto de cuasiespecies ... - Severo Ochoa
You also want an ePaper? Increase the reach of your titles
YUMPU automatically turns print PDFs into web optimized ePapers that Google loves.
comportamiento colectivo. Hay numerosos<br />
experimentos (<strong>de</strong>masiados para<br />
ser explicados aquí) que justifican que<br />
el comportamiento <strong>de</strong> un espectro <strong>de</strong><br />
mutantes no se pue<strong>de</strong> explicar a partir<br />
<strong><strong>de</strong>l</strong> comportamiento <strong>de</strong> los individuos<br />
que lo componen. Ello no es baladí, ya<br />
que implica que las formulaciones <strong>de</strong> la<br />
genética poblacional clásica (los mo<strong><strong>de</strong>l</strong>os<br />
<strong>de</strong> equilibrio <strong>de</strong> mutación-selección,<br />
a veces <strong>de</strong>nominados mo<strong><strong>de</strong>l</strong>os <strong>de</strong><br />
Wright-Fisher) pue<strong>de</strong>n no ser a<strong>de</strong>cuados<br />
para explicar el comportamiento<br />
<strong>de</strong> los virus ARN.<br />
SITUACIÓN ACTUAL<br />
Recientemente, el <strong>concepto</strong> <strong>de</strong> <strong>cuasiespecies</strong> se ha ido<br />
extendiendo a sistemas biológicos distintos <strong>de</strong> los virus,<br />
como son las bacterias, las células tumorales y los priones<br />
[3] . Aunque las implicaciones biológicas <strong>de</strong> la dinámica<br />
<strong>de</strong> <strong>cuasiespecies</strong>, tanto en sistemas virales como en<br />
no virales, estén lejos <strong>de</strong> ser comprendidas en su totalidad,<br />
llegando al año 2012 (es <strong>de</strong>cir, 41 años <strong>de</strong>spués <strong><strong>de</strong>l</strong><br />
primer trabajo teórico <strong>de</strong> Eigen, y 34 años <strong>de</strong>spués <strong>de</strong> la<br />
primera evi<strong>de</strong>ncia experimental con el bacteriófago Qβ),<br />
po<strong>de</strong>mos expresar algunas conclusiones generales que, en<br />
el caso <strong>de</strong> los virus, son ampliamente aceptadas:<br />
(i) Los virus ARN y los virus ADN más sencillos, cuya<br />
replicación se cataliza por enzimas carentes <strong>de</strong> una actividad<br />
correctora <strong>de</strong> pruebas, están formados por espectros<br />
(también <strong>de</strong>nominados distribuciones, nubes<br />
o enjambres) <strong>de</strong> mutantes complejos y dinámicos. La<br />
presencia <strong>de</strong> multitud <strong>de</strong> mutantes en cada momento<br />
no es un artefacto <strong>de</strong>bido a errores <strong>de</strong> copia durante la<br />
amplificación <strong>de</strong> los ácidos nucleicos víricos previa a<br />
su secuenciación. Las mutaciones tampoco son el resultado<br />
<strong>de</strong> un ina<strong>de</strong>cuado procesamiento <strong>de</strong> los datos<br />
<strong>de</strong> secuenciación. A pesar <strong>de</strong> que cada uno <strong>de</strong> los métodos<br />
empleados para penetrar en la composición <strong>de</strong><br />
los espectros <strong>de</strong> mutantes víricos (amplificación por<br />
PCR con transcriptasa reversa, clonaje molecular y<br />
secuenciación <strong>de</strong> clones, o aplicación <strong>de</strong> las técnicas<br />
<strong>de</strong> secuenciación masiva) requiere controles y correcciones<br />
<strong>de</strong> los valores <strong>de</strong> heterogeneidad obtenidos, los<br />
errores <strong>de</strong> secuenciación no son la causa <strong>de</strong> la heterogeneidad<br />
observada. Las distribuciones <strong>de</strong> mutantes<br />
son reales y existen en las poblaciones naturales <strong>de</strong><br />
virus, hasta ahora sin excepciones. Los distintos métodos<br />
para secuenciar componentes individuales <strong>de</strong><br />
los espectros <strong>de</strong> mutantes son métodos <strong>de</strong> muestreo,<br />
ya que se utiliza un número limitado <strong>de</strong> secuencias<br />
para obtener una representación <strong>de</strong> una realidad<br />
mucho más numerosa. No obstante, con cualquiera<br />
Virología | Volumen 16 - Número 1/2013<br />
Artículo original: <strong>concepto</strong> <strong>de</strong> <strong>cuasiespecies</strong> en Virología<br />
Recientemente,<br />
el<br />
<strong>concepto</strong> <strong>de</strong> <strong>cuasiespecies</strong><br />
se ha ido extendiendo a<br />
sistemas biológicos<br />
distintos <strong>de</strong> los virus,<br />
como son las bacterias,<br />
las células tumorales y<br />
los priones<br />
11 <br />
<strong>de</strong> los métodos empleados, la conclusión<br />
es inevitable: las poblaciones<br />
<strong>de</strong> virus son extraordinariamente<br />
complejas, tal como se refleja en la<br />
figura 6.<br />
(ii) La gran mayoría <strong>de</strong> las alteraciones<br />
biológicamente relevantes<br />
observadas in vivo son el resultado<br />
<strong>de</strong> variaciones en la composición<br />
<strong>de</strong> los espectros <strong>de</strong> mutantes sometidos<br />
a selección positiva y negativa,<br />
así como <strong>de</strong> acontecimientos<br />
aleatorios como son los cuellos <strong>de</strong> botella poblacionales.<br />
Todos estos eventos actúan sobre multitud <strong>de</strong><br />
unida<strong>de</strong>s replicativas con distintos grados <strong>de</strong> interconexión<br />
entre ellas.<br />
(iii) Un espectro <strong>de</strong> mutantes no es un agregado neutro<br />
<strong>de</strong> genomas distintos. La composición, complejidad<br />
y amplitud <strong>de</strong> un espectro <strong>de</strong> mutantes <strong>de</strong> un virus<br />
pue<strong>de</strong> ejercer una influencia en el comportamiento<br />
<strong><strong>de</strong>l</strong> mismo. Esta influencia incluye rasgos muy relevantes<br />
<strong>de</strong>s<strong>de</strong> el punto <strong>de</strong> vista médico, como pue<strong>de</strong>n<br />
ser la capacidad <strong>de</strong> un virus para progresar hacia una<br />
infección aguda grave, para establecer una infección<br />
crónica e incluso inducir la respuesta <strong><strong>de</strong>l</strong> virus a un<br />
tratamiento. No es casual que el <strong>concepto</strong> <strong>de</strong> <strong>cuasiespecies</strong><br />
haya pasado a ser habitual en el lenguaje<br />
<strong>de</strong> la Virología clínica.<br />
(iv) La adaptación <strong>de</strong> un virus a un nuevo ambiente se<br />
produce fundamentalmente como resultado <strong>de</strong> cambios<br />
en la frecuencia relativa <strong>de</strong> las múltiples subpoblaciones<br />
que componen una población viral. Cuando<br />
la adaptación requiere una o unas pocas mutaciones<br />
que no acarrean un coste significativo <strong>de</strong> fitness, la<br />
adaptación será muy probable y podrá producirse incluso<br />
en virus con una tasa <strong>de</strong> error normal o algo inferior<br />
a la normal. La selección <strong>de</strong> mutantes resistentes<br />
a anticuerpos monoclonales neutralizantes constituye<br />
un ejemplo típico y amplísimamente documentado en<br />
la literatura. Por el contrario, cuando la adaptación<br />
requiere múltiples y bien <strong>de</strong>finidas mutaciones, es improbable<br />
que la presencia <strong>de</strong> un espectro <strong>de</strong> mutantes<br />
permita la adaptación, por consi<strong>de</strong>raciones meramente<br />
estadísticas. Esta es la razón por la que los virus<br />
mantienen generalmente su i<strong>de</strong>ntidad como agentes<br />
infecciosos. Es muy improbable convertir al FMDV<br />
en el virus <strong>de</strong> la poliomielitis humana, <strong>de</strong>bido a que<br />
los cambios genéticos necesarios son inaccesibles a los<br />
mecanismos evolutivos habituales. Gracias a ello po<strong>de</strong>mos<br />
clasificar los virus y agra<strong>de</strong>cer su esfuerzo a<br />
nuestros colegas miembros <strong>de</strong> la Comisión Internacional<br />
para la Taxonomía <strong>de</strong> Virus.