Download - Station Biologique de Roscoff - Portail des applications
Download - Station Biologique de Roscoff - Portail des applications
Download - Station Biologique de Roscoff - Portail des applications
You also want an ePaper? Increase the reach of your titles
YUMPU automatically turns print PDFs into web optimized ePapers that Google loves.
Sophie ARNAUD-HAOND - Candidature à une Habilitation à Diriger <strong>de</strong>s Recherches, Février 2008<br />
3. Résumé <strong>de</strong>s travaux <strong>de</strong> Recherche<br />
II.2<br />
Within-population spatial genetic structure, neighbourhood size and<br />
clonal subrange in the seagrass Cymodocea nodosa. Molecular Ecology,<br />
2005.<br />
Dans le cadre <strong>de</strong> la thèse <strong>de</strong> Filipe Alberto, l'étu<strong>de</strong> <strong>de</strong> la dispersion clonale<br />
versus sexuée chez Cymodocea nodosa a été réalisée dans <strong>de</strong>s herbiers présentant<br />
<strong>de</strong>s niveaux <strong>de</strong> perturbation contrastés. Nous avons développé et appliqué le<br />
principe <strong>de</strong> clonal subrange (qui corresponds à l’éventail <strong>de</strong>s distances minimales<br />
d’extension clonale) afin d’estimer les distances <strong>de</strong> dispersion par voie clonale<br />
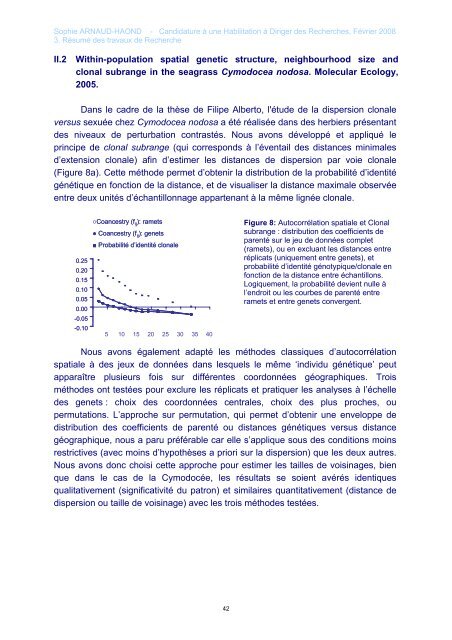
(Figure 8a). Cette métho<strong>de</strong> permet d’obtenir la distribution <strong>de</strong> la probabilité d’i<strong>de</strong>ntité<br />
génétique en fonction <strong>de</strong> la distance, et <strong>de</strong> visualiser la distance maximale observée<br />
entre <strong>de</strong>ux unités d’échantillonnage appartenant à la même lignée clonale.<br />
0.25<br />
0.20<br />
0.15<br />
0.10<br />
0.05<br />
0.00<br />
-0.05<br />
-0.10<br />
○Coancestry (f ij ): ramets<br />
● Coancestry (f ij ): genets<br />
■ Probabilité d’i<strong>de</strong>ntité clonale<br />
5 10 15 20 25 30 35 40<br />
Figure 8: Autocorrélation spatiale et Clonal<br />
subrange : distribution <strong>de</strong>s coefficients <strong>de</strong><br />
parenté sur le jeu <strong>de</strong> données complet<br />
(ramets), ou en excluant les distances entre<br />
réplicats (uniquement entre genets), et<br />
probabilité d’i<strong>de</strong>ntité génotypique/clonale en<br />
fonction <strong>de</strong> la distance entre échantillons.<br />
Logiquement, la probabilité <strong>de</strong>vient nulle à<br />
l’endroit ou les courbes <strong>de</strong> parenté entre<br />
ramets et entre genets convergent.<br />
Nous avons également adapté les métho<strong>de</strong>s classiques d’autocorrélation<br />
spatiale à <strong>de</strong>s jeux <strong>de</strong> données dans lesquels le même ‘individu génétique’ peut<br />
apparaître plusieurs fois sur différentes coordonnées géographiques. Trois<br />
métho<strong>de</strong>s ont testées pour exclure les réplicats et pratiquer les analyses à l’échelle<br />
<strong>de</strong>s genets : choix <strong>de</strong>s coordonnées centrales, choix <strong>de</strong>s plus proches, ou<br />
permutations. L’approche sur permutation, qui permet d’obtenir une enveloppe <strong>de</strong><br />
distribution <strong>de</strong>s coefficients <strong>de</strong> parenté ou distances génétiques versus distance<br />
géographique, nous a paru préférable car elle s’applique sous <strong>de</strong>s conditions moins<br />
restrictives (avec moins d’hypothèses a priori sur la dispersion) que les <strong>de</strong>ux autres.<br />
Nous avons donc choisi cette approche pour estimer les tailles <strong>de</strong> voisinages, bien<br />
que dans le cas <strong>de</strong> la Cymodocée, les résultats se soient avérés i<strong>de</strong>ntiques<br />
qualitativement (significativité du patron) et similaires quantitativement (distance <strong>de</strong><br />
dispersion ou taille <strong>de</strong> voisinage) avec les trois métho<strong>de</strong>s testées.<br />
42