- Page 5 and 6:
Gen: unidad de herencia que setrasm
- Page 7 and 8:
Gregor MendelX !X !Púrpura!Blanco!
- Page 9 and 10:
Grupo de alelos ligados: haplotipo
- Page 11 and 12:
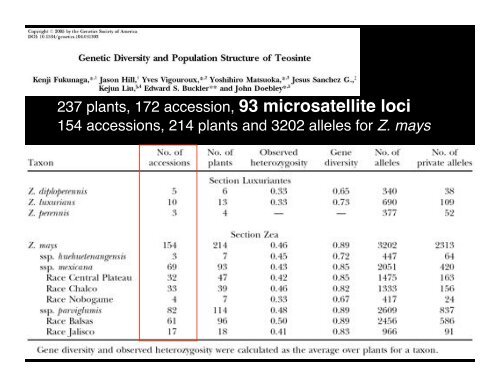
Genetic material at the molecular l
- Page 13 and 14:
Mobile elements!(transposable eleme
- Page 15 and 16:
Duplications in the 5 chromosomes o
- Page 17 and 18:
Three genomes in A. thalianaDiffere
- Page 19 and 20:
But to understand theideas and conc
- Page 21 and 22:
VARIACIÓN GENÉTICA:1) EL PRIMER P
- Page 23 and 24:
POBLACION IDEAL!modelo, poblaciones
- Page 25 and 26:
N individuals!Frequencies de A= p 0
- Page 27 and 28:
Números Frecuencias F. alélicasge
- Page 29 and 30:
Equilibrio de Hardy-Weinberg!1 = p
- Page 31 and 32:
A 1 A 1 =p 2 !A 1 A 2 =2pq!A 2 A 2
- Page 33 and 34:
Th. Dobzhansky de sus!experimentos
- Page 35 and 36:
Lo contrasta con el !“modelo clá
- Page 37 and 38:
Los resultados del programa de inve
- Page 39 and 40:
Datos antes de Lewontin!Variación
- Page 41 and 42:
Evidencia etnobotánicay botánica
- Page 43 and 44:
Bases genética sencilla, variació
- Page 45 and 46:
Análisis genéticos: !Variación C
- Page 47 and 48:
Volume10 × 10 8d40Citogenéticos:
- Page 49 and 50:
El genoma en la familia Cucurbitace
- Page 51 and 52:
Gong y Lelley (2008) reportan el ma
- Page 53 and 54:
Así podemos ver los genes recesivo
- Page 55 and 56: Si el 2o. cromosoma es el 40% del g
- Page 57 and 58: letales, 37%!letales, 55%!Variació
- Page 59 and 60: h 2 heredabilidad sentido restringi
- Page 61 and 62: Ajolote vs salamandra (A. mexicanum
- Page 64: H esperada en !HW!0 a 1...!
- Page 69 and 70: La variación en poblaciones!natura
- Page 71: Medidas de variación genética.!Da
- Page 74 and 75: UPGMAAgavelechuguillaD= -ln(I)!I= J
- Page 76: More than 2,200 studies have report
- Page 80 and 81: Marcadoresderivados del PCR:!AFLPs,
- Page 82 and 83: Agave striata ssp. striata!6 popula
- Page 84 and 85: Genetic variation (47 loci, 12 popu
- Page 86 and 87: More geneticvariation in theNorth!m
- Page 88 and 89: Dos especies mezcaleras muycercanas
- Page 90 and 91: Mapa
- Page 92 and 93: Variación Genética en Agave, espe
- Page 94 and 95: Structure: Análsis Bayesiano para
- Page 96 and 97: Dendograma UPGMA basando en las dis
- Page 98 and 99: VARIACIÓN GENÉTICA EN AGAVE"He, h
- Page 100 and 101: HILDE NYBOM!Comparison of different
- Page 102 and 103: Ferriol et al. ( 2004) C.moschata,
- Page 104 and 105: of populations, number of plants pe
- Page 108 and 109: More genetic variation in total in
- Page 110: Boostrap values suggest!that mexica
- Page 113 and 114: ... but not so well supported...!
- Page 115 and 116: A. parryi Cultivated IA. angustifol
- Page 117 and 118: Expected Heterozygosity H s!0.45!0.
- Page 119 and 120: Cloroplasto y mitocondria:!Uniparen
- Page 121 and 122: Filogenia deCucurbita:!Sanjur et al
- Page 123 and 124: mexicana Central Plateau ancestral?
- Page 125 and 126: Phylogeography and breeding system
- Page 127: PROTEOMAS!METAGENOMAS !!!!!
- Page 132 and 133: pi= 0.006!pi S= 0.0056!pi F= 0.0029
- Page 135: Indirect estimates of NaturalSelect
- Page 139: Tajima´s D (1983) has some problem
- Page 143: pi en !diferentes!organismos!
- Page 146 and 147: pi highest values in red!pi lower v
- Page 149 and 150: SNPs de muchos genes!(single nucleo
- Page 151: SNP!20cromosomas!cromo. 21!
- Page 154 and 155: Molecular Ecology (2010) 19, 1162-1
- Page 156 and 157:
Genetic signals of origin, spread,
- Page 158 and 159:
ture analysis (21) of all Mexican a
- Page 160 and 161:
ping against remainingallele eight
- Page 162:
21 millones !de snps!
- Page 169 and 170:
Algunos patrones generales!de varia
- Page 171 and 172:
Ciclos de 3 años, cada generación
- Page 173 and 174:
Los humanos tenemos baja!variación
- Page 176 and 177:
Lasespecies!con pocao nula!variaci
- Page 178:
Hobs.!Sitios con mucha variación:
- Page 181 and 182:
Secuencias ADN: mismatches, compara
- Page 183 and 184:
Deriva Génica (Foose 1986).!La var
- Page 185 and 186:
A mayor N se mantiene más var. gé
- Page 187:
Para Concluir:!Las poblaciones natu