resolver
resolver
resolver
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
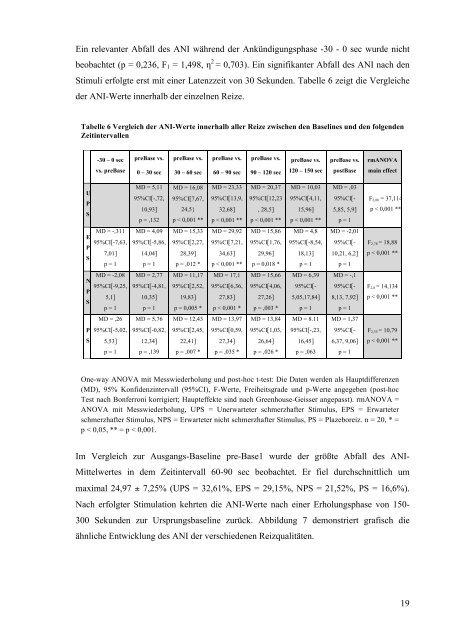
Ein relevanter Abfall des ANI während der Ankündigungsphase -30 - 0 sec wurde nicht<br />
beobachtet (p = 0,236, F 1 = 1,498, η 2 = 0,703). Ein signifikanter Abfall des ANI nach den<br />
Stimuli erfolgte erst mit einer Latenzzeit von 30 Sekunden. Tabelle 6 zeigt die Vergleiche<br />
der ANI-Werte innerhalb der einzelnen Reize.<br />
Tabelle 6 Vergleich der ANI-Werte innerhalb aller Reize zwischen den Baselines und den folgenden<br />
Zeitintervallen<br />
-30 – 0 sec<br />
preBase vs.<br />
preBase vs.<br />
preBase vs.<br />
preBase vs.<br />
preBase vs.<br />
preBase vs.<br />
rmANOVA<br />
vs. preBase<br />
0 – 30 sec<br />
30 – 60 sec<br />
60 – 90 sec<br />
90 – 120 sec<br />
120 – 150 sec<br />
postBase<br />
main effect<br />
U<br />
P<br />
S<br />
MD = 5,11<br />
95%CI[-,72,<br />
10,93]<br />
p = ,132<br />
MD = 16,08<br />
95%CI[7,67,<br />
24,5}<br />
p < 0,001 **<br />
MD = 23,33<br />
95%CI[13,9,<br />
32,68]<br />
p < 0,001 **<br />
MD = 20,37<br />
95%CI[12,23<br />
, 28,5]<br />
p < 0,001 **<br />
MD = 10,03<br />
95%CI[4,11,<br />
15,96]<br />
p < 0,001 **<br />
MD = ,03<br />
95%CI[-<br />
5,85, 5,9]<br />
p = 1<br />
F 2,86 = 37,114<br />
p < 0,001 **<br />
E<br />
P<br />
S<br />
MD = -,311<br />
95%CI[-7,63,<br />
7,01]<br />
p = 1<br />
MD = 4,09<br />
95%CI[-5,86,<br />
14,04]<br />
p = 1<br />
MD = 15,33<br />
95%CI[2,27,<br />
28,39]<br />
p = ,012 *<br />
MD = 29,92<br />
95%CI[7,21,<br />
34,63]<br />
p < 0,001 **<br />
MD = 15,86<br />
95%CI[1,76,<br />
29,96]<br />
p = 0,018 *<br />
MD = 4,8<br />
95%CI[-8,54,<br />
18,13]<br />
p = 1<br />
MD = -2,01<br />
95%CI[-<br />
10,21, 6,2]<br />
p = 1<br />
F 2,78 = 18,88<br />
p < 0,001 **<br />
N<br />
P<br />
S<br />
MD = -2,08<br />
95%CI[-9,25,<br />
5,1]<br />
p = 1<br />
MD = 2,77<br />
95%CI[-4,81,<br />
10,35]<br />
p = 1<br />
MD = 11,17<br />
95%CI[2,52,<br />
19,83]<br />
p = 0,005 *<br />
MD = 17,1<br />
95%CI[6,36,<br />
27,83]<br />
p < 0,001 *<br />
MD = 15,66<br />
95%CI[4,06,<br />
27,26]<br />
p = ,003 *<br />
MD = 6,39<br />
95%CI[-<br />
5,05,17,84]<br />
p = 1<br />
MD = -,1<br />
95%CI[-<br />
8,13, 7,92]<br />
p = 1<br />
F 2,8 = 14,134<br />
p < 0,001 **<br />
MD = ,26<br />
MD = 5,76<br />
MD = 12,43<br />
MD = 13,97<br />
MD = 13,84<br />
MD = 8.11<br />
MD = 1,37<br />
P<br />
95%CI[-5,02,<br />
95%CI[-0,82,<br />
95%CI[2,45,<br />
95%CI[0,59,<br />
95%CI[1,03,<br />
95%CI[-,23,<br />
95%CI[-<br />
F 2,33 = 10,79<br />
S<br />
5,53]<br />
12,34]<br />
22,41]<br />
27,34]<br />
26,64]<br />
16,45]<br />
6,37, 9,06]<br />
p < 0,001 **<br />
p = 1<br />
p = ,139<br />
p = ,007 *<br />
p = ,035 *<br />
p = ,026 *<br />
p = ,063<br />
p = 1<br />
One-way ANOVA mit Messwiederholung und post-hoc t-test: Die Daten werden als Hauptdifferenzen<br />
(MD), 95% Konfidenzintervall (95%CI), F-Werte, Freiheitsgrade und p-Werte angegeben (post-hoc<br />
Test nach Bonferroni korrigiert; Haupteffekte sind nach Greenhouse-Geisser angepasst). rmANOVA =<br />
ANOVA mit Messwiederholung, UPS = Unerwarteter schmerzhafter Stimulus, EPS = Erwarteter<br />
schmerzhafter Stimulus, NPS = Erwarteter nicht schmerzhafter Stimulus, PS = Plazeboreiz. n = 20, * =<br />
p < 0,05, ** = p < 0,001.<br />
Im Vergleich zur Ausgangs-Baseline pre-Base1 wurde der größte Abfall des ANI-<br />
Mittelwertes in dem Zeitintervall 60-90 sec beobachtet. Er fiel durchschnittlich um<br />
maximal 24,97 ± 7,25% (UPS = 32,61%, EPS = 29,15%, NPS = 21,52%, PS = 16,6%).<br />
Nach erfolgter Stimulation kehrten die ANI-Werte nach einer Erholungsphase von 150-<br />
300 Sekunden zur Ursprungsbaseline zurück. Abbildung 7 demonstriert grafisch die<br />
ähnliche Entwicklung des ANI der verschiedenen Reizqualitäten.<br />
19