I ité I é Immunité Innée
I ité I é Immunité Innée
I ité I é Immunité Innée
You also want an ePaper? Increase the reach of your titles
YUMPU automatically turns print PDFs into web optimized ePapers that Google loves.
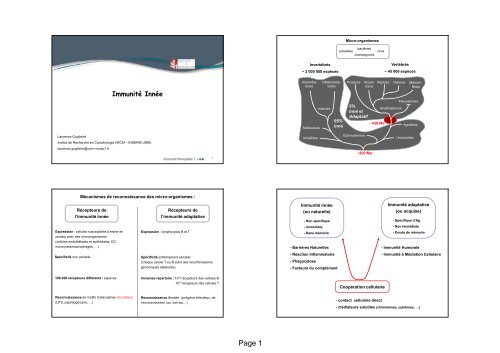
Micro-organismes<br />
bact<strong>é</strong>ries<br />
parasites<br />
champignons<br />
virus<br />
Invert<strong>é</strong>br<strong>é</strong>s<br />
~ 2 000 000 espèces<br />
Vert<strong>é</strong>br<strong>é</strong>s<br />
~ 45 000 espèces<br />
Immun<strong>it<strong>é</strong></strong> Inn<strong>é</strong>e<br />
H<strong>é</strong>t<strong>é</strong>rom<strong>é</strong>taboles<br />
Holom<strong>é</strong>taboles<br />
Mollusques<br />
Reptiles Oiseaux Mammifères<br />
Insectes<br />
95%<br />
Inn<strong>é</strong><br />
Poissons<br />
5%<br />
Inn<strong>é</strong> et<br />
Adaptatif<br />
Amphibiens<br />
- 450 Ma<br />
Placodermes<br />
Gnathostomes<br />
Agnathes<br />
Laurence Guglielmi<br />
Institut de Recherche en Canc<strong>é</strong>rologie (IRCM – INSERM U896)<br />
Ann<strong>é</strong>lides<br />
Echinodermes<br />
Urochord<strong>é</strong>s<br />
laurence.guglielmi@univ-montp1.fr<br />
1<br />
- 800 Ma<br />
M<strong>é</strong>canismes de reconnaissance des micro-organismes :<br />
R<strong>é</strong>cepteurs de<br />
R<strong>é</strong>cepteurs de<br />
l’immun<strong>it<strong>é</strong></strong> inn<strong>é</strong>e<br />
l’immun<strong>it<strong>é</strong></strong> adaptative<br />
Expression : cellules susceptibles d’entrer en<br />
Expression : lymphocytes B et T<br />
contact avec des microorganismes<br />
(cellules endoth<strong>é</strong>liales et <strong>é</strong>pith<strong>é</strong>liales, DC,<br />
monocytes/macrophages, …)<br />
Sp<strong>é</strong>cific<strong>it<strong>é</strong></strong> non variable<br />
Sp<strong>é</strong>cific<strong>it<strong>é</strong></strong> extrêmement variable<br />
(chaque cellule T ou B subit des recombinaisons<br />
g<strong>é</strong>nomiques al<strong>é</strong>atoires)<br />
Immun<strong>it<strong>é</strong></strong> inn<strong>é</strong>e<br />
(ou naturelle)<br />
- Non sp<strong>é</strong>cifique<br />
- Imm<strong>é</strong>diate<br />
- Sans m<strong>é</strong>moire<br />
- Barrières Naturelles<br />
- R<strong>é</strong>action Inflammatoire<br />
- Phagocytose<br />
- Facteurs du compl<strong>é</strong>ment<br />
Immun<strong>it<strong>é</strong></strong> adaptative<br />
(ou acquise)<br />
- Sp<strong>é</strong>cifique d’Ag<br />
- Non Imm<strong>é</strong>diate<br />
- Dou<strong>é</strong>e de m<strong>é</strong>moire<br />
- Immun<strong>it<strong>é</strong></strong> Humorale<br />
- Immun<strong>it<strong>é</strong></strong> à M<strong>é</strong>diation Cellulaire<br />
100-200 r<strong>é</strong>cepteurs diff<strong>é</strong>rents / espèces<br />
Immense r<strong>é</strong>pertoire : 10 12 r<strong>é</strong>cepteurs des cellules B<br />
10 15 r<strong>é</strong>cepteurs des cellules T<br />
Coop<strong>é</strong>ration cellulaire<br />
Reconnaissance de motifs mol<strong>é</strong>culaires microbiens<br />
(LPS, peptidoglycane, …)<br />
Reconnaissance illim<strong>it<strong>é</strong></strong>e (antigène infectieux, de<br />
l’environnement, soi, non soi…)<br />
- contact cellulaire direct<br />
- m<strong>é</strong>diateurs solubles (chimiokines, cytokines, …)<br />
Page 1
BARRIERES<br />
Barrières naturelles<br />
Flore intestinale<br />
Notion de danger et reconnaissance<br />
R<strong>é</strong>action inflammatoire<br />
Les lymphocytes de la r<strong>é</strong>ponse inn<strong>é</strong>e<br />
Barrières physiques :<br />
• peau (≈ 1,7 m 2 )<br />
• muqueuses (≈ 390 m 2 ) (respiratoire, digestive, uro-g<strong>é</strong>nitale)<br />
Barrières biologiques / biochimiques :<br />
• pH : acid<strong>it<strong>é</strong></strong> locale (estomac, urine, vagin)<br />
• acides gras toxiques (peau)<br />
• peptides antimicrobiens<br />
• enzymes : lysozymes (salive, sueur, larmes)<br />
pepsine (intestin)<br />
Barrière <strong>é</strong>cologique :<br />
• flore bact<strong>é</strong>rienne<br />
Symbiose hôte-microbes<br />
Barrières naturelles<br />
Flore intestinale<br />
Notion de danger et reconnaissance<br />
R<strong>é</strong>action inflammatoire<br />
Les lymphocytes de la r<strong>é</strong>ponse inn<strong>é</strong>e<br />
~ 10 12 cellules<br />
~3.10 4 gènes<br />
~ 10 14 germes<br />
~3.10 6 gènes<br />
~ 1000 espèces bact<strong>é</strong>riennes<br />
Colonisation dès la naissance<br />
Évolution parallèle chez les mammifères depuis des millions d’ann<strong>é</strong>es<br />
Page 2
Microbiote = Flore bact<strong>é</strong>rienne<br />
Hom<strong>é</strong>ostasie intestinale<br />
Rôles :<br />
Bact<strong>é</strong>ries<br />
Commensales<br />
Pathogènes<br />
Limitation du contact direct entre bact<strong>é</strong>rie et <strong>é</strong>pith<strong>é</strong>lium :<br />
• M<strong>é</strong>tabolisme :<br />
destin<strong>é</strong>e à augmenter la digestion en<br />
d<strong>é</strong>gradant les polysaccharides, à produire<br />
des vitamines et des acides gras à chaîne l<strong>é</strong>gère<br />
Microbiote = flore intestinale<br />
Bact<strong>é</strong>ries commensales (≈ 10 14 )<br />
Mucus<br />
+ IgA s<strong>é</strong>cr<strong>é</strong>toires (IgAs)<br />
+ peptides anti-microbiens<br />
• Protection contre les bact<strong>é</strong>ries pathogènes<br />
- comp<strong>é</strong>tition avec les pathogènes (nutriments, captation du fer)<br />
- blocage d'accès pour l'<strong>é</strong>pith<strong>é</strong>lium<br />
- production de substances antibiotiques (colicine)<br />
Cellules <strong>é</strong>pith<strong>é</strong>liales<br />
• D<strong>é</strong>veloppement du système immunitaire<br />
D<strong>é</strong>fensines = peptides antimicrobiens<br />
Sites de production des plasmocytes IgA :<br />
• peptides de 2-6 kDa,<br />
• produites par neutrophiles, les<br />
cellules <strong>é</strong>pith<strong>é</strong>liales, certains<br />
macrophages, les cellules NK, les<br />
cellules de Paneth,<br />
• microbicide,<br />
• recrutement des neutrophiles,<br />
GALT<br />
- Ganglions lymphatiques m<strong>é</strong>sent<strong>é</strong>riques<br />
- Plaques de Peyer<br />
- Follicules lymphoïdes isol<strong>é</strong>s<br />
- Lamina propria<br />
• activ<strong>it<strong>é</strong></strong> chimiotactique,<br />
• stimulation de la phagocytose<br />
Structure dim<strong>é</strong>rique<br />
des -d<strong>é</strong>fensines humaines<br />
adapt<strong>é</strong> de Izcue A, et al.<br />
Annu. Rev. Immunol 2009. 27:313<br />
Page 3
TRANSCYTOSE via les ent<strong>é</strong>rocytes<br />
Lumière intestinale<br />
r<strong>é</strong>cepteur<br />
d’Ig<br />
polym<strong>é</strong>riques<br />
dimère IgA<br />
dimère IgA<br />
+ pièce s<strong>é</strong>cr<strong>é</strong>toire<br />
Barrières naturelles<br />
Flore intestinale<br />
Notion de danger et reconnaissance<br />
R<strong>é</strong>action inflammatoire<br />
Les lymphocytes de la r<strong>é</strong>ponse inn<strong>é</strong>e<br />
Lamina propria<br />
Plasmocytes<br />
Notion de DANGER<br />
Notion de DANGER<br />
Comment distinguer le soi et le non-soi (les microbes) ?<br />
R<strong>é</strong>cepteur Toll chez la drosophile :<br />
- intervient dans le d<strong>é</strong>veloppement dorso-ventral,<br />
- intervient dans la d<strong>é</strong>fense anti-infectieuse.<br />
Prix Nobel 2011 : Jules Hoffmann (Strasbourg), Bruce Beutler<br />
(La Jolla), Ralph Steinman (NY)<br />
1997 : Charles Janeway et al. d<strong>é</strong>couvrent l’<strong>é</strong>quivalent chez l’homme :<br />
les Toll-like-receptors (TLR).<br />
Microorganismes<br />
PAMPs<br />
Pathogen-Associated<br />
Molecular Patterns<br />
MAMPs<br />
Microbe-Associated<br />
Molecular Patterns<br />
R<strong>é</strong>cepteurs<br />
PRR<br />
Pattern-Recognition<br />
Receptor<br />
Page 4
DC-SIGN<br />
NKG2D<br />
Dectin-2<br />
Pathogen‐Associated Molecular Patterns (PAMPs)<br />
Pattern Recognition Receptor (PRR)<br />
Caract<strong>é</strong>ristiques :<br />
• Produits uniquement par les micro‐organismes,<br />
• Motifs structuraux très conserv<strong>é</strong>s entre micro‐organismes d'une classe donn<strong>é</strong>e,<br />
(motifs r<strong>é</strong>pandus, invariants et communs à de nombreux micro‐organismes)<br />
MILIEU<br />
EXTRA-<br />
CELLULAIRE<br />
PGN (Gram+)<br />
Zymosan (levure)<br />
LPS "atypique"<br />
…<br />
Lipoprot<strong>é</strong>ines<br />
… Lipoprot<strong>é</strong>ines<br />
…<br />
LPS<br />
HSP60<br />
…<br />
Flagelline<br />
levure<br />
bact<strong>é</strong>rie<br />
• Rôle essentiel dans la physiologie et la survie des micro‐organismes<br />
TLR2<br />
TLR2<br />
TLR6<br />
TLR2<br />
TLR1<br />
TLR4<br />
TLR5<br />
(mutations importantes improbables peu de possibil<strong>it<strong>é</strong></strong>s d'<strong>é</strong>chappement au système immunitaire)<br />
CYTOPLASME<br />
TOLL-LIKE RECEPTOR : TLR<br />
C-TYPE LECTIN RECEPTOR : CLR<br />
TLR3<br />
ARN db<br />
TLR7/8<br />
ARN sb<br />
RIG-LIKE RECEPTOR : RLR<br />
NOD-LIKE RECEPTOR : NLR<br />
ADN<br />
CpG<br />
RIG-1<br />
NOD1<br />
ENDOSOME<br />
TLR9<br />
ARN viral<br />
MDA-5<br />
LGP2<br />
Peptidoglycane<br />
NOD2<br />
NLRP1<br />
NLRP3<br />
Toll Like Receptor (TLR)<br />
DAMPs : Danger‐Associated Molecular Patterns<br />
dommage /<br />
stress/<br />
n<strong>é</strong>crose<br />
tissue<br />
Signaux<br />
d’alarme<br />
13 TLR identifi<strong>é</strong>s chez le mammifère<br />
Heat shock proteins (HSP)<br />
Acide urique<br />
ATP extracellulaire<br />
High mobility group 1 (HMGB1)<br />
IL‐1<br />
F‐actine<br />
D<strong>é</strong>riv<strong>é</strong> oxyg<strong>é</strong>n<strong>é</strong> ROS<br />
Dissolution de la matrice extra‐cellulaire<br />
…<br />
APC<br />
T<br />
Page 5
DAMPs : Danger‐Associated Molecular Patterns<br />
Activation des PRR<br />
• Production de cytokines et<br />
chimiokines inflammatoires<br />
(TNF‐, IL‐6, IL‐12, IL‐8, IL‐1)<br />
• R<strong>é</strong>ponse anti‐virale :<br />
production d'IFN de type I<br />
(IFN‐, IFN‐)<br />
inflammation<br />
MyD88 ‐/‐<br />
infections bact<strong>é</strong>riennes<br />
inflammation<br />
Adapt<strong>é</strong> de Kawai & Akira, Nat. Immunol., 2010, 11(5):373<br />
Inflammasome<br />
Inflammasome<br />
pro-IL-1<br />
pro-IL-18<br />
IL-1<br />
IL-18<br />
IL-1<br />
IL-18<br />
Deganais M et al. 2012. Cell Death Differ<br />
Page 6
Activation de la r<strong>é</strong>ponse immunitaire adaptative<br />
par la r<strong>é</strong>ponse immunitaire inn<strong>é</strong>e<br />
Cytokines<br />
(IL-1, IL6, IL12, …)<br />
PRR<br />
lymphocyte T<br />
naïf<br />
NF-B<br />
CD80/CD86<br />
CD28<br />
T<br />
CMH<br />
TCR<br />
Phagosome<br />
Ex : Burnet Janeway Matzinger<br />
1969 1989 2002<br />
cellule<br />
pr<strong>é</strong>sentatrice<br />
d'antigène<br />
R<strong>é</strong>cepteur<br />
phagocytaire<br />
Microorganismes<br />
pathogènes<br />
L’activation des PRR induit :<br />
• Maturation des CPA<br />
• Augmentation de l'expression des<br />
mol<strong>é</strong>cules de co‐stimulation (CD80/CD86)<br />
Pradeu & Cooper, Frontiers in Immunology, 2012<br />
Expl : immun<strong>it<strong>é</strong></strong> des muqueuses<br />
« M<strong>é</strong>nage à trois » : Microbiote - hôte - pathogène<br />
Bact<strong>é</strong>ries commensales<br />
Pathogènes<br />
pathogène<br />
Microbiote<br />
r<strong>é</strong>sident<br />
IL-10<br />
TGF- <br />
Signaux de danger<br />
IL-1, IL-6, IL-8, CCL5<br />
INFLAMMATION<br />
Microbiote<br />
Microbiote<br />
r<strong>é</strong>sident<br />
Microbiote<br />
r<strong>é</strong>sident<br />
Microbiote<br />
r<strong>é</strong>sident<br />
r<strong>é</strong>sident<br />
pathogène Microbiote<br />
Microbiote<br />
r<strong>é</strong>sident Microbiote<br />
r<strong>é</strong>sident<br />
r<strong>é</strong>sident<br />
DC<br />
« tol<strong>é</strong>rogène »<br />
DC<br />
T4<br />
PNN<br />
DC<br />
DC<br />
« immunogène »<br />
T4<br />
TOLERANCE<br />
IMMUNITE<br />
Epith<strong>é</strong>lium intestinal à<br />
Epith<strong>é</strong>lium intestinal<br />
l’hom<strong>é</strong>ostasie<br />
inflammatoire<br />
«Switch»<br />
commensalisme - pathog<strong>é</strong>nic<strong>it<strong>é</strong></strong><br />
Th17<br />
Th1<br />
Tr1<br />
Treg Treg<br />
Th2<br />
Th17<br />
Th1<br />
Tr1<br />
Treg<br />
Th2<br />
Treg<br />
Page 7
R<strong>é</strong>action inflammatoire<br />
Reconnaissance de<br />
mico-organismes<br />
Barrières naturelles<br />
Flore intestinale<br />
Notion de danger et reconnaissance<br />
R<strong>é</strong>action inflammatoire<br />
Les lymphocytes de la r<strong>é</strong>ponse inn<strong>é</strong>e<br />
Augmentation ti n de la<br />
perm<strong>é</strong>abil<strong>it<strong>é</strong></strong> vasculaire<br />
Modification des propri<strong>é</strong>t<strong>é</strong>s<br />
d’adh<strong>é</strong>rence de l’endoth<strong>é</strong>lium<br />
Lib<strong>é</strong>ration de m<strong>é</strong>diateurs par<br />
les cellules phagocytaires.<br />
R<strong>é</strong>paration du tissu l<strong>é</strong>s<strong>é</strong> et prise<br />
en charge de l’Ag par des CPA.<br />
R<strong>é</strong>action inflammatoire<br />
R<strong>é</strong>action inflammatoire<br />
Reconnaissance de<br />
mico-organismes<br />
Augmentation ti n de la<br />
perm<strong>é</strong>abil<strong>it<strong>é</strong></strong> vasculaire<br />
Modification des propri<strong>é</strong>t<strong>é</strong>s<br />
d’adh<strong>é</strong>rence de l’endoth<strong>é</strong>lium<br />
Agent<br />
agresseur<br />
mastocyte<br />
histamine<br />
basophile<br />
histamine<br />
Agent<br />
agresseur<br />
Mo<br />
PN<br />
Reconnaissance de<br />
mico-organismes<br />
Augmentation ti n de la<br />
perm<strong>é</strong>abil<strong>it<strong>é</strong></strong> vasculaire<br />
Modification des propri<strong>é</strong>t<strong>é</strong>s<br />
d’adh<strong>é</strong>rence de l’endoth<strong>é</strong>lium<br />
C3a<br />
C5a<br />
Compl<strong>é</strong>ment<br />
Kinines<br />
Coagulation<br />
Plasma<br />
PN<br />
PN<br />
Mo<br />
Lib<strong>é</strong>ration de m<strong>é</strong>diateurs par<br />
TISSU<br />
ENDOTHELIUM<br />
VAISSEAU<br />
les cellules phagocytaires.<br />
Lib<strong>é</strong>ration de m<strong>é</strong>diateurs par<br />
les cellules phagocytaires<br />
TISSU<br />
ENDOTHELIUM<br />
VAISSEAU<br />
R<strong>é</strong>paration du tissu l<strong>é</strong>s<strong>é</strong> et prise<br />
en charge de l’Ag par des CPA.<br />
Lib<strong>é</strong>ration d'amines vasoactives<br />
(Rougeur, chaleur)<br />
R<strong>é</strong>paration du tissu l<strong>é</strong>s<strong>é</strong> et prise<br />
en charge de l’Ag par des CPA<br />
Apport de m<strong>é</strong>diateurs plasmatiques solubles<br />
(Gonflement)<br />
Page 8
VOIE DES LECTINES<br />
MBL, ficolines<br />
VOIE CLASSIQUE<br />
complexe immun Ag-Ac<br />
VOIE ALTERNE<br />
membrane microbienne<br />
Action du compl<strong>é</strong>ment<br />
mannose<br />
MASP<br />
MBL<br />
bact<strong>é</strong>ries<br />
C4a<br />
C4<br />
C2<br />
C1r C1s<br />
C1q<br />
C1 Inhibitor<br />
C1QBP<br />
C3a<br />
Facteur H<br />
C2<br />
C3b<br />
Bb<br />
pathogène<br />
Facteur D<br />
Facteur B<br />
D<strong>é</strong>fense<br />
anti-infectieuse<br />
Complexe d’attaque membranaire<br />
(C5b, C6, C7, C8, C9)<br />
bact<strong>é</strong>rie<br />
C3b<br />
Neutrophile<br />
Macrophage<br />
C2b<br />
C4BP, CD46,<br />
Facteur I<br />
C2a<br />
C4b<br />
C3a<br />
CR1, CR2, MCP<br />
CD46, Facteur I<br />
C3a<br />
Bb<br />
C3b<br />
Ba<br />
DAF<br />
LYSE<br />
OPSONISATION & PHAGOCYTOSE<br />
C3<br />
C3b<br />
C3<br />
Système du compl<strong>é</strong>ment:<br />
C4b<br />
C2a<br />
C3b<br />
C3b<br />
C3b<br />
Bb<br />
Mastocytes<br />
-30aine prot<strong>é</strong>ines plasmatiques<br />
ou membranaires,<br />
- la plupart sont des enzymes<br />
à activ<strong>it<strong>é</strong></strong> prot<strong>é</strong>olytique, elles-même<br />
activ<strong>é</strong>es par clivage enzymatique.<br />
CD59<br />
C5<br />
C5a<br />
C5b<br />
C6-C9<br />
poly C9<br />
C8<br />
COMPLEXE<br />
C6 C7 D'ATTAQUE<br />
C5b MEMBRANAIRE<br />
M<strong>é</strong>diateurs de<br />
l’inflammation<br />
Prostaglandines<br />
Leucotriènes<br />
C5a<br />
DEGRANULATION<br />
Cytokines<br />
Histamines<br />
C5a<br />
VAISSEAU<br />
SANGUIN<br />
TISSU<br />
RECRUTEMENT DES PHAGOCYTES<br />
"cascade d'activation du compl<strong>é</strong>ment" LYSE<br />
Bhakdi S. et Tranum-Jensen J.<br />
PNAS, 1979<br />
R<strong>é</strong>action inflammatoire<br />
Reconnaissance de<br />
mico-organismes<br />
R<strong>é</strong>cepteur<br />
de chimiokine<br />
Ligand de<br />
s<strong>é</strong>lectine<br />
2 Int<strong>é</strong>grine<br />
Augmentation ti n de la<br />
perm<strong>é</strong>abil<strong>it<strong>é</strong></strong> vasculaire<br />
Modification des propri<strong>é</strong>t<strong>é</strong>s<br />
d’adh<strong>é</strong>rence de l’endoth<strong>é</strong>lium<br />
Recrutement des phagocytes<br />
vers le foyer infectieux<br />
Es<strong>é</strong>lectine<br />
ou<br />
Ps<strong>é</strong>lectine<br />
PNN<br />
Prot<strong>é</strong>oglycane<br />
et chimiokine<br />
ICAM1<br />
Roulement<br />
Activation<br />
Adh<strong>é</strong>rence<br />
irr<strong>é</strong>versible<br />
Diap<strong>é</strong>dèse<br />
V<br />
A<br />
I<br />
S<br />
S<br />
E<br />
A<br />
U<br />
ENDOTHELIUM<br />
Lib<strong>é</strong>ration de m<strong>é</strong>diateurs par<br />
les cellules phagocytaires<br />
IL-1<br />
TNF<br />
Activation de<br />
l’endoth<strong>é</strong>lium<br />
T<br />
I<br />
S<br />
S<br />
U<br />
R<strong>é</strong>paration du tissu l<strong>é</strong>s<strong>é</strong> et prise<br />
en charge de l’Ag par des CPA<br />
Mastocyte<br />
(Macrophage)<br />
bact<strong>é</strong>ries<br />
Chimiotactisme<br />
vers le site<br />
d’infection<br />
Gradient<br />
chimiokines<br />
attractives<br />
Page 9
Phagocytose<br />
Phagocytose<br />
1. CHIMIOTACTISME<br />
2 cat<strong>é</strong>gories de r<strong>é</strong>cepteurs phagocytaires :<br />
- r<strong>é</strong>cepteurs liant des particules opsonis<strong>é</strong>es<br />
(i.e. marqu<strong>é</strong>es par des mol<strong>é</strong>cules solubles qui<br />
les enrobent)<br />
- r<strong>é</strong>cepteurs liant directement les microbes :<br />
• r<strong>é</strong>cepteur du mannose, dectine-1, …<br />
• r<strong>é</strong>cepteurs <strong>é</strong>boueurs ("scavenger<br />
receptors")<br />
• CD14 …<br />
R Fc<br />
R<strong>é</strong>cepteur des<br />
fragments Fc des Ig<br />
R C3b<br />
R<strong>é</strong>cepteur du<br />
compl<strong>é</strong>ment<br />
Macrophage<br />
Neutrophile<br />
DC<br />
R<strong>é</strong>cepteurs<br />
phagocytaires<br />
opsonisation<br />
Rôle de la phagocytose :<br />
polym<strong>é</strong>risation<br />
- destruction des agents pathogènes d’actine dactine<br />
- <strong>é</strong>limination des cellules apoptotiques<br />
- <strong>é</strong>vacuation de particules exogènes<br />
inertes<br />
fusion du phagosome<br />
avec des granules et<br />
des lysosomes<br />
=<br />
phagolysosome<br />
3. INTERNALISATION<br />
lysosomes<br />
4. DESTRUCTION<br />
(enzymes, O 2‐ , H 2 O 2 , d<strong>é</strong>riv<strong>é</strong>s NO)<br />
2. CAPTURE<br />
R<strong>é</strong>action inflammatoire<br />
R<strong>é</strong>action inflammatoire<br />
Reconnaissance de<br />
mico-organismes<br />
Reconnaissance de<br />
mico-organismes<br />
DC<br />
Augmentation ti n de la<br />
perm<strong>é</strong>abil<strong>it<strong>é</strong></strong> vasculaire<br />
Enzymes lysosomiales<br />
Radicaux libres oxyg<strong>é</strong>n<strong>é</strong>s<br />
PN<br />
Augmentation ti n de la<br />
perm<strong>é</strong>abil<strong>it<strong>é</strong></strong> vasculaire<br />
Mo<br />
Mo<br />
IL-8<br />
Mo<br />
CSF<br />
Modification des propri<strong>é</strong>t<strong>é</strong>s<br />
d’adh<strong>é</strong>rence de l’endoth<strong>é</strong>lium<br />
Ac.arachidonique<br />
PN<br />
PN<br />
PN<br />
Mo<br />
Modification des propri<strong>é</strong>t<strong>é</strong>s<br />
d’adh<strong>é</strong>rence de l’endoth<strong>é</strong>lium<br />
Macrophage<br />
T<br />
Moelle<br />
osseuse<br />
Lib<strong>é</strong>ration de m<strong>é</strong>diateurs par<br />
IL-6<br />
les cellules phagocytaires<br />
PG LT PAF<br />
Lib<strong>é</strong>ration de m<strong>é</strong>diateurs par<br />
les cellules phagocytaires<br />
TISSU<br />
ENDOTHELIUM<br />
VAISSEAU<br />
R<strong>é</strong>paration du tissu l<strong>é</strong>s<strong>é</strong> et prise<br />
en charge de l’Ag par des CPA<br />
TISSU<br />
ENDOTHELIUM<br />
VAISSEAU<br />
R<strong>é</strong>paration du tissu l<strong>é</strong>s<strong>é</strong> et prise<br />
en charge de l’Ag par des CPA<br />
Inflammation chronique<br />
Page 10
Cytokines : r<strong>é</strong>gulation de l'inflammation<br />
Cytokines : r<strong>é</strong>gulation de l'inflammation<br />
IL-1<br />
IL-1ra<br />
IL-1-R<br />
TNF<br />
IL-1<br />
IL-8<br />
PF4<br />
NAE2<br />
MIP-1<br />
MCAF<br />
PDGF<br />
EGF<br />
FGF<br />
IGF-1<br />
IGF-2<br />
NGF<br />
TGF<br />
macrophage<br />
TNF-<br />
sTNF-R<br />
Inflammation aigue :<br />
activ<strong>it<strong>é</strong></strong><br />
chimiotactique<br />
Inflammation chronique :<br />
persistance<br />
prolif<strong>é</strong>ration cellulaire<br />
fibrose<br />
TNF-R<br />
IL-1ra, TNF-Rs,<br />
IL-4, IL-6, IL-10,<br />
IFN<br />
IFN<br />
Bloque les cytokines pro-inflammatoires<br />
Supprime CXCL1 et CXCL8<br />
Induit CXCL5 et CXCL6<br />
Induit les antagonistes d’IL-1 et TNF<br />
Induit l’apoptose des polynucl<strong>é</strong>aires<br />
Recrutement de<br />
leucocytes<br />
immun<strong>it<strong>é</strong></strong> inn<strong>é</strong>e<br />
Ry<br />
Monocytes<br />
Lymphocytes T et B<br />
Polynucl<strong>é</strong>aires<br />
temps<br />
Rôle de l’IL-6<br />
immun<strong>it<strong>é</strong></strong> acquise<br />
Influence la polarisation des T<br />
Empêche l’apoptose des T<br />
Contrôle la r<strong>é</strong>gulation T<br />
Favorise la migration<br />
Contrôle la diff<strong>é</strong>renciation<br />
des monocytes<br />
Contrôle la maturation des<br />
cellules dendritiques<br />
Contrôle l’expression des<br />
r<strong>é</strong>cepteurs de chimiokines<br />
sur les T<br />
Barrières naturelles<br />
Flore intestinale<br />
Notion de danger et reconnaissance<br />
R<strong>é</strong>action inflammatoire<br />
Les lymphocytes de la r<strong>é</strong>ponse inn<strong>é</strong>e<br />
Page 11
Morphologie et ph<strong>é</strong>notype<br />
Famille des grands lymphocytes granuleux (LGL)<br />
Absence d’expression de r<strong>é</strong>cepteur pour l’antigène<br />
Cellules NK<br />
(natural killer)<br />
cellules « tueuses naturelles »<br />
CD16<br />
R<strong>é</strong>cepteur<br />
de basse affin<strong>it<strong>é</strong></strong><br />
pour le fragment<br />
Fc des IgG<br />
NK<br />
CD56<br />
(NCAM)<br />
R<strong>é</strong>cepteurs Inhibiteurs<br />
R<strong>é</strong>cepteurs Activateurs<br />
capac<strong>it<strong>é</strong></strong> à lyser spontan<strong>é</strong>ment, sans activation et amplification<br />
pr<strong>é</strong>alable, des cellules tumorales ou infect<strong>é</strong>es tout en<br />
<strong>é</strong>pargnant les cellules saines.<br />
2 populations distinctes<br />
CD56 + CD16 + CD56 +++ CD16 -<br />
~ 90% des cellules NK circulantes<br />
activ<strong>it<strong>é</strong></strong> cytotoxique<br />
Organes lymphoïdes secondaires<br />
s<strong>é</strong>cr<strong>é</strong>tion de cytokines/chimiokines<br />
NK<br />
R<strong>é</strong>cepteurs activateurs / inhibiteurs<br />
R<strong>é</strong>cepteur Inhibiteur<br />
ligands = mol<strong>é</strong>cules du CMH classe I<br />
R<strong>é</strong>cepteur Activateur<br />
signal OFF<br />
nombreux ligands (prot<strong>é</strong>ines de stress,<br />
marqueurs d’infections,…)<br />
signal ON<br />
2 grandes familles des R<strong>é</strong>cepteurs :<br />
R<strong>é</strong>cepteurs activateur / inhibiteur<br />
Membre de la superfamille des Ig : KIR (Killer cell Immunoglobuline-like Receptor)<br />
Famille des lectines de type C (CD94/NKG2)<br />
Expl :<br />
r<strong>é</strong>cepteurs KIR<br />
R<strong>é</strong>cepteur<br />
activateur<br />
P<br />
P<br />
DAP12<br />
ITAM<br />
ITIM<br />
P<br />
P<br />
R<strong>é</strong>cepteur<br />
inhibiteur<br />
R<strong>é</strong>cepteurs<br />
Inhibiteurs<br />
R<strong>é</strong>cepteurs<br />
Activateurs<br />
activation en cascade de<br />
phosphorylases / kinases<br />
activation de<br />
phosphatases<br />
-<br />
+<br />
CYTOTOXICITE<br />
ITAM : Immunoreceptor Tyrosine-based Activation Motif<br />
ITIM : Immunoreceptor Tyrosine-based Inhibition Motif<br />
Page 12
Modes d’action<br />
1. Cytotoxic<strong>it<strong>é</strong></strong> naturelle<br />
Immunosurveillance<br />
Cellule normale<br />
"Soi manquant"<br />
Cellule tumorale<br />
ou infect<strong>é</strong>e<br />
Exocytose<br />
perforine/granzyme<br />
R<strong>é</strong>cepteur<br />
inhibiteur<br />
NK<br />
R<strong>é</strong>cepteur<br />
activateur<br />
Perforine<br />
Granzymes<br />
cellules<br />
infect<strong>é</strong>es ou<br />
tumorales<br />
n<strong>é</strong>crose<br />
CYTOTOXICITE<br />
"Soi modifi<strong>é</strong>"<br />
Cellule tumorale<br />
ou infect<strong>é</strong>e<br />
R<strong>é</strong>cepteurs de mort<br />
NK<br />
NK<br />
FasL<br />
Fas (CD95)<br />
cellules<br />
infect<strong>é</strong>es ou<br />
tumorales<br />
Allor<strong>é</strong>activ<strong>it<strong>é</strong></strong><br />
Cellule <strong>é</strong>trangère<br />
mol<strong>é</strong>cules CMH classe I<br />
incompatibles<br />
TRAIL<br />
TNF-<br />
TRAILR<br />
apoptose<br />
p<br />
R<strong>é</strong>cepteur inhibiteur<br />
R<strong>é</strong>cepteur activateur<br />
HLA Classe I<br />
Ligand activateur<br />
S<strong>é</strong>cr<strong>é</strong>tion de TNF-<br />
NK<br />
TNF-R<br />
cellules<br />
infect<strong>é</strong>es ou<br />
tumorales<br />
apoptose<br />
Modes d’action<br />
2. Cytotoxic<strong>it<strong>é</strong></strong> cellulaire d<strong>é</strong>pendante des<br />
anticorps (ADCC)<br />
Modes d’action<br />
3. Production de cytokines<br />
NK<br />
TNF<br />
perforine<br />
Cellule<br />
cible<br />
pathogènes<br />
Mφ<br />
macrophage<br />
Cellule stromale<br />
IL-12<br />
TNF-<br />
IL-15<br />
IFN-<br />
NK<br />
IFN-<br />
TNF-<br />
IL-10<br />
Chimiokines<br />
CD16<br />
Fc-r<strong>é</strong>cepteur<br />
Anticorps<br />
IgG<br />
Antigène<br />
R<strong>é</strong>gulation de la r<strong>é</strong>ponse inflammatoire :<br />
recrutement et activation de macrophages et cellules dendritiques<br />
Contrôle de la r<strong>é</strong>plication virale par la production d’IFN-<br />
Orientation de la r<strong>é</strong>ponse adaptative (humorale / cellulaire / r<strong>é</strong>gulatrice)<br />
Page 13
Lymphocytes T <br />
Lymphocytes NKT<br />
Distribution<br />
• Sang : 1 à 5% des lymphocytes circulants (DN CD4 - CD8 - )<br />
• Epith<strong>é</strong>liums (intestin, peau) : 50% des cellules T (CD8 dans l'intestin)<br />
Fonction<br />
• Production de cytokines/chimiokines<br />
• Cytotoxic<strong>it<strong>é</strong></strong><br />
Distribution<br />
• Sang : 0,001 % à 3 % des lymphocytes circulants<br />
• organes lymphoïdes (rate thymus, OL2aire) : 2,5% des LT<br />
• foie : 30% des LT<br />
Expriment des marqueurs de cellules NK (CD56 et CD16) et de<br />
cellules T (TCR et CD3).<br />
TCR très conserv<strong>é</strong> (semi-invariant):<br />
chaîne du TCR : V14-J18<br />
Le r<strong>é</strong>pertoire de TCR est très lim<strong>it<strong>é</strong></strong><br />
Pas de restriction aux mol<strong>é</strong>cules de CMH classiques<br />
Reconnaissent des <strong>é</strong>pitopes conserv<strong>é</strong>s au sein de pathogènes<br />
CD16<br />
CD56<br />
TCR<br />
V14-J18<br />
associ<strong>é</strong> pr<strong>é</strong>f<strong>é</strong>rentiellement à la<br />
chaîne du TCR : V11<br />
Natural Killer T lymphocyte semi-invariant (iNKT)<br />
Lymphocytes B1<br />
CD161<br />
IFN-<br />
IgM<br />
B1<br />
Ac naturels<br />
et IgA<br />
TCR<br />
V14-J18<br />
CD1d<br />
APC<br />
IL-4<br />
IL-17<br />
Pr<strong>é</strong>sence d’Ac "naturels" pr<strong>é</strong>existants à une infection, s<strong>é</strong>cr<strong>é</strong>t<strong>é</strong>s par les cellules B1<br />
protection pr<strong>é</strong>coce, rapide contre les infections virales et bact<strong>é</strong>riennes<br />
Cellules B1<br />
Reconnaissance d’Ag (glyco)lipides endogènes ou exogènes (paroi de<br />
bact<strong>é</strong>ries Gram- n’ exprimant pas de LPS) pr<strong>é</strong>sent<strong>é</strong>s par la mol<strong>é</strong>cule<br />
l<br />
CD1d exprim<strong>é</strong>e par les CPA telles que les DC et MΦ.<br />
Production massive de cytokines<br />
D<strong>é</strong>veloppement durant la vie fœtale et post‐natale, puis maintient par auto‐renouvellement.<br />
localisation : cav<strong>it<strong>é</strong></strong>s p<strong>é</strong>riton<strong>é</strong>ale et pleurale, lamina propria de l’intestin<br />
Production d’Ac ind<strong>é</strong>pendante des LT, sans stimulation antig<strong>é</strong>nique :<br />
• IgM "naturels" et IgA<br />
• divers<strong>it<strong>é</strong></strong> très lim<strong>it<strong>é</strong></strong>e (utilisation exclusive des segments VH les plus proches de D,<br />
absence de divers<strong>it<strong>é</strong></strong> jonctionnelle)<br />
• absence d’HMS<br />
Page 14
Lymphocytes B MZ<br />
3 sous‐populations de lymphocytes B<br />
MZ<br />
IgM<br />
IgM<br />
IgG<br />
IgA<br />
B1<br />
Ac naturels<br />
et IgA<br />
Production rapide d’Ac (~3 jours) contre les agents infectieux (polysaccharides des<br />
bact<strong>é</strong>ries encapsul<strong>é</strong>es) pr<strong>é</strong>sents dans le sang<br />
"innate-like"<br />
MZ<br />
IgM<br />
IgG<br />
IgA<br />
Cellules MZ<br />
Nombre peu <strong>é</strong>lev<strong>é</strong> chez le nouveau‐n<strong>é</strong>, effectif significatif ~ 1‐2 ans<br />
apoptose<br />
Centre<br />
germinatif<br />
Prolif<strong>é</strong>ration<br />
et mutations<br />
Localisation : zone marginale (MZ) de la rate<br />
B2<br />
Cellule<br />
m<strong>é</strong>moire<br />
Ph<strong>é</strong>notype de cellules activ<strong>é</strong>es<br />
Production d’Ac ind<strong>é</strong>pendante des LT après stimulation antig<strong>é</strong>nique :<br />
• IgM, IgG, IgA<br />
• divers<strong>it<strong>é</strong></strong> moyenne<br />
• absence d’HMS ???<br />
adaptatif<br />
Adapt<strong>é</strong> de<br />
Shapiro‐Shelef & Calame,<br />
Nat Rev Immunol.<br />
2005; 5:230‐242.<br />
Cellule<br />
folliculaire<br />
IgM<br />
S<strong>é</strong>lection et<br />
commutation<br />
isotypique<br />
Semaine 1 Semaine 2<br />
Survie<br />
dans MO<br />
Semaine 3<br />
IgG<br />
IgA<br />
IgE<br />
Page 15