5.7MB - Facultad de Ciencias
5.7MB - Facultad de Ciencias
5.7MB - Facultad de Ciencias
Create successful ePaper yourself
Turn your PDF publications into a flip-book with our unique Google optimized e-Paper software.
Curso <strong>de</strong> Evolución 2006<br />
<strong>Facultad</strong> <strong>de</strong> <strong>Ciencias</strong><br />
Montevi<strong>de</strong>o, Uruguay<br />
http://evolucion.fcien.edu.uy/<br />
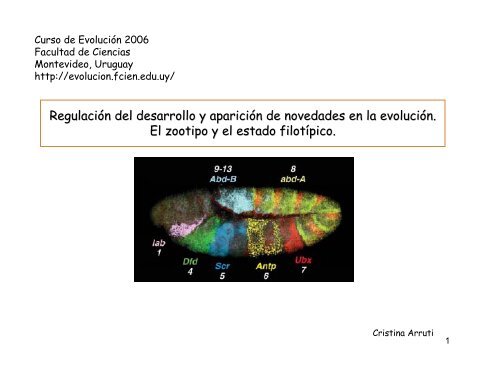
Regulación n <strong>de</strong>l <strong>de</strong>sarrollo y aparición n <strong>de</strong> noveda<strong>de</strong>s en la evolución.<br />
El zootipo y el estado filotípico<br />
pico.<br />
Cristina Arruti<br />
1
Ernst Mayr<br />
(1904-2005)<br />
‘‘There are fashionable problems<br />
and there are neglected<br />
problems in any field of research.<br />
The problem of the emergence of<br />
evolutionary novelties has<br />
undoubtedly been greatly neglected<br />
during the past two or three <strong>de</strong>ca<strong>de</strong>s,<br />
in spite of its importance in the<br />
theory of evolution.’’<br />
Mayr E. 1960. The emergence of evolutionary novelties.<br />
En: Tax S, Editor. Evolution after Darwin. Cambridge, MA.<br />
Harvard University Press. p 349–380.<br />
2
Sean B. Carroll<br />
Endless Forms Most Beautiful: The New<br />
Science of Evo Devo<br />
W. W. Norton (2005).<br />
“Carroll emphasizes throughout that the evolution of animal form and<br />
complexity results from three factors.<br />
The first is modularity of organization: the ground plan of bilateral animals<br />
involves repeated segments that can evolve in<strong>de</strong>pen<strong>de</strong>ntly.<br />
The second factor is that most animals share a small but similar set of<br />
‘tool-kit genes’ that regulate the <strong>de</strong>velopment of different modules. These<br />
genes, which produce regulatory proteins called transcription factors, are<br />
highly conserved in function; Hox genes are the canonical example.<br />
Thirdthesis: themainengineofevolutionisnotchangein protein-coding<br />
genes but in the switches that control them. Changes in these switches —<br />
the promoters and enhancers in DNA that regulate the transcription of<br />
protein-coding genes —supposedly promote evolution by causing existing<br />
genes to be expressed at new times and places.”<br />
3
Modularidad <strong>de</strong> la organización<br />
La existencia <strong>de</strong> módulos en la organización <strong>de</strong>l individuo permite<br />
cambios sin que se produzca disrupción <strong>de</strong> la actividad funcional<br />
en el resto <strong>de</strong>l organismo<br />
4
Ejemplo 1 <strong>de</strong> modularidad: tamaños relativos <strong>de</strong> las áreas oculares<br />
en algunos amniotas<br />
Jeffery et al. 2002<br />
5
Ejemplo 2 <strong>de</strong> modularidad: “in<strong>de</strong>pen<strong>de</strong>ncia” en el <strong>de</strong>sarrollo <strong>de</strong> campos<br />
morfogenéticos. Campo ocular<br />
Ambystoma punctatum<br />
Ambystoma tigrinum<br />
Crecimiento <strong>de</strong> complejos oculares transplantados entre A. tigrinum yA. punctatum,<br />
Se conservan las tasas <strong>de</strong> crecimiento <strong>de</strong> las especies <strong>de</strong> orígen<br />
6
Ejemplo 3 <strong>de</strong> modularidad: comportamiento modular <strong>de</strong> los campos<br />
<strong>de</strong> miembro anterior en transplantes cruzados<br />
A. punctatum<br />
A. tigrinum<br />
7
El concepto <strong>de</strong> modularidad se extien<strong>de</strong> a:<br />
* Circuitos metabólicos<br />
* Vías <strong>de</strong> señalización<br />
Al igual que en los módulos <strong>de</strong> organización<br />
morfológica, éstos están compuestos <strong>de</strong><br />
partes homólogas (moléculas) organizadas<br />
según diseños homólogos.<br />
* Complejos <strong>de</strong> regulación génica<br />
1.- La evolución <strong>de</strong>pen<strong>de</strong> <strong>de</strong> cambios heredables en el <strong>de</strong>sarrollo<br />
2.- El <strong>de</strong>sarrollo es modular, los módulos pue<strong>de</strong>n intercambiarse<br />
sin afectar a otros módulos<br />
3.- Los módulos pue<strong>de</strong>n ser co-optados para nuevas funciones<br />
4.- Los módulos <strong>de</strong>pen<strong>de</strong>n <strong>de</strong> comunicación intercelular.<br />
Gilbert-Bolker J. Exp. Zool. (Mol. Dev. Evol.) (2001.), 291:1–12.<br />
8
Ejemplo 1 <strong>de</strong> modularidad con homologías en componentes <strong>de</strong> los circuitos<br />
Vía <strong>de</strong> Wnt<br />
9
Ejemplo 2 <strong>de</strong> modularidad con homologías en complejos <strong>de</strong> regulación.<br />
Dorsal<br />
Eje dorso-ventral en Drosophila y ratón<br />
SN<br />
Drosophila<br />
Ventral<br />
Dorsal<br />
SN<br />
Ratón<br />
Ventral<br />
10
Genes reguladores <strong>de</strong>l <strong>de</strong>sarrollo compartidos.<br />
Caso canónico: HOX<br />
11
Hepta hibridización “in situ” <strong>de</strong> transcriptos <strong>de</strong> genes Hox<br />
en embrión <strong>de</strong> Drosophila<br />
Anterior<br />
Posterior<br />
labial (lab),<br />
Deformed (Dfd),<br />
Sexcombs reduced (Scr),<br />
Antennapedia (Antp),<br />
Ultrabithorax (Ubx),<br />
abdominal-A (abd-A),<br />
Abdominal-B (Abd-B).<br />
D. Kosman, en<br />
Lemons and McGinnis, 2006<br />
12
Regiones <strong>de</strong> expresión <strong>de</strong> genes Hox en embriones <strong>de</strong> ratón<br />
Ant.<br />
Post.<br />
13
Distribución <strong>de</strong> complejos<br />
Hox en el cuerpo <strong>de</strong> un<br />
insecto y <strong>de</strong> un embrión<br />
<strong>de</strong> mamífero<br />
14
Organización cromosómica <strong>de</strong> genes Hox en animales representativos<br />
Lemons and McGinnis, 2006<br />
15
Otros genes reguladores<br />
Pax 6<br />
17
Formación ectópica <strong>de</strong> estructuras oculares por expresión <strong>de</strong><br />
genes Pax 6<br />
Ojos en patas <strong>de</strong> Drosophila<br />
Pax 6 <strong>de</strong> ratón<br />
Pax 6 <strong>de</strong> calamar<br />
18
Intercambiabilidad <strong>de</strong> proteínas homólogas<br />
Rescate <strong>de</strong> ratones KO para Engrailed-1 con secuencia <strong>de</strong> Drosophila<br />
19
Cambios en los sistemas <strong>de</strong> regulación como<br />
maquinarias <strong>de</strong>l cambio evolutivo<br />
20
(1920-<br />
21
“Le bricolage <strong>de</strong> l’evolution”<br />
Dón<strong>de</strong>? Cambios <strong>de</strong> lugar<br />
Cuándo? Cambios en el tiempo<br />
Cuánto? Cambios en la cantidad<br />
Cuál? Cambios en la cualidad<br />
HETEROTOPÍA<br />
HETEROCRONÍA<br />
HETEROMETRÍA<br />
HETEROTIPIA<br />
W.Arthur (2004)<br />
22
“Small changes modifying the<br />
distribution in time and space of<br />
the same structures are sufficient<br />
to affect <strong>de</strong>eply the form, the<br />
functioning, and the behavior of<br />
the final product-the adult animal.”<br />
F. Jacob, 1977<br />
HETEROTOPÍA<br />
HETEROCRONÍA<br />
HETEROMETRÍA<br />
HETEROTIPIA<br />
Algunos ejemplos:<br />
23
HETEROTOPÍA<br />
Ejemplo 1: membrana interdigital <strong>de</strong>l miembro posterior<br />
Pollo<br />
BMP4 Gremlin Apoptosis Morfología<br />
Pato<br />
BMP4= induce apoptosis<br />
Gremlin= inhibidor <strong>de</strong> BMP4<br />
24
HETEROTOPÍA<br />
Ejemplo 2:segmentos en crustáceos e insectos<br />
25
HETEROCRONÍA<br />
Ejemplo 1 : tamaños relativos <strong>de</strong> las áreas oculares<br />
en algunos amniotas<br />
Jeffery et al. 2002<br />
26
HETEROCRONÍA<br />
Ejemplo 2 : pérdida <strong>de</strong> dígitos en miembro<br />
<strong>de</strong> una lagartija australiana (Hemierges)<br />
Shapiro et al., 2003<br />
27
HETEROMETRÍA<br />
Ejemplo: Forma <strong>de</strong>l pico y niveles<br />
<strong>de</strong> expresión <strong>de</strong> Bmp4 en pinzones<br />
Abzhanov et al. 2004<br />
Niveles <strong>de</strong> expresión <strong>de</strong> Bmp4<br />
en la masa fronto-nasal <strong>de</strong> pollo<br />
y pato<br />
Wu et al. 2004<br />
28
HETEROMETRÍA: ALOMETRÍA<br />
Ejemplo: variación en la tasa<br />
<strong>de</strong> crecimiento <strong>de</strong> módulos cefálicos<br />
en el <strong>de</strong>sarrollo <strong>de</strong> chimpancé y<br />
humano<br />
Chimpancé<br />
Humano<br />
29
HETEROTIPIA<br />
Ejemplo: expansión <strong>de</strong> un repetido <strong>de</strong> polialanina en Hoxd13<br />
Heterocigotes: polidactilia<br />
Homocigotes: sindactilia<br />
30
Correlación entre cambios en genes Hox y<br />
cambios evolutivos en la morfología<br />
31
¿Qué <strong>de</strong>fine a un animal?<br />
Respuestas <strong>de</strong>s<strong>de</strong> la Biología <strong>de</strong>l Desarrollo<br />
32
DEFINICIONES<br />
JMW Slack<br />
33
“UNIDAD DE TIPO”<br />
Etienne Geoffroy Saint Hilaire<br />
(1772 - 1844)<br />
“…es como si la naturaleza se hubiera<br />
enclaustrado <strong>de</strong>ntro <strong>de</strong> ciertos límites,<br />
y que no hubiera formado a los seres<br />
vivos más que sobre un plan único,<br />
esencialmente el mismo en sus principios,<br />
pero al que ella habría variado <strong>de</strong> mil<br />
formas en sus partes accesorias “<br />
Mémoire sur les rapports naturels <strong>de</strong>s makis, 1796<br />
34
Karl Ernst von Baer<br />
(1792 - 1876)<br />
“The embryo of the mammal, bird, lizard, and snake and<br />
probably also the turtle, are in their early stages so<br />
uncommonly similar to one another that one can distinguish<br />
them only according to their size. I posess two small<br />
embryos in spirits of wine, embryos whose name I<br />
neglected to note down, and I am now in no position to<br />
<strong>de</strong>termine the classes to which they belong. They could be<br />
lizards, small birds, or even very young mammals.”<br />
35
KARL ERNST von BAER:<br />
“The general features of a large group of animals<br />
appear earlier in <strong>de</strong>velopment than do the specialized<br />
features of a smaller group…The early embryo is never<br />
like a lower animal, but only like its early embryo.”<br />
36<br />
(Diapo <strong>de</strong> S. Gilbert)
Ernst Haeckel<br />
“ONTOGENY RECAPITULATES<br />
PHYLOGENY”<br />
Diapo <strong>de</strong> S. Gilbert<br />
37
Zootipo<br />
• versión mo<strong>de</strong>rna <strong>de</strong>l<br />
arquetipo <strong>de</strong> Geoffroy<br />
• patrón común a todo el<br />
reino animal en la<br />
organización <strong>de</strong>l <strong>de</strong>sarrollo<br />
Estadío filotípico<br />
• fase <strong>de</strong>l <strong>de</strong>sarrollo en que<br />
se manifiesta el plan<br />
estructural <strong>de</strong> cada phylum<br />
(Diapo E. Lessa)<br />
40
Algunos embriones en su estadio filotípico<br />
Richardson,1997<br />
41
Richardson et al. 1997<br />
43
¿Cuán temprano, o tar<strong>de</strong>, se comienzan a <strong>de</strong>sarrollar las diferencias?<br />
KIWI<br />
MURCIÉLAGO<br />
Richardson, 1999<br />
44
Retomando el “bricolage” <strong>de</strong> la evolución:<br />
breve visita a un módulo sorpren<strong>de</strong>nte,<br />
o el gran problema <strong>de</strong> la evolución ocular<br />
45
“To suppose that the eye, with all its inimitable contrivances<br />
for adjusting the focus to different distances, for admitting<br />
different amounts of light, and for the correction of spherical<br />
and chromatic aberration, could have been formed by natural<br />
selection, seems, I freely confess, absurd in the highest<br />
possible <strong>de</strong>gree.”<br />
46
Platynereis dumerilii<br />
49
Volvox<br />
Organelos “oculares”<br />
Erythropsis Warnowia (Dinoflagelados)<br />
50
The likely evolution of single-chambered eyes. Arrows indicate functional <strong>de</strong>velopments,<br />
not specific evolutionary pathways.<br />
(Land MF, Fernald RD: The evolution of eyes. Annu Rev Neurosci 1992;15:1-29. )<br />
a) Pit eye, common throughout the<br />
lower phyla.<br />
b) Pinhole of Haliotis (abalone) or<br />
Nautilus.<br />
c) Eye with a lens.<br />
d) Eye with homogeneous lens,<br />
showing failure to focus.<br />
e) Eye with lens having a gradient<br />
of refractive in<strong>de</strong>x.<br />
f) Multiple lens eye of male<br />
Pontella.<br />
g)Two-lens eye of the copepod<br />
crustacean Copilia. Solid arrow<br />
shows image position and open<br />
arrow the movement of the second<br />
lens.<br />
h)Terrestrial eye of Homo sapiens<br />
with cornea and lens;<br />
Ic= image formed by cornea alone;<br />
Ir= final image on the retina.<br />
i) Mirror eye of the scallop Pecten.<br />
51
Posibles estructuras oculares en el más antiguo fósil<br />
<strong>de</strong> bilateria<br />
(¡¡ 40 a 55 millones <strong>de</strong> años antes <strong>de</strong>l Cámbrico !!)<br />
40µm<br />
Vernanimalcula guizhouena.<br />
Chen et al., 2004<br />
52
Ocelos unicelulares en la larva<br />
plánula <strong>de</strong> Tripedalia<br />
Ojos en la base <strong>de</strong> los tentáculos <strong>de</strong> Cladonema 53
Ropalios <strong>de</strong> Cubomedusa (Tripedalia cystophora)<br />
54
Platynereis dumerilii<br />
55
Ojos compuestos (insectos)<br />
56
Estructura <strong>de</strong>l ojo compuesto: omátidas<br />
57
Fotorecepción en la larva <strong>de</strong> Drosophila melanogaster<br />
Órgano <strong>de</strong> Bolwig<br />
12 fotoreceptores<br />
(8 con rodopsina 6, sensible al ver<strong>de</strong>)<br />
(4 con rodopsina 5, sensible al azul<br />
59
Ojos camerulares: calamar<br />
60
Estructura <strong>de</strong>l ojo <strong>de</strong> calamar<br />
61
Ojo <strong>de</strong> vertebrados<br />
(camerular)<br />
Pez cebra<br />
62
Inversión <strong>de</strong> capas retinianas<br />
Vertebrados<br />
Cefalópodos<br />
63
Un pez "cuatro ojos"<br />
Anableps anableps<br />
64
Esquema <strong>de</strong>l ojo <strong>de</strong> Anableps<br />
65
Building plans of three different types of eyes.<br />
a)A vertebrate eye.<br />
c)A cephalopod lens eye.<br />
b)An arthopod compound eye.<br />
The construction of eyes varies consi<strong>de</strong>rably. In vertebrates,<br />
photoreceptor cells differentiate from the central nervous system,<br />
whereas in cephalopod and arthropod eyes, they differentiate from<br />
the epi<strong>de</strong>rmis. In addition, the retina is inverse (i.e. photoreceptors<br />
are at the back of the eye) in vertebrates and everse (i.e.<br />
photoreptors are at the front of the eye) in cephalopods.<br />
66
Fernald 2006<br />
sombras refracción reflexión<br />
67<br />
Tipos principales <strong>de</strong> ópticas
A possible landscape of eye evolution created by Mike Land. Height represents<br />
optical quality and the ground plane evolutionary distance. Land writes that<br />
‘Climbing the hills is straightforward but going from one hilltop to another is near<br />
impossible’.<br />
From Dawkins R: Climbing Mount Improbable. New York, Norton, 1996<br />
68
Gradientes <strong>de</strong> proteínas y variaciones en el índice <strong>de</strong> refracción<br />
Cristalino <strong>de</strong> pez<br />
Determinación <strong>de</strong> convergencia<br />
usando laser <strong>de</strong> argón.<br />
69
¿Las similitu<strong>de</strong>s estructurales existentes entre<br />
los diferentes tipos <strong>de</strong> ojos resultan <strong>de</strong><br />
convergencia evolutiva <strong>de</strong>bida a presiones selectivas<br />
similares (analogía) o resultan <strong>de</strong> la existencia <strong>de</strong> un<br />
ancestro común (homología)?<br />
70
Homologías <strong>de</strong>:<br />
Moléculas<br />
Células<br />
71
La molécula funcionalmente esencial<br />
72
Fotoblanqueo <strong>de</strong> la<br />
rodopsina<br />
73
Fotoreceptores<br />
Rabdomérico<br />
Ciliar<br />
75
Genes involucrados en la "producción" <strong>de</strong> ojos<br />
77
Platynereis dumerilii<br />
80
Platynereis<br />
Vertebrados<br />
Arendt et al., 2004<br />
81
Differences in emphasis of explanatory factors (bold print) in different fields<br />
of evolutionary biology (dots). (a) Some of the traditional disciplines in<br />
evolutionary biology. (b) Some areas that have emerged as parts of evo-<strong>de</strong>vo.<br />
The shading indicates the overall emphasis in neo-darwinian evolutionary biology<br />
(a) and in evo-<strong>de</strong>vo (b).<br />
Breuker et al., 2006<br />
83