B. Sc. - Integrated Life Science
B. Sc. - Integrated Life Science
B. Sc. - Integrated Life Science
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
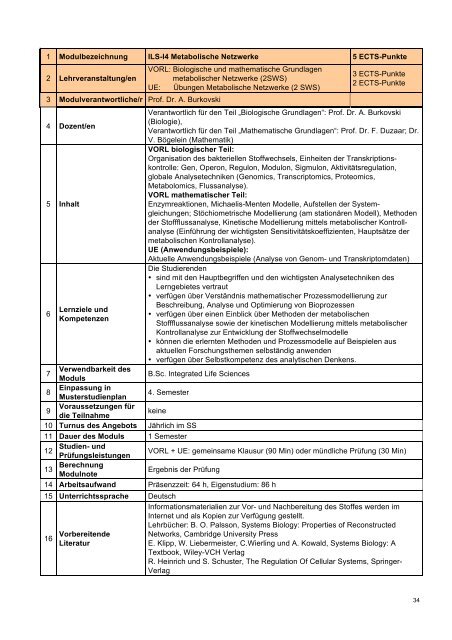
1 Modulbezeichnung ILS-I4 Metabolische Netzwerke 5 ECTS-Punkte<br />
2 Lehrveranstaltung/en<br />
3 Modulverantwortliche/r Prof. Dr. A. Burkovski<br />
4 Dozent/en<br />
5 Inhalt<br />
6<br />
Lernziele und<br />
Kompetenzen<br />
VORL: Biologische und mathematische Grundlagen<br />
metabolischer Netzwerke (2SWS)<br />
UE: Übungen Metabolische Netzwerke (2 SWS)<br />
3 ECTS-Punkte<br />
2 ECTS-Punkte<br />
Verantwortlich für den Teil „Biologische Grundlagen“: Prof. Dr. A. Burkovski<br />
(Biologie),<br />
Verantwortlich für den Teil „Mathematische Grundlagen“: Prof. Dr. F. Duzaar; Dr.<br />
V. Bögelein (Mathematik)<br />
VORL biologischer Teil:<br />
Organisation des bakteriellen Stoffwechsels, Einheiten der Transkriptionskontrolle:<br />
Gen, Operon, Regulon, Modulon, Sigmulon, Aktivitätsregulation,<br />
globale Analysetechniken (Genomics, Transcriptomics, Proteomics,<br />
Metabolomics, Flussanalyse).<br />
VORL mathematischer Teil:<br />
Enzymreaktionen, Michaelis-Menten Modelle, Aufstellen der Systemgleichungen;<br />
Stöchiometrische Modellierung (am stationären Modell), Methoden<br />
der Stoffflussanalyse, Kinetische Modellierung mittels metabolischer Kontrollanalyse<br />
(Einführung der wichtigsten Sensitivitätskoeffizienten, Hauptsätze der<br />
metabolischen Kontrollanalyse).<br />
UE (Anwendungsbeispiele):<br />
Aktuelle Anwendungsbeispiele (Analyse von Genom- und Transkriptomdaten)<br />
Die Studierenden<br />
• sind mit den Hauptbegriffen und den wichtigsten Analysetechniken des<br />
Lerngebietes vertraut<br />
• verfügen über Verständnis mathematischer Prozessmodellierung zur<br />
Beschreibung, Analyse und Optimierung von Bioprozessen<br />
• verfügen über einen Einblick über Methoden der metabolischen<br />
Stoffflussanalyse sowie der kinetischen Modellierung mittels metabolischer<br />
Kontrollanalyse zur Entwicklung der Stoffwechselmodelle<br />
• können die erlernten Methoden und Prozessmodelle auf Beispielen aus<br />
aktuellen Forschungsthemen selbständig anwenden<br />
• verfügen über Selbstkompetenz des analytischen Denkens.<br />
7<br />
Verwendbarkeit des<br />
Moduls<br />
B.<strong>Sc</strong>. <strong>Integrated</strong> <strong>Life</strong> <strong>Sc</strong>iences<br />
8<br />
Einpassung in<br />
Musterstudienplan<br />
4. Semester<br />
9<br />
Voraussetzungen für<br />
die Teilnahme<br />
keine<br />
10 Turnus des Angebots Jährlich im SS<br />
11 Dauer des Moduls 1 Semester<br />
Studien- und<br />
12<br />
Prüfungsleistungen<br />
VORL + UE: gemeinsame Klausur (90 Min) oder mündliche Prüfung (30 Min)<br />
13 Berechnung<br />
Modulnote<br />
Ergebnis der Prüfung<br />
14 Arbeitsaufwand Präsenzzeit: 64 h, Eigenstudium: 86 h<br />
15 Unterrichtssprache Deutsch<br />
16 Vorbereitende<br />
Literatur<br />
Informationsmaterialien zur Vor- und Nachbereitung des Stoffes werden im<br />
Internet und als Kopien zur Verfügung gestellt.<br />
Lehrbücher: B. O. Palsson, Systems Biology: Properties of Reconstructed<br />
Networks, Cambridge University Press<br />
E. Klipp, W. Liebermeister, C.Wierling und A. Kowald, Systems Biology: A<br />
Textbook, Wiley-VCH Verlag<br />
R. Heinrich und S. <strong>Sc</strong>huster, The Regulation Of Cellular Systems, Springer-<br />
Verlag<br />
34