Kärntner Schaf - Verein Kärntner Brillenschafe
Kärntner Schaf - Verein Kärntner Brillenschafe
Kärntner Schaf - Verein Kärntner Brillenschafe
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
35<br />
Tab. 12: Beobachtete (HO) und erwartete (HE) Heterozygotieraten sowie die Anzahl der Allele der Karntner<br />
Brillenschafpopulation (N=746) fu r alle 11 Mikrosatelliten-Marker<br />
Locus HO HE Anzahl Allele<br />
McM42 0,578 0,568 7<br />
TGLA53 0,830 0,816 11<br />
OarFCB20 0,812 0,811 13<br />
INRA49 0,627 0,651 6<br />
MAF65 0,723 0,733 10<br />
McM527 0,743 0,742 9<br />
OarCP49 0,794 0,777 15<br />
OarAE119 0,802 0,817 8<br />
HSC 0,834 0,844 12<br />
MAF214 0,579 0,583 13<br />
OarFCB11 0,744 0,727 7<br />
TOTAL (11 Loci) 0,733 ’ 0,097 0,734 ’ 0,095 10,09 ’ 2,95/Locus<br />
Der tatsachlich beobachtete Anteil an heterozygoten Tieren in der Population (HO) stimmte<br />
mit dem aus den Allelfrequenzen ermittelten Wert (HE) u berein. Es gibt also keinen Hinweis<br />
darauf, dass sich die Population nicht im Hardy-Weinberg-Gleichgewicht (HWG) befindet.<br />
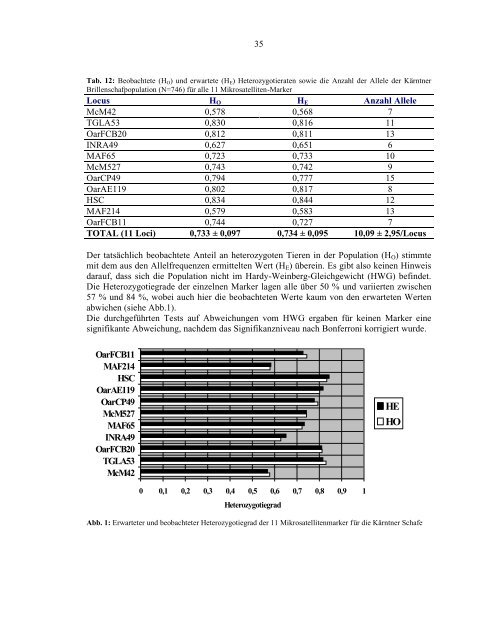
Die Heterozygotiegrade der einzelnen Marker lagen alle u ber 50 % und variierten zwischen<br />
57 % und 84 %, wobei auch hier die beobachteten Werte kaum von den erwarteten Werten<br />
abwichen (siehe Abb.1).<br />
Die durchgefu hrten Tests auf Abweichungen vom HWG ergaben fur keinen Marker eine<br />
signifikante Abweichung, nachdem das Signifikanzniveau nach Bonferroni korrigiert wurde.<br />
OarFCB11<br />
MAF214<br />
HSC<br />
OarAE119<br />
OarCP49<br />
McM527<br />
MAF65<br />
INRA49<br />
OarFCB20<br />
TGLA53<br />
McM42<br />
0 0,1 0,2 0,3 0,4 0,5 0,6 0,7 0,8 0,9 1<br />
Heterozygotiegrad<br />
Abb. 1: Erwarteter und beobachteter Heterozygotiegrad der 11 Mikrosatellitenmarker fu r die Karntner <strong>Schaf</strong>e<br />
HE<br />
HO