VILNIAUS UNIVERSITETAS - Biotechnologijos institutas
VILNIAUS UNIVERSITETAS - Biotechnologijos institutas
VILNIAUS UNIVERSITETAS - Biotechnologijos institutas
Create successful ePaper yourself
Turn your PDF publications into a flip-book with our unique Google optimized e-Paper software.
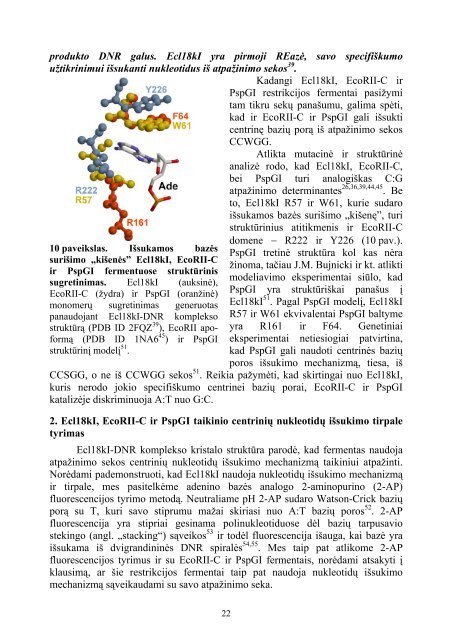
produkto DNR galus. Ecl18kI yra pirmoji REazė, savo specifiškumoužtikrinimui išsukanti nukleotidus iš atpažinimo sekos 39 .Kadangi Ecl18kI, EcoRII-C irPspGI restrikcijos fermentai pasižymitam tikru sekų panašumu, galima spėti,kad ir EcoRII-C ir PspGI gali išsukticentrinę bazių porą iš atpažinimo sekosCCWGG.Atlikta mutacinė ir struktūrinėanalizė rodo, kad Ecl18kI, EcoRII-C,bei PspGI turi analogiškas C:Gatpažinimo determinantes 26,36,39,44,45 . Beto, Ecl18kI R57 ir W61, kurie sudaroišsukamos bazės surišimo „kišenę”, turistruktūrinius atitikmenis ir EcoRII-C10 paveikslas. Išsukamos bazėssurišimo „kišenės” Ecl18kI, EcoRII-Cir PspGI fermentuose struktūrinissugretinimas. Ecl18kI (auksinė),EcoRII-C (žydra) ir PspGI (oranžinė)monomerų sugretinimas generuotaspanaudojant Ecl18kI-DNR kompleksostruktūrą (PDB ID 2FQZ 39 ), EcoRII apoformą(PDB ID 1NA6 45 ) ir PspGIstruktūrinį modelį 51 .domene − R222 ir Y226 (10 pav.).PspGI tretinė struktūra kol kas nėražinoma, tačiau J.M. Bujnicki ir kt. atliktimodeliavimo eksperimentai siūlo, kadPspGI yra struktūriškai panašus įEcl18kI 51 . Pagal PspGI modelį, Ecl18kIR57 ir W61 ekvivalentai PspGI baltymeyra R161 ir F64. Genetiniaieksperimentai netiesiogiai patvirtina,kad PspGI gali naudoti centrinės baziųporos išsukimo mechanizmą, tiesa, išCCSGG, o ne iš CCWGG sekos 51 . Reikia pažymėti, kad skirtingai nuo Ecl18kI,kuris nerodo jokio specifiškumo centrinei bazių porai, EcoRII-C ir PspGIkatalizėje diskriminuoja A:T nuo G:C.2. Ecl18kI, EcoRII-C ir PspGI taikinio centrinių nukleotidų išsukimo tirpaletyrimasEcl18kI-DNR komplekso kristalo struktūra parodė, kad fermentas naudojaatpažinimo sekos centrinių nukleotidų išsukimo mechanizmą taikiniui atpažinti.Norėdami pademonstruoti, kad Ecl18kI naudoja nukleotidų išsukimo mechanizmąir tirpale, mes pasitelkėme adenino bazės analogo 2-aminopurino (2-AP)fluorescencijos tyrimo metodą. Neutraliame pH 2-AP sudaro Watson-Crick baziųporą su T, kuri savo stiprumu mažai skiriasi nuo A:T bazių poros 52 . 2-APfluorescencija yra stipriai gesinama polinukleotiduose dėl bazių tarpusaviostekingo (angl. „stacking“) sąveikos 53 ir todėl fluorescencija išauga, kai bazė yraišsukama iš dvigrandininės DNR spiralės 54,55 . Mes taip pat atlikome 2-APfluorescencijos tyrimus ir su EcoRII-C ir PspGI fermentais, norėdami atsakyti įklausimą, ar šie restrikcijos fermentai taip pat naudoja nukleotidų išsukimomechanizmą sąveikaudami su savo atpažinimo seka.22