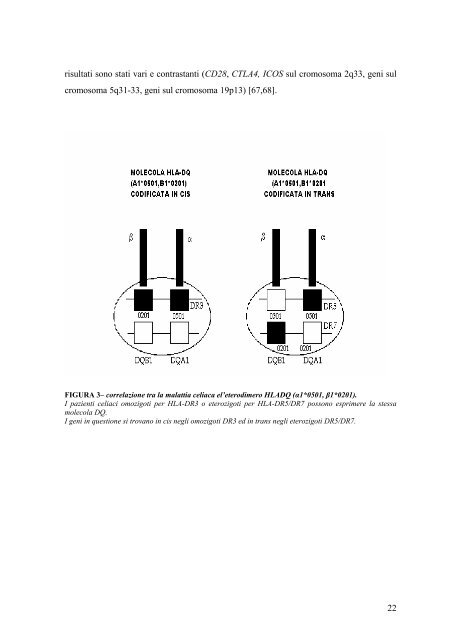
isultati sono stati vari e contrastanti (CD28, CTLA4, ICOS sul cromosoma 2q33, geni sul cromosoma 5q31-33, geni sul cromosoma 19p13) [67,68]. FIGURA 3– correlazione tra la malattia celiaca el’etero<strong>di</strong>mero HLADQ (α1*0501, β1*0201). I pazienti celiaci omozigoti per HLA-DR3 o eterozigoti per HLA-DR5/DR7 possono esprimere la stessa molecola DQ. I geni in questione si trovano in cis negli omozigoti DR3 ed in trans negli eterozigoti DR5/DR7. 22
1.5.1 GENI NON-HLA NELLA MALATTIA CELIACA Recenti stu<strong>di</strong> <strong>di</strong> screening genomico, in famiglie in cui più figli risultavano affetti da malattia celiaca, hanno evidenziato che anche altri geni, non appartenenti al sistema HLA, sono coinvolti nel conferimento della suscettibilità alla malattia stessa. L’analisi <strong>di</strong> linkage ha <strong>di</strong>mostrato che appaiono essere coinvolti geni localizzati su cromosomi <strong>di</strong>fferenti [69].Il primo possibile can<strong>di</strong>dato è stato in<strong>di</strong>viduato sul braccio corto del cromosoma 6, in posizione telomerica a 30 cM dai loci HLA [70].Altre regioni geniche che sembrano avere un legame con la malattia celiaca, sono situate suicromosomi 7 (7q31), 11 (11p11), 15 (15q26) e 22è[ Figura 3] In ogni caso, va sottolineato che i risultati ottenuti in <strong>di</strong>versi stu<strong>di</strong> sono contrastanti, per cui l’eventuale legame <strong>di</strong> queste regioni geniche con la malattia celiaca è ancora tutto da chiarire[69, 71, 72]. D’altro canto, altri lavori hanno riportato un’associazione della malattia con regioni geni che localizzate sul cromosoma 11 (11qter), questo fattore potrebbe consentire <strong>di</strong> <strong>di</strong>scernere la presentazione clinica, sintomatica o silente, della malattia [73]. Inoltre, anche un locus ,recentemente in<strong>di</strong>viduato nella porzione terminale del cromosoma 5q, sembra essere coinvolto nelle <strong>di</strong>fferenti manifestazioni cliniche della malattia [71]. Nonostante l’elevato numero <strong>di</strong> stu<strong>di</strong> condotti, ad oggi, il solo gene per cui sono stati effettuati in quantità stu<strong>di</strong> <strong>di</strong> associazione con la malattia celiaca è certamente il gene che co<strong>di</strong>fica per il CTLA-4 [74,75]. Questo gene mappa sul cromosoma 2 (2q33) e co<strong>di</strong>fica per una molecola <strong>di</strong> superficie dei linfociti T in grado <strong>di</strong> legarsi al B7 espresso dalle cellule presentanti l’antigene e <strong>di</strong> sviluppare, come conseguenza, un segnale negativo per le cellule Tin grado <strong>di</strong> me<strong>di</strong>are la loro stessa apoptosi. Tale sistema potrebbe contribuire al mantenimento della tolleranza nei confronti <strong>degli</strong> antigeni “self”. Il coinvolgimento <strong>di</strong> questa molecola nella malattia è stato ipotizzato sulla base <strong>di</strong> <strong>di</strong>versi lavori in vitro che hanno <strong>di</strong>mostrato la variazione del singolo nucleotide nel primo esone delgene, in cui la transizione dall’allele A all’allele G comporta il cambiamento <strong>di</strong> un amminoacido, da treonina ad alanina, nella molecola co<strong>di</strong>ficata. La probabilità che questa variazione allelica del gene partecipi al meccanismo della malattia, mo<strong>di</strong>ficando l’espressione <strong>di</strong> membrana della stessa, è ritenuta bassa [74]. 23
- Page 1 and 2: UNIVERSITA' DEGLI STUDI DI TRIESTE
- Page 3 and 4: LA PREVALENZA DEGLI AAA Pg. 45 4.2
- Page 5 and 6: Cap 8 DISCUSSIONE TECNICA Pg. 84 BI
- Page 7 and 8: E’ stata poi valutata la validit
- Page 9 and 10: ulbi di tulipano. Finita la guerra,
- Page 11 and 12: 1.2 EPIDEMIOLOGIA DELLA MALATTIA CE
- Page 13 and 14: FIGURA 1-l’iceberg della malattia
- Page 15 and 16: malattia in maniera sicuramente pi
- Page 17 and 18: Descrizione CLASSE 0 (TIPO NORMALE)
- Page 19 and 20: 1.4 MODIFICAZIONI DELLA MUCOSA INTE
- Page 21: 1.5 GENETICA L’interazione, ancor
- Page 25 and 26: 1.6 RISPOSTA IMMUNITARIA È ormai c
- Page 27 and 28: immuni potenzialmente dannose, form
- Page 29 and 30: B7, il CTLA-4 stesso compete progre
- Page 31 and 32: Seppure l’attivazione dei linfoci
- Page 33 and 34: 1.6.2 RISPOSTA IMMUNITARIA UMORALE
- Page 35 and 36: non ancora espressa clinicamente, c
- Page 37 and 38: Il contributo dei geni del compless
- Page 39 and 40: 3 L’ACTINA L’Actina è una prot
- Page 41 and 42: 2. permettono una parte del traspor
- Page 43 and 44: FIGURA 8-la Gelsolina si lega ad un
- Page 45 and 46: Fibronectina), nel ricambio (Collag
- Page 47 and 48: 4.3 POSSIBILE RUOLO DEGLI AAA NELLA
- Page 49 and 50: 5 OBBIETTIVI DEL LAVORO Considerand
- Page 51 and 52: FIGURA 10- esempi di test d’ immu
- Page 53 and 54: 9. Incubare con l’ anticorpo seco
- Page 55 and 56: La seconda porzione del campione bi
- Page 57 and 58: 6.6 CONFRONTO TRA PIÙ OPERATORI E
- Page 59 and 60: Seconda prova: Ipotizzando che Acti
- Page 61 and 62: saturazione è pari a 1:1000 per le
- Page 63 and 64: 2° Giorno 1. Centrifugare a 7000-8
- Page 65 and 66: 3. Duplicare la master plate in una
- Page 67 and 68: La concentrazione dell’enzima di
- Page 69 and 70: d) PRECIPITAZIONE DELLA PCR DI SEQU
- Page 71 and 72: 7 RISULTATI DELLO STUDIO 7.1 SENSIB
- Page 73 and 74:
Nella ricerca degli AAA, tra i sier
- Page 75 and 76:
7.2 CORRELAZIONE CON LA SEVERITA’
- Page 77 and 78:
7.4 CONFRONTO DELLA LETTURA TRA PI
- Page 79 and 80:
7.6 TESTARE LA POSITIVITA’DEGLI A
- Page 81 and 82:
7.8 SELEZIONI DI LIBRERIE ANTICORPA
- Page 83 and 84:
CLONE VH Gene V Score CDR3 B5 VH 1
- Page 85 and 86:
distinguere le lesioni intestinali
- Page 87 and 88:
BIBLIOGRAFIA 1. Gee S. On the coeli
- Page 89 and 90:
34 . Ferreira M, Lloyd Davies S, Bu
- Page 91 and 92:
65 Van de Wal Y, Kooy Y, Van Veelen
- Page 93 and 94:
90. Przemioslo RT, Lundin KEA, Soll
- Page 95:
124 Smith DB, Janmey PA, Herbert TJ