PDF Download - Laborwelt
PDF Download - Laborwelt
PDF Download - Laborwelt
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
B L I T Z L I C H T<br />
Größenbestimmung und<br />
Analyse von Proteinen<br />
Ein besonderes Chipdesign ermöglicht außerdem<br />
die Analyse von bis zu 10 Proteinproben<br />
im Größenbereich von 14 bis 200 kD in<br />
weniger als 30 Minuten 7 . Um vergleichbare<br />
Daten mit SDS-PAGE zu erzielen, werden<br />
etwa drei Stunden benötigt. Das bedeutet,<br />
daß mit der neuen Technologie ein signifikanter<br />
Zeitgewinn gegenüber der konventionellen<br />
Methode möglich ist. Die Lab-on-a-<br />
Chip-Technologie ermöglicht die Integration<br />
Abb. 4: Gesamt-RNA isoliert<br />
von kultivierten Jurkatzellen<br />
(100 ng/µl). Die Ergebnisse<br />
der Analyse mit dem Labon-a-Chip-System<br />
(RNA<br />
6000 LabChip ® -Kit) sind als<br />
gelähnliche Darstellung<br />
(rechts) und Elektropherogramm<br />
(links) gezeigt. Das<br />
erste Elektropherogramm<br />
zeigt intakte Gesamt-RNA,<br />
die beiden folgenden zeigen<br />
die fortschreitende RNA-<br />
Degradation durch RNase-<br />
Kontamination.<br />
und Automatisierung verschiedener manueller<br />
und zeitaufwendiger Arbeitsschritte, wie<br />
die Färbung und Entfärbung von Proteinen.<br />
Eine Vielzahl verschiedener Proben, wie<br />
Zellysate, Säulenfraktionen, Antikörper oder<br />
aufgereinigte Proteine können analysiert werden.<br />
Die Sensitivität, die mit einem auf laserinduzierter<br />
Fluoreszenz basierten Lab-on-a-<br />
Chip-System erreicht werden kann, ist vergleichbar<br />
zu einer normalen Coomassie-Färbung<br />
von Polyacrylamidgelen. Abbildung 5<br />
zeigt die Analyse einer Proteinmischung mit<br />
dem Agilent 2100 Bioanalyzer und einem 4-<br />
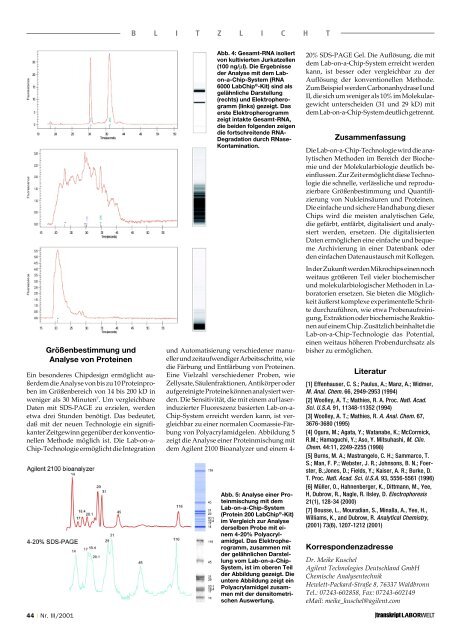
Abb. 5: Analyse einer Proteinmischung<br />
mit dem<br />
Lab-on-a-Chip-System<br />
(Protein 200 LabChip ® -Kit)<br />
im Vergleich zur Analyse<br />
derselben Probe mit einem<br />
4-20% Polyacrylamidgel.<br />
Das Elektropherogramm,<br />
zusammen mit<br />
der gelähnlichen Darstellung<br />
vom Lab-on-a-Chip-<br />
System, ist im oberen Teil<br />
der Abbildung gezeigt. Die<br />
untere Abbildung zeigt ein<br />
Polyacrylamidgel zusammen<br />
mit der densitometrischen<br />
Auswertung.<br />
20% SDS-PAGE Gel. Die Auflösung, die mit<br />
dem Lab-on-a-Chip-System erreicht werden<br />
kann, ist besser oder vergleichbar zu der<br />
Auflösung der konventionellen Methode.<br />
Zum Beispiel werden Carbonanhydrase I und<br />
II, die sich um weniger als 10% im Molekulargewicht<br />
unterscheiden (31 und 29 kD) mit<br />
dem Lab-on-a-Chip-System deutlich getrennt.<br />
Zusammenfassung<br />
Die Lab-on-a-Chip-Technologie wird die analytischen<br />
Methoden im Bereich der Biochemie<br />
und der Molekularbiologie deutlich beeinflussen.<br />
Zur Zeit ermöglicht diese Technologie<br />
die schnelle, verlässliche und reproduzierbare<br />
Größenbestimmung und Quantifizierung<br />
von Nukleinsäuren und Proteinen.<br />
Die einfache und sichere Handhabung dieser<br />
Chips wird die meisten analytischen Gele,<br />
die gefärbt, entfärbt, digitalisiert und analysiert<br />
werden, ersetzen. Die digitalisierten<br />
Daten ermöglichen eine einfache und bequeme<br />
Archivierung in einer Datenbank oder<br />
den einfachen Datenaustausch mit Kollegen.<br />
In der Zukunft werden Mikrochips einen noch<br />
weitaus größeren Teil vieler biochemischer<br />
und molekularbiologischer Methoden in Laboratorien<br />
ersetzen. Sie bieten die Möglichkeit<br />
äußerst komplexe experimentelle Schritte<br />
durchzuführen, wie etwa Probenaufreinigung,<br />
Extraktion oder biochemische Reaktionen<br />
auf einem Chip. Zusätzlich beinhaltet die<br />
Lab-on-a-Chip-Technologie das Potential,<br />
einen weitaus höheren Probendurchsatz als<br />
bisher zu ermöglichen.<br />
Literatur<br />
[1] Effenhauser, C. S.; Paulus, A.; Manz, A.; Widmer,<br />
M. Anal. Chem. 66, 2949-2953 (1994)<br />
[2] Woolley, A. T.; Mathies, R. A. Proc. Natl. Acad.<br />
Sci. U.S.A. 91, 11348-11352 (1994)<br />
[3] Woolley, A. T.; Mathies, R. A. Anal. Chem. 67,<br />
3676-3680 (1995)<br />
[4] Ogura, M.; Agata, Y.; Watanabe, K.; McCormick,<br />
R.M.; Hamaguchi, Y.; Aso, Y. Mitsuhashi, M. Clin.<br />
Chem. 44:11, 2249-2255 (1998)<br />
[5] Burns, M. A.; Mastrangelo, C. H.; Sammarco, T.<br />
S.; Man, F. P.; Webster, J. R.; Johnsons, B. N.; Foerster,<br />
B.;Jones, D.; Fields, Y.; Kaiser, A. R.; Burke, D.<br />
T. Proc. Natl. Acad. Sci. U.S.A. 93, 5556-5561 (1996)<br />
[6] Müller, O., Hahnenberger, K., Dittmann, M., Yee,<br />
H, Dubrow, R., Nagle, R. Ilsley, D. Electrophoresis<br />
21(1), 128-34 (2000)<br />
[7] Bousse, L., Mouradian, S., Minalla, A., Yee, H.,<br />
Williams, K., and Dubrow, R. Analytical Chemistry,<br />
(2001) 73(6), 1207-1212 (2001)<br />
Korrespondenzadresse<br />
Dr. Meike Kuschel<br />
Agilent Technologies Deutschland GmbH<br />
Chemische Analysentechnik<br />
Hewlett-Packard-Straße 8, 76337 Waldbronn<br />
Tel.: 07243-602858, Fax: 07243-602149<br />
eMail: meike_kuschel@agilent.com<br />
44 | Nr. III/2001 |transkript LABORWELT