View - JUWEL - Forschungszentrum Jülich
View - JUWEL - Forschungszentrum Jülich
View - JUWEL - Forschungszentrum Jülich
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
54 4 Ergebnisse<br />
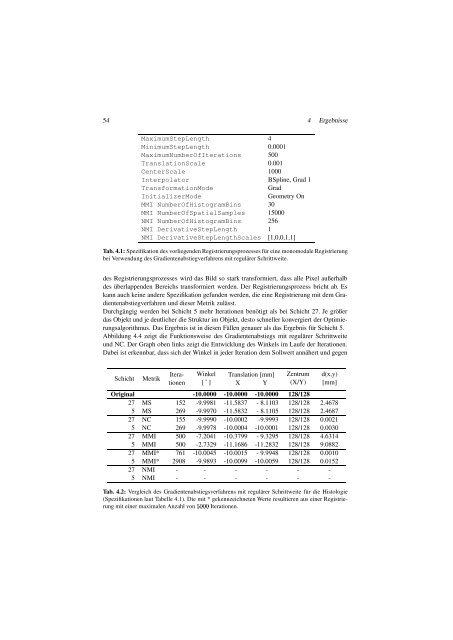
MaximumStepLength 4<br />
MinimumStepLength 0.0001<br />
MaximumNumberOfIterations 500<br />
TranslationScale 0.001<br />
CenterScale 1000<br />
Interpolator BSpline, Grad 1<br />
TransformationMode Grad<br />
InitializerMode Geometry On<br />
MMI NumberOfHistogramBins 30<br />
MMI NumberOfSpatialSamples 15000<br />
NMI NumberOfHistogramBins 256<br />
NMI DerivativeStepLength 1<br />
NMI DerivativeStepLengthScales [1,0,0,1,1]<br />
Tab. 4.1: Spezifikation des vorliegenden Registrierungsprozesses für eine monomodale Registrierung<br />
bei Verwendung des Gradientenabstiegverfahrens mit regulärer Schrittweite.<br />
des Registrierungsprozesses wird das Bild so stark transformiert, dass alle Pixel außerhalb<br />
des überlappenden Bereichs transformiert werden. Der Registrierungsprozess bricht ab. Es<br />
kann auch keine andere Spezifikation gefunden werden, die eine Registrierung mit dem Gradientenabstiegverfahren<br />
und dieser Metrik zulässt.<br />
Durchgängig werden bei Schicht 5 mehr Iterationen benötigt als bei Schicht 27. Je größer<br />
das Objekt und je deutlicher die Struktur im Objekt, desto schneller konvergiert der Optimierungsalgorithmus.<br />
Das Ergebnis ist in diesen Fällen genauer als das Ergebnis für Schicht 5.<br />
Abbildung 4.4 zeigt die Funktionsweise des Gradientenabstiegs mit regulärer Schrittweite<br />
und NC. Der Graph oben links zeigt die Entwicklung des Winkels im Laufe der Iterationen.<br />
Dabei ist erkennbar, dass sich der Winkel in jeder Iteration dem Sollwert annähert und gegen<br />
Schicht Metrik<br />
Iterationen<br />
Winkel<br />
[˚]<br />
Translation [mm]<br />
X Y<br />
Zentrum<br />
(X/Y)<br />
d(x,y)<br />
[mm]<br />
Original -10.0000 -10.0000 -10.0000 128/128<br />
27 MS 152 -9.9981 -11.5837 - 8.1103 128/128 2.4678<br />
5 MS 269 -9.9970 -11.5832 - 8.1105 128/128 2.4687<br />
27 NC 155 -9.9990 -10.0002 -9.9993 128/128 0.0021<br />
5 NC 269 -9.9978 -10.0004 -10.0001 128/128 0.0030<br />
27 MMI 500 -7.2041 -10.3799 - 9.3295 128/128 4.6314<br />
5 MMI 500 -2.7329 -11.1686 -11.2832 128/128 9.0882<br />
27 MMI* 761 -10.0045 -10.0015 - 9.9948 128/128 0.0010<br />
5 MMI* 2908 -9.9893 -10.0099 -10.0059 128/128 0.0152<br />
27 NMI - - - - - -<br />
5 NMI - - - - - -<br />
Tab. 4.2: Vergleich des Gradientenabstiegsverfahrens mit regulärer Schrittweite für die Histologie<br />
(Spezifikationen laut Tabelle 4.1). Die mit * gekennzeichneten Werte resultieren aus einer Registrie-<br />
<br />
rung mit <br />
einer maximalen Anzahl von Iterationen.