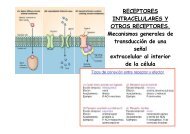
Drosophila - Severo Ochoa - Universidad Autónoma de Madrid
Drosophila - Severo Ochoa - Universidad Autónoma de Madrid
Drosophila - Severo Ochoa - Universidad Autónoma de Madrid
Create successful ePaper yourself
Turn your PDF publications into a flip-book with our unique Google optimized e-Paper software.
Jefe <strong>de</strong> Línea /<br />
Group Lea<strong>de</strong>r:<br />
Mauricio García Mateu<br />
Estabilidad e ingeniería<br />
<strong>de</strong> proteínas víricas<br />
Stability and engineering<br />
of viral proteins<br />
C6<br />
Publicaciones<br />
Publications<br />
Resumen <strong>de</strong> investigación<br />
Research summary<br />
<strong>de</strong>l Álamo, M. and Mateu, M.G. (2005). Electrostatic repulsion,<br />
compensatory mutations, and long-range non-additive effects at the<br />
dimerization interface of the HIV capsid protein.<br />
J. Mol. Biol. 345, 893-906.<br />
Postdoctorales /<br />
Fellows:<br />
Roberto Mateo Fernán<strong>de</strong>z<br />
Becarios Predoctorales /<br />
Predoctoral Fellows:<br />
Marta <strong>de</strong>l Álamo Camuñas<br />
Aura Carreira Moreno<br />
Eva Luna García<br />
Milagros Castellanos Molina<br />
Verónica Rincón Forero<br />
Rebeca Bocanegra Rojo<br />
Inmunología y Virología Immunology and Virology<br />
Nuestra investigación se centra en el estudio <strong>de</strong> los<br />
<strong>de</strong>terminantes moleculares <strong>de</strong>l ensamblaje, estabilidad,<br />
propieda<strong>de</strong>s y funciones biológicas <strong>de</strong> virus, para el diseño<br />
<strong>de</strong> nuevas vacunas y antivirales. Utilizamos técnicas <strong>de</strong><br />
biología molecular y celular, bioquímica y biofísica. Entre<br />
nuestros colaboradores se cuentan J.L.Neira (CBMC),<br />
Pedro J. <strong>de</strong> Pablo (UAM), J.M.Almendral (CBMSO), G.Rivas<br />
(CIB) y P.L.Davies (Queen´s University, Canada).<br />
Ingeniería <strong>de</strong> virus <strong>de</strong> mayor estabilidad, y dinámica <strong>de</strong><br />
mutaciones compensatorias en la cápsida <strong>de</strong>l virus <strong>de</strong> la<br />
fiebre aftosa. Hemos introducido nuevos puentes disulfuro<br />
o salinos entre subunida<strong>de</strong>s <strong>de</strong> la cápsida, y se han<br />
obtenido dos mutantes <strong>de</strong> termoestabilidad incrementada,<br />
<strong>de</strong> interés para el <strong>de</strong>sarrollo <strong>de</strong> vacunas más estables, que<br />
continúan siendo analizados. Hemos encontrado a<strong>de</strong>más<br />
en la cápsida una sorpren<strong>de</strong>nte dinámica <strong>de</strong> mutaciones<br />
con efectos compensatorios sobre la eficacia biológica<br />
durante la evolución <strong>de</strong> este virus.<br />
Participación <strong>de</strong>l ácido nucleico genómico y <strong>de</strong> cavida<strong>de</strong>s <strong>de</strong><br />
la cápsida <strong>de</strong>l virus diminuto <strong>de</strong>l ratón en las propieda<strong>de</strong>s<br />
conformacionales, térmicas y mecánicas <strong>de</strong>l virión. Hemos<br />
encontrado que la conservación <strong>de</strong>l tamaño y la forma <strong>de</strong><br />
pequeñas cavida<strong>de</strong>s presentes en la cápsida pue<strong>de</strong> ser<br />
necesaria para la flexibilidad <strong>de</strong> la misma a través <strong>de</strong> un<br />
cambio conformacional que se requiere para la infección.<br />
A<strong>de</strong>más, hemos <strong>de</strong>mostrado que el DNA genómico es<br />
aprovechado como material para la arquitectura <strong>de</strong>l virión, y<br />
refuerza térmica y mecánicamente la cápsida <strong>de</strong> un modo<br />
compatible con la flexibilidad requerida para la infección.<br />
Efectos <strong>de</strong> la aglomeración molecular sobre el ensamblaje<br />
<strong>de</strong> la cápsida <strong>de</strong>l virus <strong>de</strong> la inmuno<strong>de</strong>ficiencia humana, y<br />
análisis <strong>de</strong> inhibidores <strong>de</strong> ensamblaje. Hemos puesto a<br />
punto un sistema <strong>de</strong> ensamblaje in vitro <strong>de</strong> la cápsida que<br />
ocurre en condiciones fisiológicas <strong>de</strong> fuerza iónica y<br />
concentración <strong>de</strong> proteína; estamos ensayando a<strong>de</strong>más el<br />
efecto inhibidor sobre el ensamblaje <strong>de</strong> la cápsida, <strong>de</strong><br />
variantes proteicos y peptídicos. Estos estudios son<br />
importantes para el <strong>de</strong>sarrollo <strong>de</strong> nuevos fármacos anti-VIH.<br />
Research in our group is focused on the molecular<br />
<strong>de</strong>terminants of assembly, stability, properties and biological<br />
functions of viral capsids, for the <strong>de</strong>sign of vaccines and<br />
antiviral agents. The techniques we use involve those of<br />
molecular and cell biology, biophysics and biochemistry.<br />
Our collaborators inclu<strong>de</strong> J.L.Neira (CBMC), Pedro J. <strong>de</strong><br />
Pablo (UAM), J.M.Almendral (CBMSO), G. Rivas (CIB) and<br />
P.L.Davies (Queen´s University, Canada).<br />
Engineering viruses with increased thermostability, and<br />
dynamics od compensatory mutations in the foot-and-mouth<br />
disease virus capsid. We have introduced intersubunit<br />
disulfi<strong>de</strong> bonds or salt bridges in the virus capsid. Two<br />
mutants show increased thermostability and are potentialy<br />
useful for the <strong>de</strong>velopment of thermostable vaccines. We<br />
have also found in the capsid a surprising dynamics of<br />
<strong>de</strong>terministic mutations that exert compensatory effects on<br />
the biological fitness during the evolution of this virus.<br />
Participation of the genomic nucleic acid and capsid cavities<br />
in the conformational, thermal and mechanical properties of<br />
the minute virus of mice. We have found evi<strong>de</strong>nce that<br />
conservation of the size and shape of small cavities naturally<br />
found in the capsid is required for flexibility and the<br />
occurrence of a capsid conformational change nee<strong>de</strong>d for<br />
infectivity. In addition, we have shown that the genomic DNA<br />
exerts an architectural role by thermally and mechanically<br />
reinforcing the capsid. Such reinforcement is compatible<br />
with the local flexibility that may be required for the abovementioned<br />
conformational change to occur.<br />
Effects of molecular crowding on the assembly of the human<br />
immuno<strong>de</strong>ficiency virus capsid, and analyses of assembly<br />
inhibitors. We have <strong>de</strong>veloped an in vitro system for the<br />
assembly of the capsid un<strong>de</strong>r physiological conditions of<br />
ionic strength and effective protein concentration. We are<br />
also analysing the inhibitory effect of pepti<strong>de</strong> and protein<br />
variants on capsid assembly. These studies are important<br />
for the <strong>de</strong>velopment of new anti-HIV compounds.<br />
Reguera, J., Grueso, E., Carreira, A., Sánchez-Martínez, C.,<br />
Almendral, J.M. and Mateu, M.G. (2005). Functional relevance of<br />
amino acid residues involved in interactions with or<strong>de</strong>red nucleic acid<br />
in a spherical virus. J. Biol. Chem. 280, 17969-17977.<br />
Lidón-Moya, M.C., Barrera, F.N., Bueno, M., Pérez-Jiménez, R.,<br />
Sancho, J., Mateu, M.G. and Neira, J.L. (2005). An extensive<br />
thermodynamic characterization of the dimerization domain<br />
of the HIV-1 capsid protein. Protein Sci. 14, 2387-2404.<br />
Del Álamo, M., Rivas, G. and Mateu, M.G. (2005). Effect of<br />
macromolecular crowding agents on human immuno<strong>de</strong>ficiency virus<br />
type-1 capsid protein assembly in vitro. J.Virol. 79, 14271-14281.<br />
Riolobos, L., Reguera, J., Mateu, M.G. and Almendral, J.M. (2006).<br />
Nuclear transport of trimeric assembly intermediates exerts a<br />
morphogenetic control on the icosahedral parvovirus capsid.<br />
J. Mol. Biol. 357, 1026-1038.<br />
Carreira, A. and Mateu, M.G. (2006). Structural tolerance versus<br />
functional intolerance to mutation of amino acid residues surrounding<br />
cavities in a parvovirus capsid. J. Mol. Biol. 360, 1081-1093.<br />
Carrasco, C., Carreira, A., Schaap, I.A.T., Serena, P.A., Gómez-<br />
Herrero, J., Mateu, M.G. and <strong>de</strong> Pablo, P.J. (2006). DNA-mediated<br />
anisotropic mechanical reinforcement of a virus.<br />
Proc. Natl. Acad. Sci. USA 103, 13706-13711.<br />
Tesis doctorales<br />
Doctoral Theses<br />
Marta <strong>de</strong>l Álamo Camuñas. (2005). Disección termodinámica <strong>de</strong> una<br />
interfase proteína-proteína implicada en la formación <strong>de</strong> la cápsida<br />
<strong>de</strong>l virus <strong>de</strong> la inmuno<strong>de</strong>ficiencia humana.<br />
<strong>Universidad</strong> Autónoma <strong>de</strong> <strong>Madrid</strong>.<br />
Aura Carreira Moreno. (2005). Estudio <strong>de</strong>l <strong>de</strong>sensamblaje in vitro<br />
y análisis estructura-función <strong>de</strong> cavida<strong>de</strong>s <strong>de</strong> la cápsida <strong>de</strong>l virus<br />
diminuto <strong>de</strong>l ratón.<br />
<strong>Universidad</strong> Autónoma <strong>de</strong> <strong>Madrid</strong>.<br />
Figura 1<br />
Figura 1. Estructura <strong>de</strong> la cápsida <strong>de</strong>l virus diminuto <strong>de</strong>l ratón. Se indican los residuos en las interfases entre subunida<strong>de</strong>s que son críticos para el ensamblaje (violeta) y<br />
los implicados en un cambio conformacional que es necesario para la infectividad (amarillo).<br />
Estos últimos residuos se localizan cerca <strong>de</strong> cavida<strong>de</strong>s <strong>de</strong> la cápsida; una <strong>de</strong> éstas se muestra en <strong>de</strong>talle en la Fig.2 (figura <strong>de</strong> D.Abia y A.R.Ortiz).<br />
Figura 2<br />
Figure 1. Structure of the capsid of the minute virus of mice. Those residues at the intersubunit interfaces that are critical for capsid assembly (violet) or involved<br />
in a conformational change nee<strong>de</strong>d for infectivity (yellow) are indicated. One of these residues is shown in <strong>de</strong>tail in Fig.2 (figure by D.Abia and A.R.Ortiz).<br />
CBM 2005/2006<br />
66<br />
Figura 2. Esquema <strong>de</strong> una cavidad en la cápsida <strong>de</strong>l virus diminuto <strong>de</strong>l ratón.<br />
Los residuos que ro<strong>de</strong>an la cavidad se representan en diferentes colores, y el contorno <strong>de</strong> la cavidad se representa en blanco.<br />
Figure 2. Scheme of a cavity in the capsid of the minute virus of mice. The residues that surround the cavity are shown in different colours,<br />
and the cavity contour is represented in white.<br />
67