Apri file allegato (risultatiricerca.pdf) - Cra
Apri file allegato (risultatiricerca.pdf) - Cra
Apri file allegato (risultatiricerca.pdf) - Cra
Create successful ePaper yourself
Turn your PDF publications into a flip-book with our unique Google optimized e-Paper software.
Tipizzazione molecolare di lieviti saccharomyces di interesse enologico<br />
PREMESSA<br />
L’identificazione della composizione della flora dei lieviti all’interno del mosto si rende necessaria<br />
per il miglioramento delle caratteristiche qualitative del vino. Tradizionalmente, l’identificazione e<br />
la caratterizzazione di specie di lievito e di specifici ceppi all’interno della stessa specie si basavano<br />
sull’analisi di tratti morfologici e soprattutto sulle loro caratteristiche fisiologiche specifiche.<br />
Queste caratteristiche sono però fortemente influenzate dalle condizioni di coltura e possono produrre<br />
risultati incerti e talvolta non corretti.<br />
Recentemente sono state sviluppate numerose tecniche molecolari innovative che costituiscono validi<br />
metodi alternativi in grado di mettere in risalto la diversità genetica dei ceppi (Kellis et al.,2003; Richard<br />
e Dujon 2006; Schuller et al., 2004). In tale ambito, l’amplificazione di sequenze di DNA specifiche<br />
tramite PCR è divenuto un metodo molecolare largamente utilizzato in quanto altamente riproducibile.<br />
A questa tecnica sono stati successivamente affiancati metodi di analisi più sensibili quali la RAPD<br />
(Random Amplification of Polymorphic DNA) (Quesada e Cenis, 1995), la RFLP (Restriction Fragment<br />
Length Polymorphism) (Guillamon et al.., 1998) e la AFLP (Amplified Fragment Length Polymorphism)<br />
(Azumi and Goto-Yamamoto, 2001).<br />
Negli anni più recenti tali tecniche sono state impiegate per lo studio della variabilità di sequenza di<br />
alcune regioni del genoma, soprattutto di quelle in cui sono localizzati i geni che codificano per gli RNA<br />
ribosomiali (rRNA). In particolare, sono stati analizzati i domini D1/D2 dei geni codificanti per il 26S<br />
rRNA (Laitila et al.., 2006) e le regioni interne spaziatrici trascritte (ITS) del cluster dei geni ribosomiali<br />
(26S, 18S e 5S) (Guillamon et al.., 1998; Granchi et al.., 1999; Esteve-Zarzoso et al.., 1999) .<br />
L’attenzione e stata rivolta anche allo studio del polimorfismo di singoli geni specifici conservati nei<br />
lieviti quali il 5S, Actina e Metionina 2 (Daniel e Meyer,2003; Antunovics et al.., 2005).<br />
Ad onor del vero, nessuno di questi metodi fino ad oggi si è rivelato in grado di garantire da solo risultati<br />
che consentano l’identificazione certa di una specie o di un ceppo di lievito.<br />
A queste tecniche si possono affiancare altre metodiche che però presentano lo svantaggio di essere<br />
più complesse e che possono richiedere costose apparecchiature, quali l’analisi del cariotipo mediante<br />
l’impiego della tecnica PFGE (Pulsed-Field Gel Electrophoresis) (Cardinali e Martini, 1994). Va<br />
menzionata infine l’analisi del DNA mitocondriale (mtDNA) che presenta una variabilità genetica<br />
intrinseca maggiore rispetto al DNA nucleare.<br />
Rimane pertanto importante identificare nuove regioni variabili del genoma che possano consentire<br />
l’identificazione certa dei ceppi a livello della loro specie e, possibilmente, mettere in evidenza le<br />
differenze all’interno della stessa specie.<br />
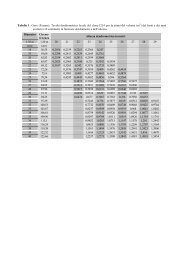
A tale scopo, si è cercato di mettere a punto un sistema discriminante basato sull’amplificazione dei geni<br />
ADH, presenti in tutti i lieviti, che codificano per attività alcool deidrogenasiche.<br />
I ceppi di lievito analizzati, isolati prevalentemente dall’uva, dai mosti e dal vino, sono stati forniti<br />
dall’Istituto Sperimentale per l’Enologia di Velletri (ora CRA-Unità di ricerca per le produzioni enologiche<br />
dell’Italia centrale Velletri), e dal Dipartimento di Biologia Vegetale dell’Università di Perugia.<br />
44