Einfluss von Mutationen auf die NS2/3-Prozessierung und die ...
Einfluss von Mutationen auf die NS2/3-Prozessierung und die ...
Einfluss von Mutationen auf die NS2/3-Prozessierung und die ...
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
ERGEBNISSE<br />
mehr RNA als das vergleichbare Wildtypvirus. Beim Vergleich des NCP7 mit<br />
der entsprechenden Mutante fällt <strong>auf</strong>, dass hier das Wildtypvirus deutlich mehr<br />
RNA bildet.<br />
In einer zweiten PCR werden zur Kontrolle ebenfalls 2 µl des RT-<br />
Reaktionsansatzes eingesetzt. Hier wird jedoch das für <strong>die</strong> GAPDH spezifische<br />
Primerpaar verwendet. Diese Kontrollreaktion <strong>die</strong>nt lediglich dem Nachweis,<br />
dass jeweils <strong>die</strong> gleiche Menge an RNA eingesetzt wurde. Aufgr<strong>und</strong> der<br />
gleichstarken Bandenausbildung der verschiedenen Reaktionen (Abb. 23) kann<br />
da<strong>von</strong> ausgegangen werden, dass <strong>die</strong> eingesetzte Menge an RT-Template<br />
stets konstant war.<br />
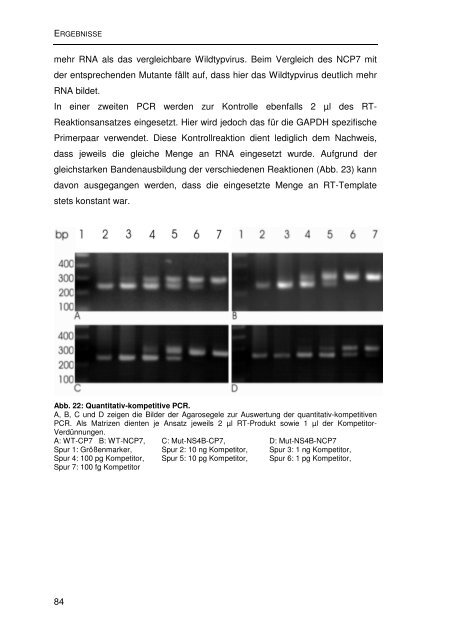
Abb. 22: Quantitativ-kompetitive PCR.<br />
A, B, C <strong>und</strong> D zeigen <strong>die</strong> Bilder der Agarosegele zur Auswertung der quantitativ-kompetitiven<br />
PCR. Als Matrizen <strong>die</strong>nten je Ansatz jeweils 2 µl RT-Produkt sowie 1 µl der Kompetitor-<br />
Verdünnungen.<br />
A: WT-CP7 B: WT-NCP7, C: Mut-NS4B-CP7, D: Mut-NS4B-NCP7<br />
Spur 1: Größenmarker, Spur 2: 10 ng Kompetitor, Spur 3: 1 ng Kompetitor,<br />
Spur 4: 100 pg Kompetitor, Spur 5: 10 pg Kompetitor, Spur 6: 1 pg Kompetitor,<br />
Spur 7: 100 fg Kompetitor<br />
84