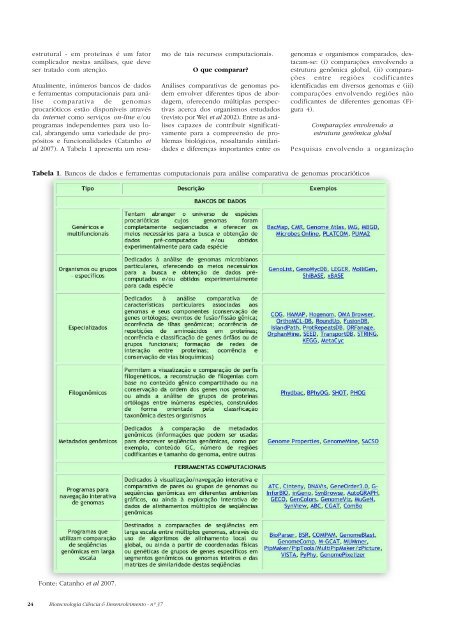
estrutural - em proteínas é um fatorcomplicador nestas análises, que deveser tratado com atenção.Atualmente, inúmeros bancos de dadose ferramentas computacionais para análisecomparativa de genomasprocarióticos estão disponíveis atravésda internet como serviços on-line e/ouprogramas independentes para uso local,abrangendo uma variedade de propósitose funcionalidades (Catanho etal 2007). A Tabela 1 apresenta um resumode tais recursos computacionais.O que comparar?Análises comparativas de genomas podemenvolver diferentes tipos de abordagem,oferecendo múltiplas perspectivasacerca dos organismos estudados(revisto por Wei et al 2002). Entre as análisescapazes de contribuir significativamentepara a compreensão de problemasbiológicos, ressaltando similaridadese diferenças importantes entre osgenomas e organismos comparados, destacam-se:(i) comparações envolvendo aestrutura genômica global, (ii) comparaçõesentre regiões codificantesidentificadas em diversos genomas e (iii)comparações envolvendo regiões nãocodificantes de diferentes genomas (Figura4).Comparações envolvendo aestrutura genômica globalPesquisas envolvendo a organizaçãoTabela 1. Bancos de dados e ferramentas computacionais para análise comparativa de genomas procarióticosFonte: Catanho et al 2007.24 <strong>Biotecnologia</strong> Ciência & <strong>Desenvolvimento</strong> - nº <strong>37</strong>
(tais como genes, operons, grupos[clusters] gênicos, elementos de inserção,repetições etc.), determinando, porexemplo, a distribuição assimétrica dosgenes entre as fitas de DNA (chamadasleading e lagging) e em relação aospontos de origem e término dareplicação, a diferença de composiçãode bases entre as fitas leading e lagginge a formação de gradientes ao longoda cadeia de DNA, representados pordesvios na composição de bases e nastaxas mutacionais nas proximidades doponto de término da replicação (revistopor Rocha 2004a).Comparações entreregiões codificantesFigura 4. Análise comparativa de genomas. O esquema representa genericamenteos três níveis de abordagem da genômica comparativa de procariotos(e também de eucariotos) e algumas análises comumente realizadas.Uma vez que seqüências genômicas completas são obtidas atravésdo seqüenciamento em larga escala dos genomas de diferentes espécies,análises comparativas envolvendo (i) a estrutura genômica, (ii) as regiõescodificantes e (iii) as regiões não codificantes entre estes genomas podemser realizadas, oferecendo múltiplas perspectivas acerca dos organismosestudados. Neste painel, segmentos genômicos sintênicos entre os genomashipotéticos A, B e C são representados por barras horizontais decores idênticas (Estrutura genômica). De maneira similar, regiões codificantesortólogas (entre diferentes genomas) e parálogas (dentro de ummesmo genoma) são representadas por círculos de cores idênticas (Regiõescodificantes). A presença de elementos regulatórios ou de pseudogenes,dentro de regiões não codificantes, conservados entre os genomashipotéticos A, B e C são representadas por círculos pontilhados (Regiõesnão codificantes)cromossômica de procariotos receberampouca atenção no passado em relaçãoa estudos similares em eucariotos.Este quadro vem se modificando, graçasaos resultados obtidos com oseqüenciamento em larga escala dosgenomas de inúmeros representantesdestes seres vivos (Rocha 2004a). Comparaçõesenvolvendo a estrutura globalde genomas procarióticos completamenteseqüenciados possibilitam a obtençãode informações sobre a organizaçãoe evolução destes genomas e tambéma identificação de característicasúnicas nos mesmos, permitindo revelare compreender as forças atuantes nestesprocessos, muitas vezes relacionadasa atividades celulares fundamentaiscomo a expressão gênica coordenada,a replicação cromossômica e adivisão celular (Rocha 2004b). Estas pesquisasincluem tipicamente (i) a descriçãode características estruturais doDNA (como por exemplo, tamanho dogenoma, conteúdo GC[guanina+citosina] global, variações doconteúdo GC ao longo do genoma, freqüênciasde mono- e oligonucleotídeos,desvios na utilização decódons e de aminoácidos, entre outros)(ii) a análise do conteúdo e distribuiçãode repetições e outras regiões debaixa complexidade, (iii) a identificaçãode regiões sintênicas conservadase de eventos de rearranjo genômicoe (iv) a análise de regiões limítrofes entreregiões sintênicas vizinhas (breakpoints).Através de análises como estas foi possível,por exemplo, demonstrar que oprocesso de replicação cromossômicaé um dos principais responsáveis pelaorganização e pela inter-relação entremuitos dos elementos que constituema organização genômica em procariotosOutra abordagem comumente empregadapara comparar os genomas de diferentesorganismos procarióticos consideraestes seres (de forma alegórica)como sendo sacos de genes, orientandoas análises somente para o conteúdocodificante de seus genomas: genes eseus produtos (proteínas especificamente).As possibilidades oferecidas poreste tipo de abordagem são inúmeras,incluindo a aquisição de informaçõessobre a organização e evolução destesgenomas, a identificação de característicasúnicas nos mesmos, aplicação diretaem processos de reconstrução metabólicae em processos de predição eclassificação funcional de genes(Galperin & Koonin 2000; Stein 2001;Gabaldon & Huynen 2004; Francke etal 2005; Lee et al 2007; Abby & Daubin2007; Skrabanek et al 2008). Tais estudosabrangem normalmente (i) a identificaçãode regiões codificantes, (ii) acomparação dos conteúdos gênico eprotéico, (iii) a identificação/análise daconservação de famílias de genesortólogos e parálogos entre os genomascomparados, (iv) a análise da conservaçãode grupos gênicos e da conservaçãoda ordem (localização) dos genesentre as diferentes espécies estudadas,(v) a identificação/análise de eventosde fusão/fissão gênica e da ocorrênciade ligação funcional entre genes nasespécies analisadas. Recentemente, análisesdeste tipo levaram a uma das maisimportantes descobertas da eragenômica. Através de comparações entreo repertório de genes codificadospelos genomas de múltiplos isoladospatogênicos de bactérias da espécieStreptococcus agalactiae (principal causade infecção neonatal em humanos),Tettelin e colaboradores (2005) demonstraramque esta espécie pode ser descritapor um pan-genoma, constituídopor um conjunto de genes compartilhadospor todos os isolados (genomacentral) e por um segundo conjunto de<strong>Biotecnologia</strong> Ciência & <strong>Desenvolvimento</strong> - nº <strong>37</strong> 25
- Page 1 and 2: Biotecnologia Ciência & Desenvolvi
- Page 3 and 4: BC&D - Como o senhor avalia aposiç
- Page 5 and 6: dicamentos.Os anticorpos monoclonai
- Page 8 and 9: PesquisaLUCIFERASES DE VAGALUMESPes
- Page 10 and 11: ger & McElroy, 1965; Hastings,1995)
- Page 12 and 13: ciferases de elaterídeos e fengod
- Page 14 and 15: utilizados como marcadores sensíve
- Page 16: 5,5-dimethyloxyluciferin. JACS 124:
- Page 19 and 20: Rev. Bras. Entom. 33: 359-366..Vivi
- Page 21 and 22: vimento de pesquisas científicas (
- Page 23: ubíquos) é inferior a 100, envolv
- Page 27 and 28: evolution of mycobacterialpathogeni
- Page 29 and 30: GLOSSÁRIOAlgoritmo. Procedimento o
- Page 31 and 32: oócito e melhora o posterior desen
- Page 33 and 34: Figura 7: Ilustração de resultado
- Page 35 and 36: 10. COELHO, L. A.; ESPER, C. R.;GAR
- Page 37 and 38: - permitir a rápida liberação do
- Page 39 and 40: de crescimento, quatro grupos de mi
- Page 41 and 42: skovia xanthineolytica LL-G109 (And
- Page 43 and 44: Tabela 1. Purificação da β-1,3 g
- Page 45 and 46: depende em parte, da venda dos subp
- Page 47 and 48: tipo poro-canal-G1pF atua por sensi
- Page 49 and 50: eutilização de células imobiliza
- Page 51 and 52: ANP - AGENCIA NACIONAL DE PETROLEO
- Page 53 and 54: inantes, incluindo eritropoetinas,
- Page 55 and 56: proteínas terapêuticas como, por
- Page 57 and 58: capsuladas, a redução de efeitos
- Page 59 and 60: Zhang W, Rong Z, Chen H, Jiang X.Br
- Page 61 and 62: FIGURA 1. Estrutura “Markush”Ma
- Page 63 and 64: Figura 2, todos os compostos origin
- Page 65 and 66: Figura 2. O filo Porifera é dividi
- Page 67 and 68: Figura 4. Microscopia eletrônica d
- Page 69 and 70: plication of genomics to uncultured
- Page 71 and 72: viabilidade celular (1) a técnica
- Page 73 and 74: Gráfico 02: Média das viabilidade
- Page 75 and 76:
Tabela 04: Análise das médias de
- Page 77 and 78:
icus blazei. Atualmente é também
- Page 79:
5. Agaricus sylvaticus é sinônimo