Untersuchung des genetischen Schadens in peripheren ...
Untersuchung des genetischen Schadens in peripheren ...
Untersuchung des genetischen Schadens in peripheren ...
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
MR bzw. rel.DNA-Schaden (%)<br />
35<br />
30<br />
25<br />
20<br />
15<br />
10<br />
5<br />
0<br />
Pat.2 Pat.5 Pat.7<br />
MR-MW1 MR-MW2 rDNA-S-MW1 rDNA-S-MW2<br />
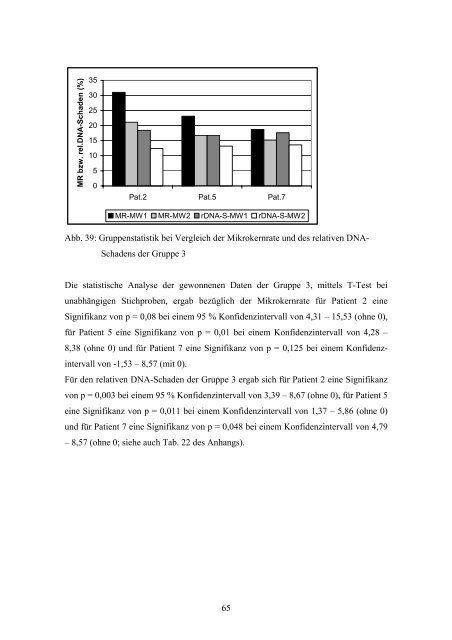
Abb. 39: Gruppenstatistik bei Vergleich der Mikrokernrate und <strong>des</strong> relativen DNA-<br />
<strong>Schadens</strong> der Gruppe 3<br />
Die statistische Analyse der gewonnenen Daten der Gruppe 3, mittels T-Test bei<br />
unabhängigen Stichproben, ergab bezüglich der Mikrokernrate für Patient 2 e<strong>in</strong>e<br />
Signifikanz von p = 0,08 bei e<strong>in</strong>em 95 % Konfidenz<strong>in</strong>tervall von 4,31 – 15,53 (ohne 0),<br />
für Patient 5 e<strong>in</strong>e Signifikanz von p = 0,01 bei e<strong>in</strong>em Konfidenz<strong>in</strong>tervall von 4,28 –<br />
8,38 (ohne 0) und für Patient 7 e<strong>in</strong>e Signifikanz von p = 0,125 bei e<strong>in</strong>em Konfidenz<strong>in</strong>tervall<br />
von -1,53 – 8,57 (mit 0).<br />
Für den relativen DNA-Schaden der Gruppe 3 ergab sich für Patient 2 e<strong>in</strong>e Signifikanz<br />
von p = 0,003 bei e<strong>in</strong>em 95 % Konfidenz<strong>in</strong>tervall von 3,39 – 8,67 (ohne 0), für Patient 5<br />
e<strong>in</strong>e Signifikanz von p = 0,011 bei e<strong>in</strong>em Konfidenz<strong>in</strong>tervall von 1,37 – 5,86 (ohne 0)<br />
und für Patient 7 e<strong>in</strong>e Signifikanz von p = 0,048 bei e<strong>in</strong>em Konfidenz<strong>in</strong>tervall von 4,79<br />
– 8,57 (ohne 0; siehe auch Tab. 22 <strong>des</strong> Anhangs).<br />
65