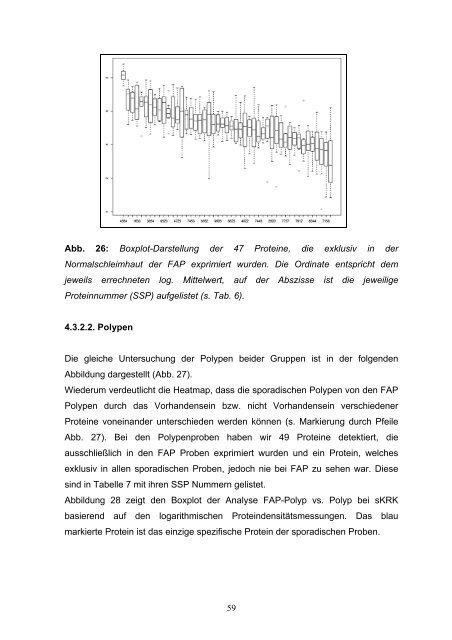
Von besonderem Interesse waren Proteine, die in sämtlichen Normalschleimhaut- FAP Proben vorhanden waren <strong>und</strong> in keinem der sporadischen Normalproben nachgewiesen wurden, sowie umgekehrt. Sie sind in Abb. 25 mit Pfeilen markiert. Um nun diejenigen Proteine zu definieren, die exklusiv in einer Gruppe von Normalgewebeproben (FAP vs. sKRK) vorhanden waren (potentielle Markerproteine), wurde das Vorhandensein bzw. nicht Vorhandensein eines jeden Proteins mittels Fischer`s Exact Test errechnet <strong>und</strong> in eine Tabellenform (Tab.6) gebracht. Hieraus ergab sich, dass 47 Proteine in der normalen Schleimhaut der FAP immer vorhanden waren <strong>und</strong> nie in der normalen Schleimhaut der sporadischen Proben detektiert wurden. Abbildung 26 zeigt den Boxplot der logarithmisierten Werte für die 47 Proteine, sortiert nach Mittelwert (MW). Protein MW Varkoef. Protein Mean Varkoef Protein Mean Varkoef 4564 8,14 0,05 7453 5,6 0,14 7443 4,79 0,19 4817 6,72 0,14 7558 5,39 0,14 3768 4,71 0,1 8634 6,57 0,11 3730 5,38 0,15 4815 4,68 0,28 1633 6,4 0,17 6562 5,36 0,15 2620 4,63 0,25 3879 6,37 0,13 4830 5,36 0,32 7325 4,32 0,2 3881 6,36 0,14 5829 5,29 0,19 5708 4,31 0,13 3854 6,29 0,18 9606 5,27 0,1 7612 4,14 0,2 3878 6,19 0,1 3736 5,23 0,1 7458 4,12 0,27 5832 6,15 0,13 8632 5,14 0,12 3322 4,02 0,25 8523 6,14 0,18 8625 5,1 0,08 6344 3,92 0,19 8627 5,88 0,12 8644 5,02 0,19 5448 3,9 0,31 6756 5,88 0,2 4827 4,96 0,16 5122 3,33 0,45 4725 5,79 0,14 4622 4,89 0,3 7158 3,32 0,37 4833 5,78 0,28 5529 4,89 0,16 8425 3,06 0,59 5630 5,62 0,13 3722 4,86 0,29 Tab.6: In der ersten Spalte findet sich die Proteinnummer (SSP Nummer), es folgt die durchschnittliche log. Densitätsmessung <strong>des</strong> spezifischen Proteins <strong>und</strong> der jeweilige Korrelationskoeffizient. Alle diese Proteine wurden exklusiv in der normalen Mukosa der FAP Proben definiert. 58
Abb. 26: Boxplot-Darstellung der 47 Proteine, die exklusiv in der Normalschleimhaut der FAP exprimiert wurden. Die Ordinate entspricht dem jeweils errechneten log. Mittelwert, auf der Abszisse ist die jeweilige Proteinnummer (SSP) aufgelistet (s. Tab. 6). 4.3.2.2. Polypen Die gleiche Untersuchung der Polypen beider Gruppen ist in der folgenden Abbildung dargestellt (Abb. 27). Wiederum verdeutlicht die Heatmap, dass die sporadischen Polypen von den FAP Polypen durch das Vorhandensein bzw. nicht Vorhandensein verschiedener Proteine voneinander unterschieden werden können (s. Markierung durch Pfeile Abb. 27). Bei den Polypenproben haben wir 49 Proteine detektiert, die ausschließlich in den FAP Proben exprimiert wurden <strong>und</strong> ein Protein, welches exklusiv in allen sporadischen Proben, jedoch nie bei FAP zu sehen war. Diese sind in Tabelle 7 mit ihren SSP Nummern gelistet. Abbildung 28 zeigt den Boxplot der Analyse FAP-Polyp vs. Polyp bei sKRK basierend auf den logarithmischen Proteindensitätsmessungen. Das blau markierte Protein ist das einzige spezifische Protein der sporadischen Proben. 59
- Seite 1 und 2:
Aus der Klinik für Chirurgie der U
- Seite 3 und 4:
Erklärung: Ich erkläre hiermit, d
- Seite 5 und 6:
Inhaltsverzeichnis Seite 1. Einleit
- Seite 7 und 8: 4.3.2.3. Karzinom 62 5. Diskussion
- Seite 9 und 10: Tabellenverzeichnis: Seite Tabelle
- Seite 11 und 12: 1. Einleitung 1.1 Benigne adenomat
- Seite 13 und 14: ist somit möglich. Die Häufigkeit
- Seite 15 und 16: handelt es sich um Adenokarzinome,
- Seite 17 und 18: Nach diesem Modell sind Mutationen
- Seite 19 und 20: 1.2.5. Screening-Untersuchungen bei
- Seite 21 und 22: sein. Untersuchungen zeigten, dass
- Seite 23 und 24: 1.4.3. Klinische Charakteristika de
- Seite 25 und 26: Sofern sie keine Symptome wie beisp
- Seite 27 und 28: 1.4.5. Familienberatung Im Vordergr
- Seite 29 und 30: 1.5.2. Definition des Proteoms Die
- Seite 31 und 32: 2. Ziel der Arbeit - Entwicklung re
- Seite 33 und 34: Technik liegt das Prinzip der Feinn
- Seite 35 und 36: 3.2.1. Isoelektrische Fokussierung
- Seite 37 und 38: Die SDS Polyacrylamid Gele haben ei
- Seite 39 und 40: 3.3.2. Matchset Ist die Proteinspot
- Seite 41 und 42: statistisch vergleichbar zu machen,
- Seite 43 und 44: zweier Verteilungen, also ob zwei u
- Seite 45 und 46: Minuten alkyliert. Trypsin wurde hi
- Seite 47 und 48: 4. Ergebnisse 4.1. Histologie: Alle
- Seite 49 und 50: Korrelationskoeffizient ist hierbei
- Seite 51 und 52: Polypen, welche als Ausreißer eher
- Seite 53 und 54: Abb.22 a+b: Massenspektrometrische
- Seite 55 und 56: Probe Patient Normal Adenom Tumor G
- Seite 57: 4.3.2. Qualitative Unterschiede zwi
- Seite 61 und 62: 1254 6,08 0,1 FAP 6431 4,31 0,18 FA
- Seite 63 und 64: 4652 1,73 0,02 FAP ja 7672 1,73 0,1
- Seite 65 und 66: 5. Diskussion Die Ergebnisse des
- Seite 67 und 68: nachgewiesen und 72 dieser Polypept
- Seite 69 und 70: zwischen dem primären Ovarialkarzi
- Seite 71 und 72: nachweislich fehlten. Ein Protein i
- Seite 73 und 74: Testpanels mehrerer Markerproteine
- Seite 75 und 76: Karzinomen exprimiert wurden und in
- Seite 77 und 78: sigmoidoscopy: implications for scr
- Seite 79 und 80: 37. Beahrs OH, Sanfelippo PM. Facto
- Seite 81 und 82: 60. Turcot J, Despres JP, St Pierre
- Seite 83 und 84: 82. Kadmon M, Moslein G, Buhr HJ, H
- Seite 85 und 86: 102. Omenn GS, States DJ, Adamski M
- Seite 87 und 88: 121. Gorg A, Postel W, Gunther S. T
- Seite 89 und 90: 142. Cui JF, Liu YK, Pan BS, Song H
- Seite 91 und 92: Anhang Reagenzien: Franzen Technik
- Seite 93 und 94: Veröffentlichungen: Originalarbeit
- Seite 95: 1994 Physikum 1995 Erstes Staatsexa