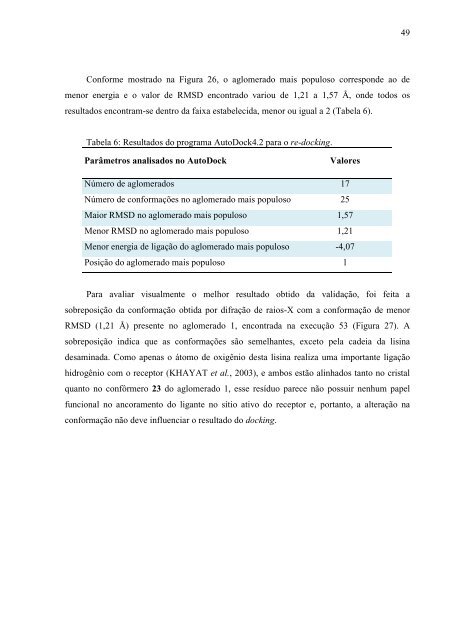
49Conforme mostrado na Figura 26, o aglomerado mais populoso correspon<strong>de</strong> ao <strong>de</strong>menor energia e o valor <strong>de</strong> RMSD encontrado variou <strong>de</strong> 1,21 a 1,57 Å, on<strong>de</strong> todos osresultados encontram-se <strong>de</strong>ntro da faixa estabelecida, menor ou igual a 2 (Tabela 6).Tabela 6: Resultados do programa AutoDock4.2 para o re-<strong>docking</strong>.Parâmetros analisados no AutoDockValoresNúmero <strong>de</strong> aglomerados 17Número <strong>de</strong> conformações no aglomerado mais populoso 25Maior RMSD no aglomerado mais populoso 1,57Menor RMSD no aglomerado mais populoso 1,21Menor energia <strong>de</strong> ligação do aglomerado mais populoso -4,07Posição do aglomerado mais populoso 1Para avaliar visualmente o melhor resultado obtido da validação, foi feita asobreposição da conformação obtida por difração <strong>de</strong> raios-X com a conformação <strong>de</strong> menorRMSD (1,21 Å) presente no aglomerado 1, encontrada na execução 53 (Figura 27). Asobreposição indica que as conformações são semelhantes, exceto pela ca<strong>de</strong>ia da lisina<strong>de</strong>saminada. Como apenas o átomo <strong>de</strong> oxigênio <strong>de</strong>sta lisina realiza uma importante ligaçãohidrogênio com o receptor (KHAYAT et al., 2003), e ambos estão alinhados tanto no cristalquanto no confôrmero 23 do aglomerado 1, esse resíduo parece não possuir nenhum papelfuncional no ancoramento do ligante no sítio ativo do receptor e, portanto, a alteração naconformação não <strong>de</strong>ve influenciar o resultado do <strong>docking</strong>.
50AglomeradosClassificadosSub-ClassificaçãoOperaçãoEnergia <strong>de</strong>LigaçãoRMSD doAglomeradoRMSD em<strong>relação</strong> àreferência1 1 46 -4,07 0,00 1,381 2 16 -4,04 0,14 1,361 3 25 -4,04 0,13 1,371 4 50 -4,03 0,59 1,311 5 70 -4,03 0,13 1,361 6 37 -4,03 0,13 1,361 7 23 -4,01 1,24 1,351 8 60 -4,01 0,96 1,571 9 22 -4,01 1,08 1,491 10 87 -4,00 1,23 1,321 11 10 -3,98 1,04 1,541 12 75 -3,98 0,97 1,561 13 72 -3,98 1,24 1,331 14 63 -3,98 1,04 1,531 15 48 -3,96 1,02 1,521 16 84 -3,96 1,03 1,531 17 73 -3,96 1,36 1,401 18 33 -3,95 1,36 1,401 19 76 -3,95 1,34 1,381 20 35 -3,93 1,00 1,521 21 68 -3,75 1,05 1,491 22 43 -3,62 1,20 1,221 23 53 -3,50 1,23 1,211 24 80 -2,59 1,89 1,241 25 86 -1,06 1,85 1,45Figura 27: Sobreposição do confôrmero encontrado no cristal (azul), código PDB 1NJU, comconfôrmero 23 (amarelo) do aglomerado 1 (acima); Tabela modificada do algomerado 1,obtida através do arquivo <strong>de</strong> saída do programa AutoDock4.2 (abaixo). Destaque emvermelho para a conformação 23 do aglomerado 1.Também foi analisada a capacida<strong>de</strong> da metodologia validada <strong>de</strong> encontrar as ligaçõeshidrogênio no programa AutoDock4.2. Foi feita uma comparação entre as ligações hidrogênioentre a protease <strong>de</strong> citomegalovírus e o ligante pepti<strong>de</strong>omimético, <strong>de</strong>scritas pelo programaLigand Explorer, disponível no banco <strong>de</strong> dados PDB e as ligações i<strong>de</strong>ntificadas peloprograma AutoDock após o re-<strong>docking</strong>. De acordo com o resultado, foi possível observar apredição pelo programa AutoDock <strong>de</strong> quatro das <strong>de</strong>z ligações hidrogênio exibidas peloprograma Ligand Explorer entre o confôrmero inicial do pepti<strong>de</strong>omimético e a protease <strong>de</strong>CMV.Comparando-se o confôrmero <strong>de</strong> menor RMSD obtido após o re-<strong>docking</strong>, com oconfôrmero inicial do cálculo <strong>de</strong> <strong>docking</strong> molecular (também analisado anteriormente no
- Page 1 and 2:
UNIVERSIDADE FEDERAL DO RIO DE JANE
- Page 3 and 4:
iiiFicha CatalográficaMello, Julia
- Page 5 and 6:
vÀ Deus e aos meus pais pelacompre
- Page 7 and 8:
viiAo CNPq, CAPES e FAPERJ pelo apo
- Page 9 and 10:
ixABSTRACTHerpes simplex is one of
- Page 11 and 12:
xiCOLORIDOS ATRAVÉS DE ESCALA DE S
- Page 13 and 14:
xiiiHIDROGÊNIO (EM VERDE) DO COMPO
- Page 15 and 16:
xvLISTA DE TABELASTABELA 1: VALORES
- Page 17 and 18: xviiLISTA DE ABREVIATURAS*dpf docki
- Page 19 and 20: xix5.1.2 MODELLER .................
- Page 21 and 22: 2Nas últimas décadas, estudos tê
- Page 23 and 24: 4HNONBrNOOOHOHN H 2NNOONHOOHAciclov
- Page 25 and 26: 6A relevância clínica dos inibido
- Page 27 and 28: 8Os inibidores do sítio ativo poss
- Page 29 and 30: 10Figura 8: Estrutura tridimensiona
- Page 31 and 32: 12somados aos recursos da computaç
- Page 33 and 34: 141.6.1.1Mecânica MolecularA mecâ
- Page 35 and 36: 16semelhança entre as estruturas p
- Page 37 and 38: 18Os métodos sistemáticos utiliza
- Page 39 and 40: 20fármacos, a avaliação do Drugl
- Page 41 and 42: 223 OBJETIVOInserido no contexto da
- Page 43 and 44: 24No Verify 3D, a análise do model
- Page 45 and 46: 26Tabela 2: Valores de IC 50 para d
- Page 47 and 48: 284.5 ESTUDO DE DRUGLIKENESS E DRUG
- Page 49 and 50: 30Figura 11: À esquerda, modelo tr
- Page 51 and 52: 325.1.2 MODELLERPara gerar o modelo
- Page 53 and 54: 34Pontuações Modelo Modeller x 1A
- Page 55 and 56: 36Figura 18: Estruturas secundária
- Page 57 and 58: Figura 19: Gráfico de Ramachandran
- Page 59 and 60: 40Figura 21: Gráfico de Ramachandr
- Page 61 and 62: 42Tabela 4: Benzoxazinonas (12-29)
- Page 63 and 64: 44nesta anel devido à ocorrência
- Page 65 and 66: 46Uma alternativa foi utilizar o pr
- Page 67: 48Tabela 5: Parâmetros de algoritm
- Page 71 and 72: 525.3.2 Docking Molecular das Benzo
- Page 73 and 74: 54benzoxazinona, através do progra
- Page 75 and 76: 56Ala39, Val28, Leu130, Ala131, Ala
- Page 77 and 78: 585.3.5 Docking molecular das demai
- Page 79 and 80: 60do tipo cátion-π é uma intera
- Page 81 and 82: 62interações dos ligantes volumos
- Page 83 and 84: 64grupamento alcoxi e o grupo amino
- Page 85 and 86: 66O docking molecular do composto 1
- Page 87 and 88: 68nitrogênio no resíduo Thr132 co
- Page 89 and 90: 70Figura 43: Comparação entre os
- Page 91 and 92: 72Figura 45: Representação do com
- Page 93 and 94: 74Figura 47: Peptideomimético 0FP
- Page 95 and 96: 765.4 AVALIAÇÃO DE DRUGLIKENESS E
- Page 97 and 98: 785.5 PROPOSTA DE NOVAS MOLÉCULAS
- Page 99 and 100: 80qualitativamente, e foi considera
- Page 101 and 102: 82Figura 51: (A) Docking molecular
- Page 103 and 104: 84de oxigênio da carbonila do subs
- Page 105 and 106: 86Estes resultados indicam que as m
- Page 107 and 108: 887 REFERÊNCIAS BIBLIOGRÁFICASABR
- Page 109 and 110: 90HEDSTROM, L. Serine protease mech
- Page 111 and 112: 92MARQUES, M. A. L.; BOTTI, S. O qu
- Page 113 and 114: 94STIERAND, K.; RAREY, M. Drawing t
- Page 115 and 116: 96Tabela 11: Parâmetros agrupados
- Page 117 and 118: 98Tabela 17: Parâmetros agrupados
- Page 119 and 120:
100Tabela 23: Parâmetros agrupados