Untersuchungen von Varianten des Polyomavirus-Hüllproteins VP1 im
Untersuchungen von Varianten des Polyomavirus-Hüllproteins VP1 im
Untersuchungen von Varianten des Polyomavirus-Hüllproteins VP1 im
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
68<br />
Da DTT in alkalischer Lösung rasch oxidiert wird, wurde der Einsatz <strong>von</strong><br />
Hydroxylamin als Nukleophil zur Induktion der Inteinspaltung untersucht. Mit einer<br />
Mischung aus 30 mM Hydroxylamin und 30 mM DTT konnte die Spaltungsreaktion<br />
vervollständigt werden, so dass mit dem Stamm BL21(DE3)/pET21-<strong>VP1</strong>Int ca. 5 mg<br />
gereinigtes <strong>VP1</strong> erhalten wurden. Eine komplette Reinigung nach dem opt<strong>im</strong>ierten<br />
Protokoll ist in Abbildung 17 zusammengefasst.<br />
Nach der Affinitätsreinigung wurde in der Proteinlösung noch eine sehr hohe<br />
Absorption bei 260 nm gemessen (Abbildung 17). Bei dieser Verunreinigung handelte<br />
es sich nicht um an <strong>VP1</strong> gebundene DNA, da eine Inkubation mit Benzonase und eine<br />
anschließende Dialyse nur zu einer geringfügigen Reduktion der Absorption bei 260 nm<br />
führte. Mit Hilfe einer Ammoniumsulfatfällung <strong>des</strong> Proteins nach der Affinitäts-<br />
Chromatographie konnte diese Verunreinigung jedoch vollständig abgetrennt werden,<br />
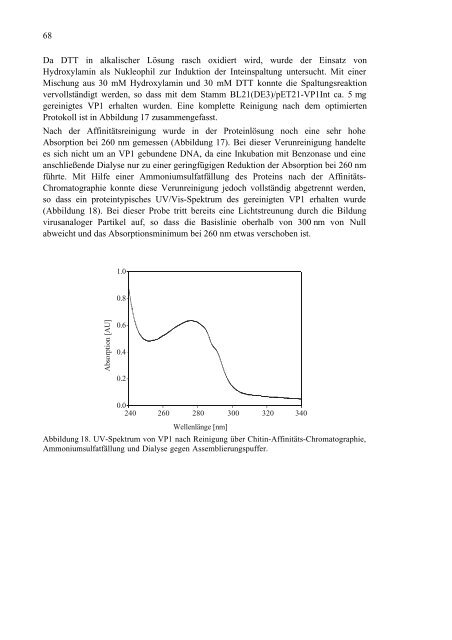
so dass ein proteintypisches UV/Vis-Spektrum <strong>des</strong> gereinigten <strong>VP1</strong> erhalten wurde<br />
(Abbildung 18). Bei dieser Probe tritt bereits eine Lichtstreunung durch die Bildung<br />
virusanaloger Partikel auf, so dass die Basislinie oberhalb <strong>von</strong> 300 nm <strong>von</strong> Null<br />
abweicht und das Absorptionsmin<strong>im</strong>um bei 260 nm etwas verschoben ist.<br />
Absorption [AU]<br />
1.0<br />
0.8<br />
0.6<br />
0.4<br />
0.2<br />
0.0<br />
240 260 280 300 320 340<br />
Wellenlänge [nm]<br />
Abbildung 18. UV-Spektrum <strong>von</strong> <strong>VP1</strong> nach Reinigung über Chitin-Affinitäts-Chromatographie,<br />
Ammoniumsulfatfällung und Dialyse gegen Assemblierungspuffer.