Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
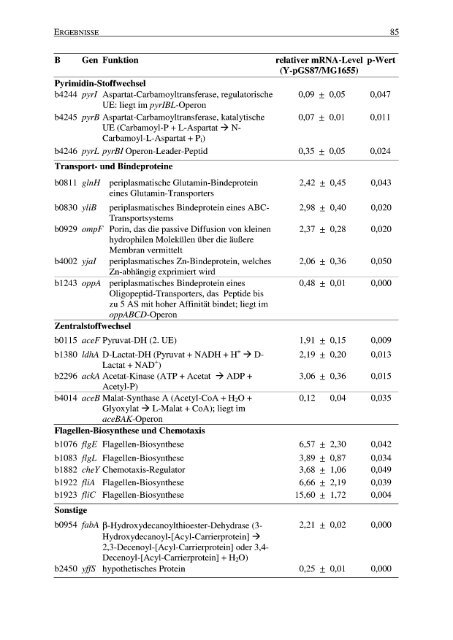
ERGEBNISSE 85<br />
B Gen Funktion relativer mRNA-Level p-Wert<br />
(Y-pGS87/MG1655)<br />
Pyrimidin-Stoffwechsel<br />
b4244 pyrI Aspartat-Carbamoyltransferase, regulatorische<br />
UE : liegt im pyrIBL-Operon<br />
0,09 ± 0,05 0,047<br />
b4245 pyrB Aspartat-Carbamoyltransferase, katalytische<br />
UE (Carbamoyl-P + L-Aspartat --> N-<br />
Carbamoyl-L-Aspartat + Pi)<br />
0,07 ± 0,01 0,011<br />
b4246 pyrL pyrBI Operon-Leader-Peptid 0,35 ± 0,05 0,024<br />
Transport- und Bindeproteine<br />
b0811 glnH periplasmatische Glutamin-Bindeprotein 2,42 ± 0,45 0,043<br />
eines Glutamin-Transporters<br />
. . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . .<br />
1.24<br />
.............. .... .......... ......... ....... . .......... . ..~...... ...... ............. ............. ............. ............. ............ ............. ............. ............. ..........<br />
b 3 oppA pe . ~p . 1as . ~at1sc~es Bindep Bindeprotein eines 0,48 + b0830 yliB periplasmatisches Bindeprotein eines ABC-<br />
Transportsystems<br />
2,98 ± 0,40 0,020<br />
b0929 ompF Porin, das die passive Diffusion von kleinen<br />
hydrophilen Molekülen über die äußere<br />
Membran vermittelt<br />
2,37 ± 0,28 0,020<br />
b4002 yjaI periplasmatisches Zn-Bindeprotein, welches 2,06 ± 0,36 0,050<br />
Zn-abhängig exprimiert wird<br />
_ 0,01 0,000<br />
Oligopeptid-Transporters, das Peptide bis<br />
zu 5 AS mit hoher Affinität bindet; liegt im<br />
oppABCD-Operon<br />
Zentralstoffwechsel<br />
b0115 aceF <strong>Pyruvat</strong>-DH (2. UE) 1,91 ± 0,15<br />
0,009<br />
. . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . . .<br />
.... ... .. ... ... ............. ............. ......... .1 .2....... .Ö...Ö4 ............. .......Ö, .<br />
b4014 .035 . .<br />
aceB Malat-SyYnthase Ä b1380 ldhA D-Lactat-DH (<strong>Pyruvat</strong> + NADH + H+ --> D-<br />
Lactat + NAD+)<br />
2,19 ± 0,20 0,013<br />
b2296 ackA Acetat-Kinase (ATP + Acetat --> ADP + 3,06 ± 0,36 0,015<br />
Acetyl-P)<br />
+ H2ö .+ Ö<br />
(AcetyY1_CoA ><br />
Glyoxylat --> L-Malat + CoA) ; liegt im<br />
aceBAK-Operon<br />
Flagellen-Biosynthese und Chemotaxis<br />
b1076 flgE Flagellen-Biosynthese 6,57 ± 2,30<br />
b1083 flgL Flagellen-Biosynthese 3,89 ± 0,87<br />
b1882 cheY Chemotaxis-Regulator 3,68 ± 1,06<br />
b1922 fliA Flagellen-Biosynthese 6,66 ± 2,19<br />
b1923 fliC Flagellen-Biosynthese 15,60 ± 1,72<br />
Sonstige<br />
b0954 fabA (3-Hydroxydecanoylthioester-Dehydrase (3- 2,21 ± 0,02<br />
Hydroxydecanoyl-[Acyl-Carrierprotein] --><br />
2,3-Decenoyl-[Acyl-Carrierprotein] oder 3,4-<br />
Decenoyl-[Acyl-Carrierprotein] + H2O)<br />
b2450 yffS hypothetisches Protein 0,25 ± 0,01<br />
0,042<br />
0,034<br />
0,049<br />
0,039<br />
0,004<br />
0,000<br />
0,000