Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
ERGEBNISSE 93<br />
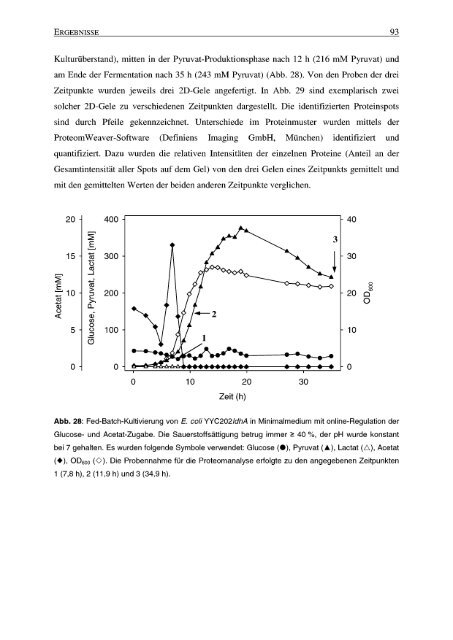
Kulturüberstand), mitten in der <strong>Pyruvat</strong>-<strong>Produktion</strong>sphase nach 12 h (216 mM <strong>Pyruvat</strong>) und<br />
am Ende der Fermentation nach 35 h (243 mM <strong>Pyruvat</strong>) (Abb . 28) . Von den Proben der drei<br />
Zeitpunkte wurden jeweils drei 2D-Gele angefertigt . In Abb . 29 sind exemplarisch zwei<br />
solcher 2D-Gele zu verschiedenen Zeitpunkten dargestellt . Die identifizierten Proteinspots<br />
sind <strong>durch</strong> Pfeile gekennzeichnet . Unterschiede im Proteinmuster wurden mittels der<br />
ProteomWeaver-Software (Definiens Imaging GmbH, München) identifiziert und<br />
quantifiziert . Dazu wurden die relativen Intensitäten der einzelnen Proteine (Anteil an der<br />
Gesamtintensität aller Spots auf dem Gel) von den drei Gelen eines Zeitpunkts gemittelt und<br />
mit den gemittelten Werten der beiden anderen Zeitpunkte verglichen .<br />
a)<br />
U<br />
a<br />
20 -<br />
5-<br />
0<br />
0 10 20 30<br />
Zeit (h)<br />
Abb . 28 : Fed-Batch-Kultivierung von E. coli YYC2021dhA in Minimalmedium mit online-Regulation der<br />
Glucose- und Acetat-Zugabe . Die Sauerstoffsättigung betrug immer >_ 40 %, der pH wurde konstant<br />
bei 7 gehalten . Es wurden folgende Symbole verwendet : Glucose ("), <strong>Pyruvat</strong> (A), Lactat (0), Acetat<br />
( " ), OD600 (O) . Die Probennahme für die Proteomanalyse erfolgte zu den angegebenen Zeitpunkten<br />
1 (7,8 h), 2 (11,9 h) und 3 (34,9 h) .