Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Pyruvat-Produktion durch acetatauxotrophe - JUWEL ...
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
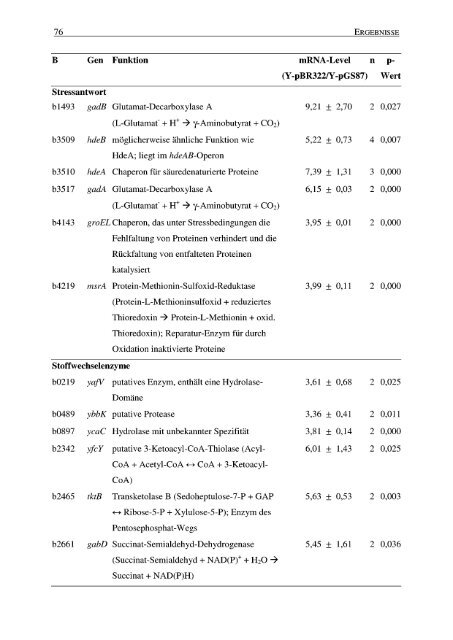
76 ERGEBNISSE<br />
B Gen Funktion mRNA-Level<br />
Stressantwort<br />
(Succinat-Semialdehyd + NAD(P)+ + H20<br />
Succinat + NAD(P)H)<br />
(Y-pBR322/Y-pGS87)<br />
n p-<br />
Wert<br />
b1493 gadB Glutamat-Decarboxylase A 9,21 ± 2,70 2 0,027<br />
(L-Glutamat + H+ --> y-Aminobutyrat + C02)<br />
b3509 hdeB möglicherweise ähnliche Funktion wie 5,22 ± 0,73 4 0,007<br />
HdeA ; liegt im hdeAB-Operon<br />
b3510 hdeA Chaperon für säuredenaturierte Proteine 7,39 ± 1,31 3 0,000<br />
b3517 gadA Glutamat-Decarboxylase A 6,15 ± 0,03 2 0,000<br />
(L-Glutamat + H+ --> y-Aminobutyrat + C02)<br />
b4143 groEL Chaperon, das unter Stressbedingungen die 3,95 ± 0,01 2 0,000<br />
Fehlfaltung von Proteinen verhindert und die<br />
Rückfaltung von entfalteten Proteinen<br />
katalysiert<br />
b4219 msrA Protein-Methionin-Sulfoxid-Reduktase 3,99 ± 0,11 2 0,000<br />
Stoffwechselenzyme<br />
(Protein-L-Methioninsulfoxid + reduziertes<br />
Thioredoxin --> Protein-L-Methionin + oxid .<br />
Thioredoxin) ; Reparatur-Enzym für <strong>durch</strong><br />
Oxidation inaktivierte Proteine<br />
b0219 yafV putatives Enzym, enthält eine Hydrolase- 3,61 ± 0,68 2 0,025<br />
Domäne<br />
b0489 ybbK putative Protease 3,36 ± 0,41 2 0,011<br />
b0897 ycaC Hydrolase mit unbekannter Spezifität 3,81 ± 0,14 2 0,000<br />
b2342 yfCY putative 3-Ketoacyl-CoA-Thiolase (Acyl- 6,01 ± 1,43 2 0,025<br />
CoA + Acetyl-CoA H CoA + 3-Ketoacyl-<br />
COA)<br />
b2465 tktB Transketolase B (Sedoheptulose-7-P + GAP 5,63 ± 0,53 2 0,003<br />
H Ribose-5-P + Xylulose-5-P) ; Enzym des<br />
Pentosephosphat-Wegs<br />
b2661 gabD Succinat-Semialdehyd-Dehydrogenase 5,45 ± 1,61 2 0,036