PDF 5.972kB - TOBIAS-lib - Universität Tübingen
PDF 5.972kB - TOBIAS-lib - Universität Tübingen
PDF 5.972kB - TOBIAS-lib - Universität Tübingen
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
ERGEBNISSE<br />
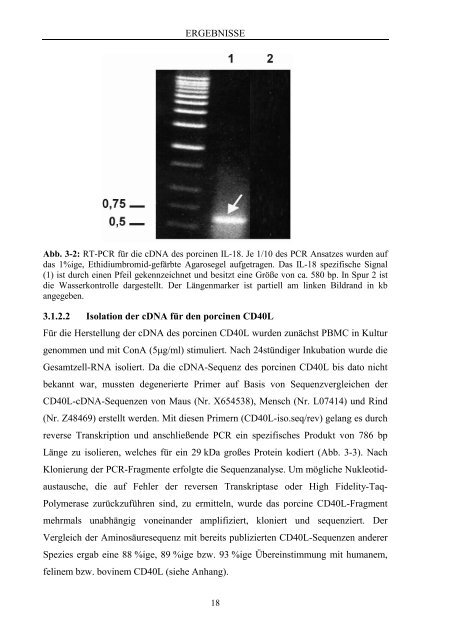
Abb. 3-2: RT-PCR für die cDNA des porcinen IL-18. Je 1/10 des PCR Ansatzes wurden auf<br />
das 1%ige, Ethidiumbromid-gefärbte Agarosegel aufgetragen. Das IL-18 spezifische Signal<br />
(1) ist durch einen Pfeil gekennzeichnet und besitzt eine Größe von ca. 580 bp. In Spur 2 ist<br />
die Wasserkontrolle dargestellt. Der Längenmarker ist partiell am linken Bildrand in kb<br />
angegeben.<br />
3.1.2.2 Isolation der cDNA für den porcinen CD40L<br />
Für die Herstellung der cDNA des porcinen CD40L wurden zunächst PBMC in Kultur<br />
genommen und mit ConA (5µg/ml) stimuliert. Nach 24stündiger Inkubation wurde die<br />
Gesamtzell-RNA isoliert. Da die cDNA-Sequenz des porcinen CD40L bis dato nicht<br />
bekannt war, mussten degenerierte Primer auf Basis von Sequenzvergleichen der<br />
CD40L-cDNA-Sequenzen von Maus (Nr. X654538), Mensch (Nr. L07414) und Rind<br />
(Nr. Z48469) erstellt werden. Mit diesen Primern (CD40L-iso.seq/rev) gelang es durch<br />
reverse Transkription und anschließende PCR ein spezifisches Produkt von 786 bp<br />
Länge zu isolieren, welches für ein 29 kDa großes Protein kodiert (Abb. 3-3). Nach<br />
Klonierung der PCR-Fragmente erfolgte die Sequenzanalyse. Um mögliche Nukleotid-<br />
austausche, die auf Fehler der reversen Transkriptase oder High Fidelity-Taq-<br />
Polymerase zurückzuführen sind, zu ermitteln, wurde das porcine CD40L-Fragment<br />
mehrmals unabhängig voneinander amplifiziert, kloniert und sequenziert. Der<br />
Vergleich der Aminosäuresequenz mit bereits publizierten CD40L-Sequenzen anderer<br />
Spezies ergab eine 88 %ige, 89 %ige bzw. 93 %ige Übereinstimmung mit humanem,<br />
felinem bzw. bovinem CD40L (siehe Anhang).<br />
18