Alberto Risueño Pérez - Gredos - Universidad de Salamanca
Alberto Risueño Pérez - Gredos - Universidad de Salamanca
Alberto Risueño Pérez - Gredos - Universidad de Salamanca
You also want an ePaper? Increase the reach of your titles
YUMPU automatically turns print PDFs into web optimized ePapers that Google loves.
Capítulo 1<br />
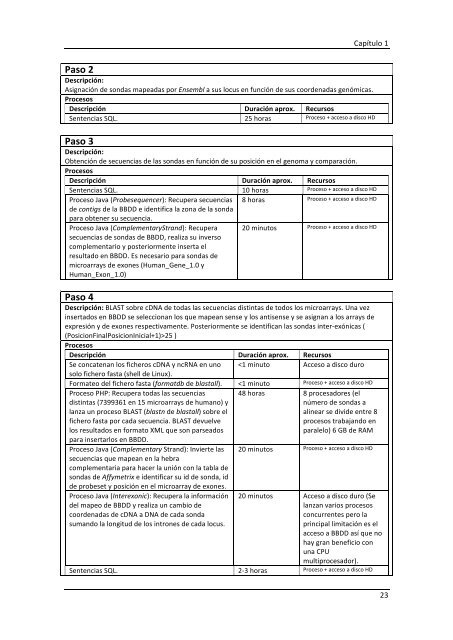
Paso 2<br />
Descripción:<br />
Asignación <strong>de</strong> sondas mapeadas por Ensembl a sus locus en función <strong>de</strong> sus coor<strong>de</strong>nadas genómicas.<br />
Procesos<br />
Descripción Duración aprox. Recursos<br />
Sentencias SQL. 25 horas Proceso + acceso a disco HD<br />
Paso 3<br />
Descripción:<br />
Obtención <strong>de</strong> secuencias <strong>de</strong> las sondas en función <strong>de</strong> su posición en el genoma y comparación.<br />
Procesos<br />
Descripción Duración aprox. Recursos<br />
Sentencias SQL. 10 horas Proceso + acceso a disco HD<br />
Proceso Java (Probesequencer): Recupera secuencias<br />
<strong>de</strong> contigs <strong>de</strong> la BBDD e i<strong>de</strong>ntifica la zona <strong>de</strong> la sonda<br />
para obtener su secuencia.<br />
8 horas<br />
Proceso + acceso a disco HD<br />
Proceso Java (ComplementaryStrand): Recupera<br />
secuencias <strong>de</strong> sondas <strong>de</strong> BBDD, realiza su inverso<br />
complementario y posteriormente inserta el<br />
resultado en BBDD. Es necesario para sondas <strong>de</strong><br />
microarrays <strong>de</strong> exones (Human_Gene_1.0 y<br />
Human_Exon_1.0)<br />
20 minutos<br />
Proceso + acceso a disco HD<br />
Paso 4<br />
Descripción: BLAST sobre cDNA <strong>de</strong> todas las secuencias distintas <strong>de</strong> todos los microarrays. Una vez<br />
insertados en BBDD se seleccionan los que mapean sense y los antisense y se asignan a los arrays <strong>de</strong><br />
expresión y <strong>de</strong> exones respectivamente. Posteriormente se i<strong>de</strong>ntifican las sondas inter-‐exónicas (<br />
(PosicionFinalPosicionInicial+1)>25 )<br />
Procesos<br />
Descripción Duración aprox. Recursos<br />
Se concatenan los ficheros cDNA y ncRNA en uno<br />
solo fichero fasta (shell <strong>de</strong> Linux).<br />