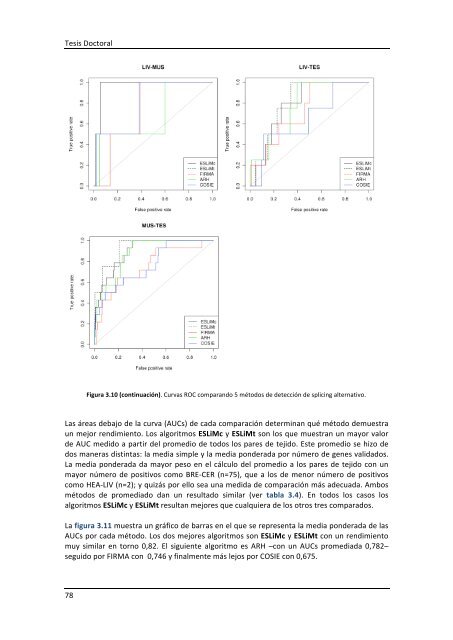
Tesis Doctoral 78 Figura 3.10 (continuación). Curvas ROC comparando 5 métodos <strong>de</strong> <strong>de</strong>tección <strong>de</strong> splicing alternativo. Las áreas <strong>de</strong>bajo <strong>de</strong> la curva (AUCs) <strong>de</strong> cada comparación <strong>de</strong>terminan qué método <strong>de</strong>muestra un mejor rendimiento. Los algoritmos ESLiMc y ESLiMt son los que muestran un mayor valor <strong>de</strong> AUC medido a partir <strong>de</strong>l promedio <strong>de</strong> todos los pares <strong>de</strong> tejido. Este promedio se hizo <strong>de</strong> dos maneras distintas: la media simple y la media pon<strong>de</strong>rada por número <strong>de</strong> genes validados. La media pon<strong>de</strong>rada da mayor peso en el cálculo <strong>de</strong>l promedio a los pares <strong>de</strong> tejido con un mayor número <strong>de</strong> positivos como BRE-‐CER (n=75), que a los <strong>de</strong> menor número <strong>de</strong> positivos como HEA-‐LIV (n=2); y quizás por ello sea una medida <strong>de</strong> comparación más a<strong>de</strong>cuada. Ambos métodos <strong>de</strong> promediado dan un resultado similar (ver tabla 3.4). En todos los casos los algoritmos ESLiMc y ESLiMt resultan mejores que cualquiera <strong>de</strong> los otros tres comparados. La figura 3.11 muestra un gráfico <strong>de</strong> barras en el que se representa la media pon<strong>de</strong>rada <strong>de</strong> las AUCs por cada método. Los dos mejores algoritmos son ESLiMc y ESLiMt con un rendimiento muy similar en torno 0,82. El siguiente algoritmo es ARH –con un AUCs promediada 0,782– seguido por FIRMA con 0,746 y finalmente más lejos por COSIE con 0,675.
ESLiMc ESLiMt FIRMA ARH COSIE BRE-‐CER 0,834 0,854 0,752 0,784 0,640 BRE-‐HEA 0,708 0,625 0,802 0,882 0,681 BRE-‐LIV 0,804 0,833 0,879 0,884 0,775 BRE-‐MUS 0,894 0,872 0,801 0,858 0,647 BRE-‐TES 0,844 0,856 0,756 0,708 0,636 CER-‐HEA 0,737 0,758 0,715 0,711 0,656 CER-‐LIV 0,763 0,785 0,645 0,735 0,705 CER-‐MUS 0,825 0,763 0,767 0,795 0,728 CER-‐TES 0,820 0,840 0,690 0,768 0,647 HEA-‐LIV 0,799 0,897 0,716 0,853 0,588 HEA-‐MUS 0,854 0,829 0,790 0,807 0,656 HEA-‐TES 0,935 0,940 0,901 0,717 0,886 LIV-‐MUS 0,966 NA 0,736 0,676 0,796 LIV-‐TES 0,789 0,809 0,732 0,773 0,650 MUS-‐TES 0,899 0,931 0,751 0,880 0,768 Media 0,832 0,828 0,762 0,789 0,697 Media pon<strong>de</strong>rada 0,823 0,818 0,746 0,782 0,675 Capítulo 3 Tabla 3.4. Comparativa <strong>de</strong> AUCs <strong>de</strong> las ROCs alcanzada por cada par <strong>de</strong> tejidos y método <strong>de</strong> <strong>de</strong>tección <strong>de</strong> splicing alternativo estudiados. Se han utilizado dos métodos para promediar los 15 contrastes: media simple y media pon<strong>de</strong>rada por número <strong>de</strong> positivos (genes con splicing validado). Los dos métodos <strong>de</strong>sarrollados en este trabajo (ESLiMc y ESLiMt) muestran un mejor rendimiento que algoritmos previamente publicados (FIRMA, ARH y COSIE). ESLiMt presenta un "NA" en la comparación LIV-‐MUS <strong>de</strong>bido a que ninguna sonda mapea en los genes validados para par <strong>de</strong> tejidos (ver tabla 3.3). Figura 3.11. Media pon<strong>de</strong>rada por número <strong>de</strong> genes validados <strong>de</strong> las AUCs provenientes <strong>de</strong> las curvas ROC <strong>de</strong> los 15 pares <strong>de</strong> tejidos. Los dos métodos <strong>de</strong>sarrollados en este trabajo (ESLiMc y ESLiMt) muestran un mejor rendimiento que algoritmos FIRMA, ARH y COSIE. Las curvas ROC son una buena técnica para comparar métodos, ya que dan una visión global clasificando todos los datos disponibles (en este caso todos los genes). Sin embargo, al tratar con datos <strong>de</strong> genómicos, la dimensión <strong>de</strong> las matrices es muy alta y sólo una pequeña parte 79
- Page 1:
Bioinformática aplicada a estudios
- Page 5 and 6:
Índice INTRODUCCIÓN GENERAL .....
- Page 7 and 8:
Introducción general Bioinformáti
- Page 9 and 10:
Figura 2. Proceso de transcripción
- Page 11 and 12:
Introducción general caciones, las
- Page 13 and 14:
Objetivos Introducción general La
- Page 15 and 16:
Capítulo 1 1.1.1. Bases de datos d
- Page 17 and 18:
Capítulo 1 sondas core y su inform
- Page 19 and 20:
caaatgacttgctattattgatggc 225 694 c
- Page 21 and 22:
presentes en el fichero. Capítulo
- Page 23 and 24:
Capítulo 1 Mus musculus MG_U74Av2
- Page 25 and 26:
Capítulo 1 Figura 1.5. Representac
- Page 27 and 28:
Capítulo 1 Paso 2 Descripción: As
- Page 29 and 30:
Capítulo 1 A la hora de escribir e
- Page 31 and 32: Capítulo 1 en regiones no codifica
- Page 33 and 34: Capítulo 1 Para optimizar la preci
- Page 35 and 36: Figura 1.9a. Distribución del núm
- Page 37 and 38: Capítulo 1 por contraste el númer
- Page 39 and 40: Capítulo 1 (cromosoma, locus, exon
- Page 41 and 42: Capítulo 1 figura 1.16). Además d
- Page 43 and 44: Capítulo 1 exhaustivo en este ámb
- Page 45 and 46: Capítulo 1 su presentación y deta
- Page 47: Capítulo 1 adaptación para los mi
- Page 50 and 51: Tesis Doctoral pueden agrupar en: t
- Page 52 and 53: Tesis Doctoral enfermedad a través
- Page 54 and 55: Tesis Doctoral los genes encontrado
- Page 56 and 57: Tesis Doctoral real (RT-‐PCR).
- Page 58 and 59: Tesis Doctoral muestras (ver figura
- Page 60 and 61: Tesis Doctoral subtipo fueron: 0.97
- Page 62 and 63: Tesis Doctoral En este trabajo se h
- Page 64 and 65: Tesis Doctoral permitiría, sin dud
- Page 66 and 67: Tesis Doctoral inclusión entre 0 y
- Page 68 and 69: Tesis Doctoral exacto del número d
- Page 70 and 71: Tesis Doctoral Los valores extremos
- Page 72 and 73: Tesis Doctoral dicho, la comparaci
- Page 74 and 75: Tesis Doctoral 70 Figura 3.6. Los d
- Page 76 and 77: Tesis Doctoral 3.8.b). Sin embargo
- Page 78 and 79: Tesis Doctoral Human Exon 1.0. La l
- Page 80 and 81: Tesis Doctoral 76 Figura 3.10. Curv
- Page 84 and 85: Tesis Doctoral del inicio del ranki
- Page 87 and 88: Capítulo 4 Análisis de coexpresi
- Page 89 and 90: Capítulo 4 los genes y la perspect
- Page 91 and 92: Capítulo 4 Utilizando el set de da
- Page 93 and 94: ENSG00000142541 RPL13A small nucleo
- Page 95 and 96: Capítulo 4 Para encontrar los gene
- Page 97 and 98: Capítulo 4 ENSG00000134287 ARF3 AD
- Page 99 and 100: Capítulo 4 Figura 4.3. Red de coex
- Page 101 and 102: Capítulo 4 Si analizamos los genes
- Page 103 and 104: Capítulo 4 se hizo comparando cont
- Page 105: 4.4. Discusión y posible trabajo f
- Page 108 and 109: Tesis Doctoral exones, y diseñando
- Page 110 and 111: Tesis Doctoral expression and isofo
- Page 112 and 113: Tesis Doctoral 37, e107. Gardina, P
- Page 114 and 115: Tesis Doctoral and survival in chro
- Page 116 and 117: Tesis Doctoral Roth, R.B., Hevezi,
- Page 118 and 119: Tesis Doctoral Xi, L., Feber, A., G
- Page 121 and 122: Risueño et al. BMC Bioinformatics
- Page 123 and 124: Risueño et al. BMC Bioinformatics
- Page 125 and 126: Risueño et al. BMC Bioinformatics
- Page 127 and 128: Risueño et al. BMC Bioinformatics
- Page 129 and 130: Risueño et al. BMC Bioinformatics
- Page 131 and 132: Risueño et al. BMC Bioinformatics
- Page 133 and 134:
ORIGINAL ARTICLE Deregulation of mi
- Page 135 and 136:
Targets component of miRecords inte
- Page 137 and 138:
log 10 2-ΔCt -2.00 -4.00 -6.00 -8.
- Page 139 and 140:
Table 4 Potential microRNA (miRNA)-
- Page 141 and 142:
myeloma pathogenesis. Proc Natl Aca
- Page 143 and 144:
genetic subtypes of CLL show differ
- Page 145 and 146:
Table 2. Cont. Up-regulated Down-re
- Page 147 and 148:
206 underexpressed in the 13q-H gro
- Page 149 and 150:
Table 3. Most significant target ge
- Page 151 and 152:
Discussion 13q deletion (13q-) is t
- Page 153 and 154:
patients with 17p and 11q deletions
- Page 155 and 156:
Human Gene Coexpression Landscape:
- Page 157 and 158:
The similarity and proximity of the
- Page 159 and 160:
As described in Methods we use a co
- Page 161 and 162:
all data points of coexpression pai
- Page 163 and 164:
Table 1. This work (2008) Pathway N
- Page 165 and 166:
In conclusion, the functional consi
- Page 167 and 168:
a total set of 48 microarrays. The
- Page 169 and 170:
original article Annals of Oncology
- Page 171 and 172:
Annals of Oncology original article
- Page 173 and 174:
Annals of Oncology original article
- Page 175 and 176:
Annals of Oncology original article