Protein ? Disassembly im Verlauf der endosomalen Prozessierung
Protein ? Disassembly im Verlauf der endosomalen Prozessierung
Protein ? Disassembly im Verlauf der endosomalen Prozessierung
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
Ergebnisse Seite 115<br />
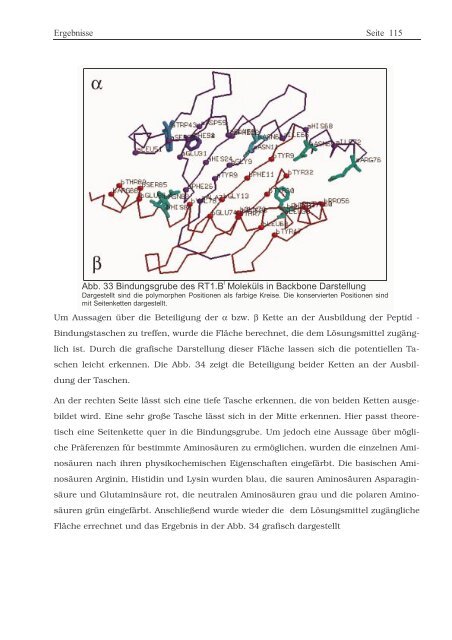
Abb. 33 Bindungsgrube des RT1.B l Moleküls in Backbone Darstellung<br />
Dargestellt sind die polymorphen Positionen als farbige Kreise. Die konservierten Positionen sind<br />
mit Seitenketten dargestellt.<br />
Um Aussagen über die Beteiligung <strong>der</strong> α bzw. β Kette an <strong>der</strong> Ausbildung <strong>der</strong> Peptid -<br />
Bindungstaschen zu treffen, wurde die Fläche berechnet, die dem Lösungsmittel zugäng-<br />
lich ist. Durch die grafische Darstellung dieser Fläche lassen sich die potentiellen Ta-<br />
schen leicht erkennen. Die Abb. 34 zeigt die Beteiligung bei<strong>der</strong> Ketten an <strong>der</strong> Ausbil-<br />
dung <strong>der</strong> Taschen.<br />
An <strong>der</strong> rechten Seite lässt sich eine tiefe Tasche erkennen, die von beiden Ketten ausge-<br />
bildet wird. Eine sehr große Tasche lässt sich in <strong>der</strong> Mitte erkennen. Hier passt theore-<br />
tisch eine Seitenkette quer in die Bindungsgrube. Um jedoch eine Aussage über mögli-<br />
che Präferenzen für best<strong>im</strong>mte Aminosäuren zu ermöglichen, wurden die einzelnen Ami-<br />
nosäuren nach ihren physikochemischen Eigenschaften eingefärbt. Die basischen Ami-<br />
nosäuren Arginin, Histidin und Lysin wurden blau, die sauren Aminosäuren Asparagin-<br />
säure und Glutaminsäure rot, die neutralen Aminosäuren grau und die polaren Amino-<br />
säuren grün eingefärbt. Anschließend wurde wie<strong>der</strong> die dem Lösungsmittel zugängliche<br />
Fläche errechnet und das Ergebnis in <strong>der</strong> Abb. 34 grafisch dargestellt