Protein ? Disassembly im Verlauf der endosomalen Prozessierung
Protein ? Disassembly im Verlauf der endosomalen Prozessierung
Protein ? Disassembly im Verlauf der endosomalen Prozessierung
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
Ergebnisse Seite 74<br />
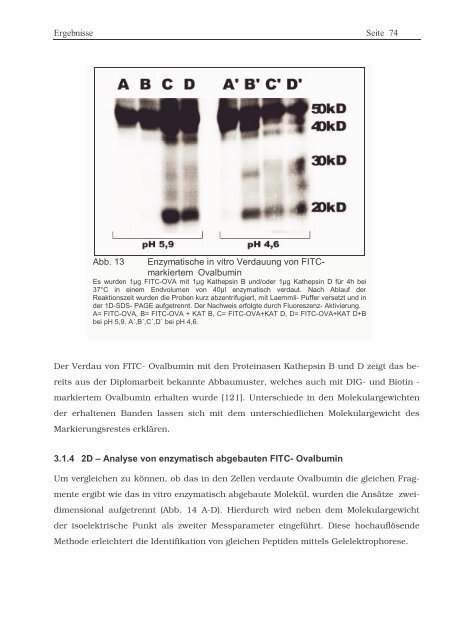
Abb. 13 Enzymatische in vitro Verdauung von FITCmarkiertem<br />
Ovalbumin<br />
Es wurden 1µg FITC-OVA mit 1µg Kathepsin B und/o<strong>der</strong> 1µg Kathepsin D für 4h bei<br />
37°C in einem Endvolumen von 40µl enzymatisch verdaut. Nach Ablauf <strong>der</strong><br />
Reaktionszeit wurden die Proben kurz abzentrifugiert, mit Laemmli- Puffer versetzt und in<br />
<strong>der</strong> 1D-SDS- PAGE aufgetrennt. Der Nachweis erfolgte durch Fluoreszenz- Aktivierung.<br />
A= FITC-OVA, B= FITC-OVA + KAT B, C= FITC-OVA+KAT D, D= FITC-OVA+KAT D+B<br />
bei pH 5,9. A´,B´,C´,D´ bei pH 4,6.<br />
Der Verdau von FITC- Ovalbumin mit den <strong>Protein</strong>asen Kathepsin B und D zeigt das be-<br />
reits aus <strong>der</strong> Diplomarbeit bekannte Abbaumuster, welches auch mit DIG- und Biotin -<br />
markiertem Ovalbumin erhalten wurde [121]. Unterschiede in den Molekulargewichten<br />
<strong>der</strong> erhaltenen Banden lassen sich mit dem unterschiedlichen Molekulargewicht des<br />
Markierungsrestes erklären.<br />
3.1.4 2D – Analyse von enzymatisch abgebauten FITC- Ovalbumin<br />
Um vergleichen zu können, ob das in den Zellen verdaute Ovalbumin die gleichen Frag-<br />
mente ergibt wie das in vitro enzymatisch abgebaute Molekül, wurden die Ansätze zwei-<br />
d<strong>im</strong>ensional aufgetrennt (Abb. 14 A-D). Hierdurch wird neben dem Molekulargewicht<br />
<strong>der</strong> isoelektrische Punkt als zweiter Messparameter eingeführt. Diese hochauflösende<br />
Methode erleichtert die Identifikation von gleichen Peptiden mittels Gelelektrophorese.