Angelika Semmler - KOPS - Universität Konstanz
Angelika Semmler - KOPS - Universität Konstanz
Angelika Semmler - KOPS - Universität Konstanz
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
3 Sollbruchstellen<br />
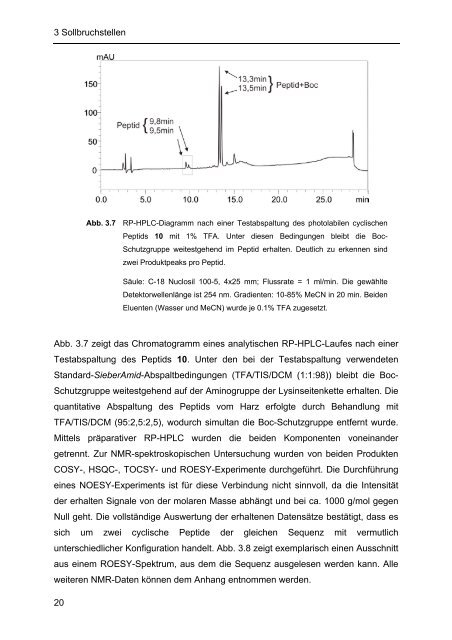
Abb. 3.7 RP-HPLC-Diagramm nach einer Testabspaltung des photolabilen cyclischen<br />
Peptids 10 mit 1% TFA. Unter diesen Bedingungen bleibt die Boc-<br />
Schutzgruppe weitestgehend im Peptid erhalten. Deutlich zu erkennen sind<br />
zwei Produktpeaks pro Peptid.<br />
Säule: C-18 Nuclosil 100-5, 4x25 mm; Flussrate = 1 ml/min. Die gewählte<br />
Detektorwellenlänge ist 254 nm. Gradienten: 10-85% MeCN in 20 min. Beiden<br />
Eluenten (Wasser und MeCN) wurde je 0.1% TFA zugesetzt.<br />
Abb. 3.7 zeigt das Chromatogramm eines analytischen RP-HPLC-Laufes nach einer<br />
Testabspaltung des Peptids 10. Unter den bei der Testabspaltung verwendeten<br />
Standard-SieberAmid-Abspaltbedingungen (TFA/TIS/DCM (1:1:98)) bleibt die Boc-<br />
Schutzgruppe weitestgehend auf der Aminogruppe der Lysinseitenkette erhalten. Die<br />
quantitative Abspaltung des Peptids vom Harz erfolgte durch Behandlung mit<br />
TFA/TIS/DCM (95:2,5:2,5), wodurch simultan die Boc-Schutzgruppe entfernt wurde.<br />
Mittels präparativer RP-HPLC wurden die beiden Komponenten voneinander<br />
getrennt. Zur NMR-spektroskopischen Untersuchung wurden von beiden Produkten<br />
COSY-, HSQC-, TOCSY- und ROESY-Experimente durchgeführt. Die Durchführung<br />
eines NOESY-Experiments ist für diese Verbindung nicht sinnvoll, da die Intensität<br />
der erhalten Signale von der molaren Masse abhängt und bei ca. 1000 g/mol gegen<br />
Null geht. Die vollständige Auswertung der erhaltenen Datensätze bestätigt, dass es<br />
sich um zwei cyclische Peptide der gleichen Sequenz mit vermutlich<br />
unterschiedlicher Konfiguration handelt. Abb. 3.8 zeigt exemplarisch einen Ausschnitt<br />
aus einem ROESY-Spektrum, aus dem die Sequenz ausgelesen werden kann. Alle<br />
weiteren NMR-Daten können dem Anhang entnommen werden.<br />
20