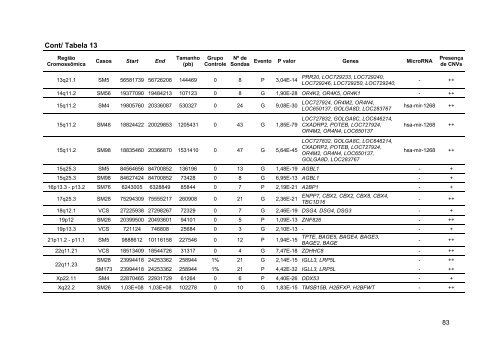
Cont/ Tabela 13 Região Cromossômica Casos Start End Tamanho (pb) Grupo Controle Nº <strong>de</strong> Sondas 13q21.1 SM5 56581739 56726208 144469 0 8 P 3,04E-14 Evento P valor Genes MicroRNA Presença <strong>de</strong> CNVs PRR20, LOC729233, LOC729240, LOC729246, LOC729250, LOC729240, - ++ 14q11.2 SM56 19377090 19484213 107123 0 8 G 1,90E-28 OR4K2, OR4K5, OR4K1 - ++ 15q11.2 SM4 19805760 20336087 530327 0 24 G 9,08E-30 15q11.2 SM48 18824422 20029853 1205431 0 43 G 1,85E-79 15q11.2 SM98 18835460 20366870 1531410 0 47 G 5,64E-45 LOC727924, OR4M2, OR4N4, LOC650137, GOLGA8D, LOC283767 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2, OR4N4, LOC650137 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2, OR4N4, LOC650137, GOLGA8D, LOC283767 hsa-mir-1268 ++ hsa-mir-1268 ++ hsa-mir-1268 ++ 15q25.3 SM5 84564656 84700852 136196 0 13 G 1,48E-19 AGBL1 - + 15q25.3 SM98 84627424 84700852 73428 0 8 G 6,95E-13 AGBL1 - + 16p13.3 - p13.2 SM76 6243005 6328849 85844 0 7 P 2,19E-21 A2BP1 - + 17q25.3 SM28 75294309 75555217 260908 0 21 G 2,36E-21 ENPP7, CBX2, CBX2, CBX8, CBX4, TBC1D16 - ++ 18q12.1 VCS 27225938 27298267 72329 0 7 G 2,46E-19 DSG4, DSG4, DSG3 - + 19p12 SM26 20399500 20493601 94101 0 5 P 1,09E-13 ZNF826 - ++ 19p13.3 VCS 721124 746808 25684 0 3 G 2,10E-13 - - + 21p11.2 - p11.1 SM5 9888612 10116158 227546 0 12 P 1,94E-15 TPTE, BAGE5, BAGE4, BAGE3, BAGE2, BAGE - ++ 22q11.21 VCS 18513409 18544726 31317 0 4 G 7,47E-18 ZDHHC8 - ++ 22q11.23 SM28 SM173 23994418 24253362 23994418 24253362 258944 258944 1% 1% 21 21 G P 2,14E-15 4,42E-32 IGLL3, LRP5L IGLL3, LRP5L - - ++ ++ Xp22.11 SM4 22870465 22931729 61264 0 6 P 4,40E-26 DDX53 - + Xq22.2 SM26 1,03E+08 1,03E+08 102278 0 10 G 1,83E-15 TMSB15B, H2BFXP, H2BFWT - ++ 83
Cont/ Tabela 13 CNVs Raras Exclusivas G2 Região Cromossômica 1p21.1 Casos Start End Tamanho (pb) Grupo Controle Nº <strong>de</strong> Sondas SM88 1,04E+08 1,04E+08 113149 0 6 G 1,67E-13 Evento P valor Genes MicroRNA Presença <strong>de</strong> CNVs AMY2B, LOC648740, AMY2A, AMY1A, AMY1C, AMY1B - ++ SL154 1,04E+08 1,04E+08 113149 0 6 G 1,74E-27 AMY2B, LOC648740, AMY2A, AMY1A, AMY1C, AMY1B - ++ 1p36.33 SM47 842526 870300 27774 0 3 G 3,31E-12 FLJ39609, SAMD11, NOC2L - + 1p36.33 SM47 1147038 1436882 289844 0 9 G 2,34E-17 SDF4, B3GALT6, FAM132A, UBE2J2, LOC100128842, SCNN1D, ACAP3, PUSL1, CPSF3L, GLTPD1, TAS1R3, DVL1, MXRA8, AURKAIP1, CCNL2, LOC148413, MRPL20, LOC441869, TMEM88B, VWA1, ATAD3C, ATAD3B - ++ 1q21.1 SM77 1,47E+08 1,48E+08 164561 1% 13 P 7,64E-16 - - ++ 1q21.1 - q21.2 MT28 1,47E+08 1,48E+08 878892 1% 18 P 2,19E-14 LOC645166, LOC645166, LOC388692, FCGR1C, PPIAL4C, PPIAL4A, LOC728855, FCGR1A, HIST2H2BF, HIST2H3D, HIST2H4A, HIST2H4B, HIST2H3C, HIST2H3A, HIST2H2AA4, HIST2H2AA3 - ++ 1q44 MT39 2,47E+08 2,47E+08 69895 1% 6 G 3,76E-13 OR2T10, OR2T11, OR2T35 - ++ 2p11.2 SM88 85641167 85677891 36724 0 4 G 6,92E-13 GGCX, VAMP8, VAMP5, RNF181 - + 2p11.2 - p11.1 SL24 89387396 91057322 1669926 0 18 P 3,33E-24 - - ++ 2p11.2 - q11.1 MT16 89222763 94892966 5670203 0 31 P 5,90E-17 LOC654342, GGT8P, ANKRD20B - ++ 2p22.2 SL55 38254265 38346267 92002 0 9 P 2,03E-28 C2orf58 - + 2q32.1 SM47 1,86E+08 1,86E+08 213053 0 10 P 1,13E-21 - - + 2q37.3 SM150 2,43E+08 2,43E+08 152305 0 13 P 3,87E-25 - - ++ 3p24.2 SM64 26254389 26371477 117088 0 4 P 2,07E-14 - - + 3q26.1 SM64 1,64E+08 1,64E+08 124842 0 7 G 1,47E-14 - - ++ SM100 1,64E+08 1,64E+08 124842 0 7 G 1,15E-16 - - ++ 84
- Page 1 and 2:
VARIAÇÃO NO NÚMERO DE CÓPIAS GE
- Page 3 and 4:
A minha família!!!! DEDICATÓRIA
- Page 5 and 6:
À minha orientadora... Dra Silvia
- Page 7 and 8:
As Instituições de Fomento... FAP
- Page 9 and 10:
Entre os pacientes sem mutação, f
- Page 11 and 12:
(exclusive from group 1) and FOXP1
- Page 13 and 14:
Figura 11 Representação esquemát
- Page 15 and 16:
LISTA DE TABELAS Tabela 1 Classific
- Page 17 and 18:
Tabela 25 Alterações identificada
- Page 19 and 20:
LISTA DE SIGLAS E ABREVIATURAS aCGH
- Page 21 and 22:
UTR* Untranslated region VNTR* Vari
- Page 23 and 24:
4.2.3 Análise de CNVs entre os fam
- Page 25 and 26:
O câncer colorretal (CCR) é o ter
- Page 27 and 28:
vezes, está associado com a histó
- Page 29 and 30:
análise de MSI é realizada pela P
- Page 31 and 32:
(2010) relataram que o tumor extrac
- Page 33 and 34:
1.2 SÍNDROME DE CÂNCER DE MAMA-C
- Page 35 and 36:
PMS2). Segundo os autores, é mais
- Page 37 and 38:
contribuir para a patogênese e pro
- Page 39 and 40:
contém um elemento upstream que re
- Page 41 and 42:
2 OBJETIVOS 2.1 OBJETIVO PRINCIPAL
- Page 43 and 44:
Figura 1 - Fluxograma representando
- Page 45 and 46:
o SMCMH2: pelo menos um indivíduo
- Page 47 and 48:
Tabela 1 - Dados clínicos e histop
- Page 49 and 50:
Tabela 2 - Dados clínicos e histop
- Page 51 and 52:
Tabela 3 - Dados clínicos e histop
- Page 53 and 54:
(1100delC) e TP53. Neste estudo, fo
- Page 55 and 56: Tabela 5 - Iniciadores utilizados n
- Page 57 and 58: Tabela 6 - Condições da PCR para
- Page 59 and 60: As sequências alteradas foram clas
- Page 61 and 62: por 2 horas e 65°C por 15 min. Foi
- Page 63 and 64: As regiões identificadas como alte
- Page 65 and 66: (http://www.ncbi.nlm.nih.gov, http:
- Page 67 and 68: Figura 2 - Representação gráfica
- Page 69 and 70: O gene de referência, GAPDH, é fr
- Page 71 and 72: (tissue microarray - TMA), contendo
- Page 73 and 74: citoplasmática moderada, porém em
- Page 75 and 76: 4 RESULTADOS 4.1 SEQUENCIAMENTO 4.1
- Page 77 and 78: Tabela 10 - Mutações não patogê
- Page 79 and 80: Figura 5 - Representação gráfica
- Page 81 and 82: número maior de CNVs, quando compa
- Page 83 and 84: 21 não apresentaram CNVs. Por outr
- Page 85 and 86: A. C. Figura 7 - Representação gr
- Page 87 and 88: envolvida em perda genômica, prese
- Page 89 and 90: Cont/ Tabela 11 Região Cromossômi
- Page 91 and 92: Cont/ Tabela 11 Região Cromossômi
- Page 93 and 94: Cont/ Tabela 12 Região Cromossômi
- Page 95 and 96: Cont/ Tabela 12 Região Cromossômi
- Page 97 and 98: Cont/ Tabela 11 Região Cromossômi
- Page 99 and 100: Cont/ Tabela 11 Região Cromossômi
- Page 101 and 102: As CNVs raras e novas raras foram c
- Page 103 and 104: Cont/ Tabela 13 Região Cromossômi
- Page 105: Cont/ Tabela 13 Região Cromossômi
- Page 109 and 110: Cont/ Tabela 13 Região Cromossômi
- Page 111 and 112: Cont/ Tabela 13 Região Cromossômi
- Page 113 and 114: Cont/ Tabela 13 Região Cromossômi
- Page 115 and 116: Cont/ Tabela 14 CNVs Novas Raras Ex
- Page 117 and 118: Tabela 15 - Alterações com genes
- Page 119 and 120: Tabela 16 - Funções dos genes map
- Page 121 and 122: Entre as CNVs novas raras comuns ao
- Page 123 and 124: 100
- Page 125 and 126: 102 Entre as CNVs novas raras exclu
- Page 127 and 128: 14q32.11: gene FOXN3 End: 89.136.41
- Page 129 and 130: 7p22.2: gene MAD1L1 Start: 2.106.88
- Page 131 and 132: 108 Entre as CNVs novas raras exclu
- Page 133 and 134: Start: 71.124.097 3p14.1: gene FOXP
- Page 135 and 136: Start: 71.478.161 17q25.1: genes AC
- Page 137 and 138: 7q36.3: gene PTPRN2E2 Start: 158.00
- Page 139 and 140: Start: 49.039.910 13q14.3: gene RCB
- Page 141 and 142: mutações no gene de reparo MLH1 (
- Page 143 and 144: Tabela 18 - Alterações identifica
- Page 145 and 146: Cont/ Tabela 18 Casos SL36 (G2) Reg
- Page 147 and 148: 124 Na Tabela 20 estão representad
- Page 149 and 150: família foi identificada apenas um
- Page 151 and 152: Tabela 21 - Alterações identifica
- Page 153 and 154: Tabela 22 - Alterações identifica
- Page 155 and 156: Tabela 23 - Alterações identifica
- Page 157 and 158:
Cont/ Tabela 23 Casos Região Cromo
- Page 159 and 160:
Tabela 25 - Alterações identifica
- Page 161 and 162:
Cont/ Tabela 26 Casos Região Cromo
- Page 163 and 164:
Figura 17 - Heredograma do caso SM5
- Page 165 and 166:
142 A plataforma de 4x180K (Agilent
- Page 167 and 168:
Start: 78.990.568 3p12.3: gene ROBO
- Page 169 and 170:
146 Após a identificação, por CG
- Page 171 and 172:
Figura 21 - Representação gráfic
- Page 173 and 174:
Tabela 29 - Cálculo do intervalo d
- Page 175 and 176:
Figura 23 - Análise gráfica dos r
- Page 177 and 178:
epresenta uma comparação em barra
- Page 179 and 180:
156 Após a caracterização da ext
- Page 181 and 182:
ROBO1. Em 61,12% das amostras foi d
- Page 183 and 184:
160 Tabela 33 - Associação entre
- Page 185 and 186:
162 Não houve associação signifi
- Page 187 and 188:
164 Tabela 34 - Associação entre
- Page 189 and 190:
4.3.2 Família SM89 166 Após a con
- Page 191 and 192:
168 No exame clínico, a probanda e
- Page 193 and 194:
170 A SM89.2 (III:3), negativa para
- Page 195 and 196:
172 A SM89.5 (IV:5), positiva para
- Page 197 and 198:
174 A presença de pequenos cromoss
- Page 199 and 200:
176 BRCA1 apresentaram 12 CNVs (SM8
- Page 201 and 202:
Tabela 37 - Alterações identifica
- Page 203 and 204:
Cont/ Tabela 37 Casos Região Cromo
- Page 205 and 206:
5 DISCUSSÃO 182 As variações gen
- Page 207 and 208:
câncer de mama e cólon. Grande pa
- Page 209 and 210:
para mutação nos genes de predisp
- Page 211 and 212:
N (SLC38A3 e SLC38A5), porém todos
- Page 213 and 214:
alterações, GRM1, MAD1L1 e NPAS1
- Page 215 and 216:
192 Neste estudo, o ganho genômico
- Page 217 and 218:
sugeriram que a nova variante do ge
- Page 219 and 220:
como linfomas, além de uma associa
- Page 221 and 222:
taxas de crescimento celular quando
- Page 223 and 224:
200 Segundo dados da literatura, os
- Page 225 and 226:
de CNVs também foi observado nas p
- Page 227 and 228:
5.1.3 Análise de CNVs entre os fam
- Page 229 and 230:
colorretal, quatro em linhagem celu
- Page 231 and 232:
produzidos durante o catabolismo do
- Page 233 and 234:
envolvendo essa região cromossômi
- Page 235 and 236:
tem sua eficiência 10 vezes reduzi
- Page 237 and 238:
214 As GTPases são responsáveis p
- Page 239 and 240:
carcinomas primários de cabeça e
- Page 241 and 242:
com história familial avaliadas no
- Page 243 and 244:
também demonstraram que pacientes
- Page 245 and 246:
cromossômicas foram observadas tan
- Page 247 and 248:
A paciente SM87 (grupo 2) apresento
- Page 249 and 250:
226 Banyard J, Barrows C, Zetter BR
- Page 251 and 252:
228 Chung GT, Sundaresan V, Hasleto
- Page 253 and 254:
230 Fre S, Huyghe M, Mourikis P, Ro
- Page 255 and 256:
232 Höglund PJ, Nordström KJ, Sch
- Page 257 and 258:
234 Kuiper RP, Ligtenberg MJ, Hooge
- Page 259 and 260:
236 Mills RE, Walter K, Stewart C,
- Page 261 and 262:
238 Peltomäki P, Vasen HF. Mutatio
- Page 263 and 264:
240 Selamat SA, Galler JS, Joshi AD
- Page 265 and 266:
242 Thélu J, Rossio P, Favier B. N
- Page 267 and 268:
244 Wang J, Luo MH, Zhang ZX, et al
- Page 269:
Anexo 1 - Heredogramas
- Page 324:
Anexo 3 - Critérios de Bethesda pa