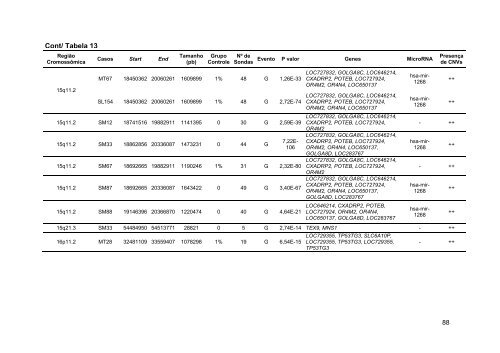
Cont/ Tabela 13 Região Cromossômica Casos Start End Tamanho (pb) Grupo Controle Nº <strong>de</strong> Sondas Evento P valor Genes MicroRNA Presença <strong>de</strong> CNVs 11q11 SM100 55157878 55187482 29604 0 4 P 3,20E-13 OR4P4, OR4S2 - ++ 11q11 SM7 SM150 55141993 55141993 55207505 55207505 65512 65512 0 0 7 7 G G 2,22E-16 2,15E-16 OR4P4, OR4S2, OR4C6 OR4P4, OR4S2, OR4C6 - - ++ ++ 12p13.31 SM33 9528390 9589925 61535 1% 6 G 2,93E-15 - - ++ 12q24.33 SM87 1,3E+08 1,3E+08 82383 0 6 P 1,09E-37 - - ++ 13q21.1 SM63 56610686 56691555 80869 0 5 P 1,42E-25 PRR20, LOC729233, LOC729240, LOC729246, LOC729250, LOC729240, PRR20, LOC729233, LOC729246, LOC729250, LOC729240, LOC729233, PRR20, LOC729246, LOC729250, LOC729240, LOC729233, PRR20, LOC729246, LOC729250, PRR20, LOC729233, LOC729240, LOC729246, LOC729250 - ++ 13q21.32 SM34 64630281 64779577 149296 0 6 P 3,85E-16 - - + 13q31.1 SM47 83920574 83973495 52921 0 4 G 4,34E-14 - - + 14q11.2 SM7 19286928 19484213 197285 0 11 G 1,59E-16 OR4M1, OR4N2, OR4K2, OR4K5, OR4K1 - ++ 14q24.3 SM59 73060101 73092218 32117 0 4 P 4,36E-14 HEATR4, ACOT1 - ++ 14q32.33 SL24 1,06E+08 1,06E+08 40274 1% 5 P 3,60E-20 - - ++ 14q32.33 SM100 1,06E+08 1,06E+08 246133 1% 18 P 9,83E-58 - - ++ 14q32.33 SM100 1,06E+08 1,06E+08 455283 0 38 G 1,66E-21 LOC100133469 - ++ 14q32.33 SM47 1,04E+08 1,04E+08 17416 0 4 G 7,57E-15 ASPG - + 15q11.2 MT16 18450362 19882911 1432549 0 32 G 8,83E-59 15q11.2 MT39 18741516 20317192 1575676 0 47 P 2,61E-27 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2, OR4N4, LOC650137, GOLGA8D, LOC283767 - ++ hsa-mir- 1268 87 ++
Cont/ Tabela 13 Região Cromossômica 15q11.2 Casos Start End Tamanho (pb) Grupo Controle Nº <strong>de</strong> Sondas MT67 18450362 20060261 1609899 1% 48 G 1,26E-33 SL154 18450362 20060261 1609899 1% 48 G 2,72E-74 15q11.2 SM12 18741516 19882911 1141395 0 30 G 2,59E-39 15q11.2 SM33 18862856 20336087 1473231 0 44 G Evento P valor Genes MicroRNA Presença <strong>de</strong> CNVs 7,22E- 106 15q11.2 SM67 18692665 19882911 1190246 1% 31 G 2,32E-80 15q11.2 SM87 18692665 20336087 1643422 0 49 G 3,40E-67 15q11.2 SM88 19146396 20366870 1220474 0 40 G 4,64E-21 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2, OR4N4, LOC650137 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2, OR4N4, LOC650137 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2, OR4N4, LOC650137, GOLGA8D, LOC283767 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2 LOC727832, GOLGA8C, LOC646214, CXADRP2, POTEB, LOC727924, OR4M2, OR4N4, LOC650137, GOLGA8D, LOC283767 LOC646214, CXADRP2, POTEB, LOC727924, OR4M2, OR4N4, LOC650137, GOLGA8D, LOC283767 hsa-mir- 1268 hsa-mir- 1268 88 ++ ++ - ++ hsa-mir- 1268 ++ - ++ 15q21.3 SM33 54484950 54513771 28821 0 5 G 2,74E-14 TEX9, MNS1 - ++ 16p11.2 MT28 32481109 33559407 1078298 1% 19 G 6,54E-15 LOC729355, TP53TG3, SLC6A10P, LOC729355, TP53TG3, LOC729355, TP53TG3 hsa-mir- 1268 hsa-mir- 1268 ++ ++ - ++
- Page 1 and 2:
VARIAÇÃO NO NÚMERO DE CÓPIAS GE
- Page 3 and 4:
A minha família!!!! DEDICATÓRIA
- Page 5 and 6:
À minha orientadora... Dra Silvia
- Page 7 and 8:
As Instituições de Fomento... FAP
- Page 9 and 10:
Entre os pacientes sem mutação, f
- Page 11 and 12:
(exclusive from group 1) and FOXP1
- Page 13 and 14:
Figura 11 Representação esquemát
- Page 15 and 16:
LISTA DE TABELAS Tabela 1 Classific
- Page 17 and 18:
Tabela 25 Alterações identificada
- Page 19 and 20:
LISTA DE SIGLAS E ABREVIATURAS aCGH
- Page 21 and 22:
UTR* Untranslated region VNTR* Vari
- Page 23 and 24:
4.2.3 Análise de CNVs entre os fam
- Page 25 and 26:
O câncer colorretal (CCR) é o ter
- Page 27 and 28:
vezes, está associado com a histó
- Page 29 and 30:
análise de MSI é realizada pela P
- Page 31 and 32:
(2010) relataram que o tumor extrac
- Page 33 and 34:
1.2 SÍNDROME DE CÂNCER DE MAMA-C
- Page 35 and 36:
PMS2). Segundo os autores, é mais
- Page 37 and 38:
contribuir para a patogênese e pro
- Page 39 and 40:
contém um elemento upstream que re
- Page 41 and 42:
2 OBJETIVOS 2.1 OBJETIVO PRINCIPAL
- Page 43 and 44:
Figura 1 - Fluxograma representando
- Page 45 and 46:
o SMCMH2: pelo menos um indivíduo
- Page 47 and 48:
Tabela 1 - Dados clínicos e histop
- Page 49 and 50:
Tabela 2 - Dados clínicos e histop
- Page 51 and 52:
Tabela 3 - Dados clínicos e histop
- Page 53 and 54:
(1100delC) e TP53. Neste estudo, fo
- Page 55 and 56:
Tabela 5 - Iniciadores utilizados n
- Page 57 and 58:
Tabela 6 - Condições da PCR para
- Page 59 and 60: As sequências alteradas foram clas
- Page 61 and 62: por 2 horas e 65°C por 15 min. Foi
- Page 63 and 64: As regiões identificadas como alte
- Page 65 and 66: (http://www.ncbi.nlm.nih.gov, http:
- Page 67 and 68: Figura 2 - Representação gráfica
- Page 69 and 70: O gene de referência, GAPDH, é fr
- Page 71 and 72: (tissue microarray - TMA), contendo
- Page 73 and 74: citoplasmática moderada, porém em
- Page 75 and 76: 4 RESULTADOS 4.1 SEQUENCIAMENTO 4.1
- Page 77 and 78: Tabela 10 - Mutações não patogê
- Page 79 and 80: Figura 5 - Representação gráfica
- Page 81 and 82: número maior de CNVs, quando compa
- Page 83 and 84: 21 não apresentaram CNVs. Por outr
- Page 85 and 86: A. C. Figura 7 - Representação gr
- Page 87 and 88: envolvida em perda genômica, prese
- Page 89 and 90: Cont/ Tabela 11 Região Cromossômi
- Page 91 and 92: Cont/ Tabela 11 Região Cromossômi
- Page 93 and 94: Cont/ Tabela 12 Região Cromossômi
- Page 95 and 96: Cont/ Tabela 12 Região Cromossômi
- Page 97 and 98: Cont/ Tabela 11 Região Cromossômi
- Page 99 and 100: Cont/ Tabela 11 Região Cromossômi
- Page 101 and 102: As CNVs raras e novas raras foram c
- Page 103 and 104: Cont/ Tabela 13 Região Cromossômi
- Page 105 and 106: Cont/ Tabela 13 Região Cromossômi
- Page 107 and 108: Cont/ Tabela 13 CNVs Raras Exclusiv
- Page 109: Cont/ Tabela 13 Região Cromossômi
- Page 113 and 114: Cont/ Tabela 13 Região Cromossômi
- Page 115 and 116: Cont/ Tabela 14 CNVs Novas Raras Ex
- Page 117 and 118: Tabela 15 - Alterações com genes
- Page 119 and 120: Tabela 16 - Funções dos genes map
- Page 121 and 122: Entre as CNVs novas raras comuns ao
- Page 123 and 124: 100
- Page 125 and 126: 102 Entre as CNVs novas raras exclu
- Page 127 and 128: 14q32.11: gene FOXN3 End: 89.136.41
- Page 129 and 130: 7p22.2: gene MAD1L1 Start: 2.106.88
- Page 131 and 132: 108 Entre as CNVs novas raras exclu
- Page 133 and 134: Start: 71.124.097 3p14.1: gene FOXP
- Page 135 and 136: Start: 71.478.161 17q25.1: genes AC
- Page 137 and 138: 7q36.3: gene PTPRN2E2 Start: 158.00
- Page 139 and 140: Start: 49.039.910 13q14.3: gene RCB
- Page 141 and 142: mutações no gene de reparo MLH1 (
- Page 143 and 144: Tabela 18 - Alterações identifica
- Page 145 and 146: Cont/ Tabela 18 Casos SL36 (G2) Reg
- Page 147 and 148: 124 Na Tabela 20 estão representad
- Page 149 and 150: família foi identificada apenas um
- Page 151 and 152: Tabela 21 - Alterações identifica
- Page 153 and 154: Tabela 22 - Alterações identifica
- Page 155 and 156: Tabela 23 - Alterações identifica
- Page 157 and 158: Cont/ Tabela 23 Casos Região Cromo
- Page 159 and 160: Tabela 25 - Alterações identifica
- Page 161 and 162:
Cont/ Tabela 26 Casos Região Cromo
- Page 163 and 164:
Figura 17 - Heredograma do caso SM5
- Page 165 and 166:
142 A plataforma de 4x180K (Agilent
- Page 167 and 168:
Start: 78.990.568 3p12.3: gene ROBO
- Page 169 and 170:
146 Após a identificação, por CG
- Page 171 and 172:
Figura 21 - Representação gráfic
- Page 173 and 174:
Tabela 29 - Cálculo do intervalo d
- Page 175 and 176:
Figura 23 - Análise gráfica dos r
- Page 177 and 178:
epresenta uma comparação em barra
- Page 179 and 180:
156 Após a caracterização da ext
- Page 181 and 182:
ROBO1. Em 61,12% das amostras foi d
- Page 183 and 184:
160 Tabela 33 - Associação entre
- Page 185 and 186:
162 Não houve associação signifi
- Page 187 and 188:
164 Tabela 34 - Associação entre
- Page 189 and 190:
4.3.2 Família SM89 166 Após a con
- Page 191 and 192:
168 No exame clínico, a probanda e
- Page 193 and 194:
170 A SM89.2 (III:3), negativa para
- Page 195 and 196:
172 A SM89.5 (IV:5), positiva para
- Page 197 and 198:
174 A presença de pequenos cromoss
- Page 199 and 200:
176 BRCA1 apresentaram 12 CNVs (SM8
- Page 201 and 202:
Tabela 37 - Alterações identifica
- Page 203 and 204:
Cont/ Tabela 37 Casos Região Cromo
- Page 205 and 206:
5 DISCUSSÃO 182 As variações gen
- Page 207 and 208:
câncer de mama e cólon. Grande pa
- Page 209 and 210:
para mutação nos genes de predisp
- Page 211 and 212:
N (SLC38A3 e SLC38A5), porém todos
- Page 213 and 214:
alterações, GRM1, MAD1L1 e NPAS1
- Page 215 and 216:
192 Neste estudo, o ganho genômico
- Page 217 and 218:
sugeriram que a nova variante do ge
- Page 219 and 220:
como linfomas, além de uma associa
- Page 221 and 222:
taxas de crescimento celular quando
- Page 223 and 224:
200 Segundo dados da literatura, os
- Page 225 and 226:
de CNVs também foi observado nas p
- Page 227 and 228:
5.1.3 Análise de CNVs entre os fam
- Page 229 and 230:
colorretal, quatro em linhagem celu
- Page 231 and 232:
produzidos durante o catabolismo do
- Page 233 and 234:
envolvendo essa região cromossômi
- Page 235 and 236:
tem sua eficiência 10 vezes reduzi
- Page 237 and 238:
214 As GTPases são responsáveis p
- Page 239 and 240:
carcinomas primários de cabeça e
- Page 241 and 242:
com história familial avaliadas no
- Page 243 and 244:
também demonstraram que pacientes
- Page 245 and 246:
cromossômicas foram observadas tan
- Page 247 and 248:
A paciente SM87 (grupo 2) apresento
- Page 249 and 250:
226 Banyard J, Barrows C, Zetter BR
- Page 251 and 252:
228 Chung GT, Sundaresan V, Hasleto
- Page 253 and 254:
230 Fre S, Huyghe M, Mourikis P, Ro
- Page 255 and 256:
232 Höglund PJ, Nordström KJ, Sch
- Page 257 and 258:
234 Kuiper RP, Ligtenberg MJ, Hooge
- Page 259 and 260:
236 Mills RE, Walter K, Stewart C,
- Page 261 and 262:
238 Peltomäki P, Vasen HF. Mutatio
- Page 263 and 264:
240 Selamat SA, Galler JS, Joshi AD
- Page 265 and 266:
242 Thélu J, Rossio P, Favier B. N
- Page 267 and 268:
244 Wang J, Luo MH, Zhang ZX, et al
- Page 269:
Anexo 1 - Heredogramas
- Page 324:
Anexo 3 - Critérios de Bethesda pa