Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
5 Ergebnisse<br />
NHA<br />
hAgo2<br />
A<br />
110<br />
100<br />
B<br />
400<br />
Rd R (nm)<br />
90<br />
80<br />
70<br />
60<br />
50<br />
Rd R (nm)<br />
300<br />
200<br />
100<br />
4°C<br />
25°C<br />
37°C<br />
C<br />
Rd (nm)<br />
40<br />
80<br />
70<br />
60<br />
50<br />
40<br />
30<br />
10 20 30 40 50<br />
Temperatur (°C)<br />
mit guide RNA<br />
ohne guide RNA<br />
20<br />
0 20 40 60 80 100 120<br />
Zeit (min)<br />
D<br />
rel. Rd<br />
0<br />
0 20 40 60 80 100 120<br />
Zeit (min)<br />
10<br />
9<br />
8<br />
7<br />
6<br />
5<br />
4<br />
3<br />
2<br />
1<br />
NHA‐hAgo2<br />
NHA‐hAgo2 + as2B<br />
NHA‐hAgo2 + as2B + ICAM‐1‐IVT<br />
NHA‐hAgo2 + ICAM‐1‐IVT<br />
NHA‐hAgo2 + asLam<br />
+ ICAM‐1‐IVT<br />
0<br />
0 10 20 30 40 50 60<br />
Temperatur (°C)<br />
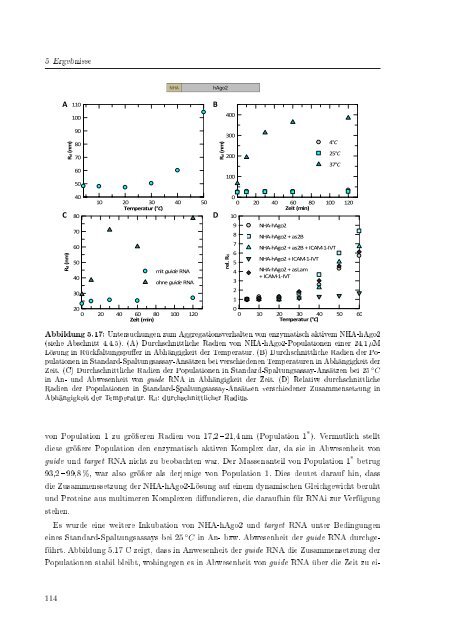
Abbildung 5.17: Untersuchungen zum Aggregationsverhalten von enzymatisch aktivem NHA-hAgo2<br />
(siehe Abschnitt 4.4.5). (A) Durchschnittliche Radien von NHA-hAgo2-Populationen einer 24,1 µM<br />
Lösung in Rückfaltungspuer in Abhängigkeit <strong>der</strong> Temperatur. (B) Durchschnittliche Radien <strong>der</strong> Populationen<br />
in Standard-Spaltungsassay-Ansätzen bei verschiedenen Temperaturen in Abhängigkeit <strong>der</strong><br />
Zeit. (C) Durchschnittliche Radien <strong>der</strong> Populationen in Standard-Spaltungsassay-Ansätzen bei 25 ◦ C<br />
in An- und Abwesenheit von guide RNA in Abhängigkeit <strong>der</strong> Zeit. (D) Relative durchschnittliche<br />
Radien <strong>der</strong> Populationen in Standard-Spaltungsassay-Ansätzen verschiedener Zusammensetzung in<br />
Abhängigkeit <strong>der</strong> Temperatur. R d : durchschnittlicher Radius.<br />
von Population 1 zu gröÿeren Radien von 17,2 21,4 nm (Population 1 * ). Vermutlich stellt<br />
diese gröÿere Population den enzymatisch aktiven Komplex dar, da sie in Abwesenheit von<br />
guide und target RNA nicht zu beobachten war. Der Massenanteil von Population 1 * betrug<br />
93,2 99,8 %, war also gröÿer als <strong>der</strong>jenige von Population 1. Dies deutet darauf hin, dass<br />
die Zusammenssetzung <strong>der</strong> NHA-hAgo2-Lösung auf einem dynamischen Gleichgewicht beruht<br />
und Proteine aus multimeren Komplexen diundieren, die daraufhin für RNAi zur Verfügung<br />
stehen.<br />
Es wurde eine weitere Inkubation von NHA-hAgo2 und target RNA unter Bedingungen<br />
eines Standard-Spaltungsassays bei 25 ◦ C in An- bzw. Abwesenheit <strong>der</strong> guide RNA durchgeführt.<br />
Abbildung 5.17 C zeigt, dass in Anwesenheit <strong>der</strong> guide RNA die Zusammensetzung <strong>der</strong><br />
Populationen stabil bleibt, wohingegen es in Abwesenheit von guide RNA über die Zeit zu ei-<br />
114