Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Erfolgreiche ePaper selbst erstellen
Machen Sie aus Ihren PDF Publikationen ein blätterbares Flipbook mit unserer einzigartigen Google optimierten e-Paper Software.
% Umsatz<br />
% Umsatz<br />
relativer Umsatz<br />
relativer Umsatz<br />
relativer Umsatz<br />
relativer Umsatz<br />
relativer Umsatz<br />
relativer Umsatz<br />
5.10 <strong>Charakterisierung</strong> <strong>der</strong> Produktfreisetzung nach target RNA-Spaltung<br />
1<br />
1<br />
0,8<br />
GST<br />
0,8<br />
hAgo2<br />
1<br />
0,6<br />
A<br />
90<br />
B<br />
1<br />
1<br />
0,6<br />
0,8<br />
0,4<br />
80<br />
0,8<br />
0,4<br />
0,6<br />
0,2<br />
50<br />
40<br />
30<br />
20<br />
10<br />
70<br />
60<br />
50<br />
40<br />
30<br />
20<br />
10<br />
0<br />
0 2000 4000 6000 8000<br />
guide RNA/target RNA<br />
Kombination<br />
P-as2B/<br />
s2B<br />
P-as2B-FAM/<br />
s2B<br />
P-as2B/<br />
s2B-BHQ<br />
P-as2B-FAM/<br />
s2B-BHQ<br />
Zeit (s)<br />
max. Umsatz<br />
(%)<br />
84,9<br />
(± 5,9)<br />
58,4<br />
(± 5,5)<br />
7,6<br />
(± 0,7)<br />
1,2<br />
(± 0,1)<br />
k gesamt<br />
(s -1 )<br />
0,0005<br />
(± 1 x 10 -4 )<br />
0,0004<br />
(± 9 x 10 -5 )<br />
0,0002<br />
(± 5 x 10 -5 )<br />
0,0002<br />
(± 4 x 10 -5 )<br />
0,6<br />
0,4<br />
1<br />
0,01<br />
0,1<br />
0,2<br />
0<br />
0,4<br />
0,2<br />
P-as2B/<br />
guide RNA/target RNA Kombination<br />
s2B<br />
0,2<br />
0<br />
P-as2B/<br />
P-as2B-FAM/<br />
guide RNA/target RNA Kombination<br />
0,1<br />
s2B<br />
s2B<br />
0<br />
P-as2B-FAM/ P-as2B/ P-as2B/<br />
guide RNA/target RNA Kombination<br />
s2B s2B s2B-BHQ<br />
0,01<br />
P-as2B/ P-as2B/ P-as2B-FAM/ P-as2B-FAM/<br />
s2B s2B-BHQ s2B s2B-BHQ<br />
P-as2B-FAM/ P-as2B-FAM/ P-as2B/<br />
guide s2B RNA/target s2B-BHQ RNA s2B-BHQ Umsatz von s2B-BHQ<br />
Kombination<br />
P-as2B/<br />
relativ zu s2B<br />
P-as2B-FAM/<br />
s2B-BHQ P-as2B/<br />
s2B<br />
P-as2B-FAM/<br />
s2B-BHQ<br />
1<br />
s2B-BHQ P-as2B/<br />
s2B-BHQ<br />
0,09<br />
P-as2B-FAM/<br />
s2B<br />
P-as2B-FAM/<br />
s2B-BHQ<br />
0<br />
guide RNA/target RNA Kombination<br />
1<br />
0,02<br />
0<br />
0 2000 4000 6000 8000<br />
Zeit (s)<br />
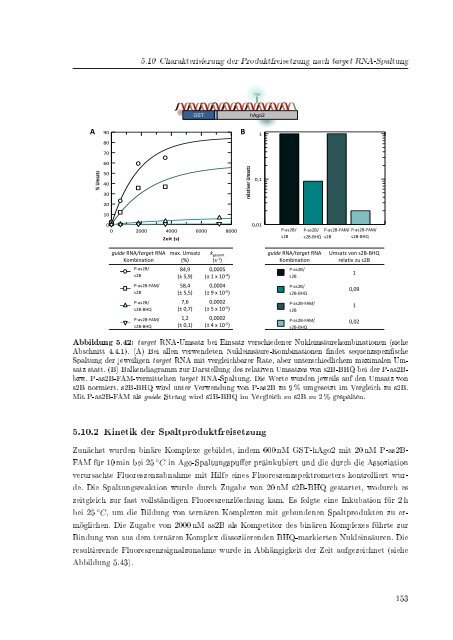
Abbildung 5.42: target RNA-Umsatz bei Einsatz verschiedener Nukleinsäurekombinationen (siehe<br />
Abschnitt 4.4.1). (A) Bei allen verwendeten Nukleinsäure-Kombinationen ndet sequenzspezische<br />
Spaltung <strong>der</strong> jeweiligen target RNA mit vergleichbarer Rate, aber unterschiedlichem maximalen Umsatz<br />
statt. (B) Balkendiagramm zur Darstellung des relativen Umsatzes von s2B-BHQ bei <strong>der</strong> P-as2Bbzw.<br />
P-as2B-FAM-<strong>vermittelten</strong> target RNA-Spaltung. Die Werte wurden jeweils auf den Umsatz von<br />
s2B normiert. s2B-BHQ wird unter Verwendung von P-as2B zu 9 % umgesetzt im Vergleich zu s2B.<br />
Mit P-as2B-FAM als guide Strang wird s2B-BHQ im Vergleich zu s2B zu 2 % gespalten.<br />
5.10.2 Kinetik <strong>der</strong> Spaltproduktfreisetzung<br />
Zunächst wurden binäre Komplexe gebildet, indem 600 nM GST-hAgo2 mit 20 nM P-as2B-<br />
FAM für 10 min bei 25 ◦ C in Ago-Spaltungspuer präinkubiert und die durch die Assoziation<br />
verursachte Fluoreszenzabnahme mit Hilfe eines Fluoreszenzspektrometers kontrolliert wurde.<br />
Die Spaltungsreaktion wurde durch Zugabe von 20 nM s2B-BHQ gestartet, wodurch es<br />
zeitgleich zur fast vollständigen Fluoreszenzlöschung kam. Es folgte eine Inkubation für 2 h<br />
bei 25 ◦ C, um die Bildung von ternären Komplexen mit gebundenen Spaltprodukten zu ermöglichen.<br />
Die Zugabe von 2000 nM as2B als Kompetitor des binären Komplexes führte zur<br />
Bindung von aus dem ternären Komplex dissoziierenden BHQ-markierten Nukleinsäuren. Die<br />
resultierende Fluoreszenzsignalzunahme wurde in Abhängigkeit <strong>der</strong> Zeit aufgezeichnet (siehe<br />
Abbildung 5.43).<br />
153