Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Biochemische Charakterisierung der siRNA-vermittelten Erkennung ...
Sie wollen auch ein ePaper? Erhöhen Sie die Reichweite Ihrer Titel.
YUMPU macht aus Druck-PDFs automatisch weboptimierte ePaper, die Google liebt.
% Umsatz<br />
% Umsatz<br />
5.9 <strong>Charakterisierung</strong> <strong>der</strong> <strong>siRNA</strong>-<strong>vermittelten</strong> target RNA-Spaltung durch hAgo2<br />
GST<br />
hAgo2<br />
A<br />
+ + + +<br />
+ + + +<br />
P-<br />
as2B<br />
+ + + +<br />
+ + + +<br />
P-<br />
si2B<br />
+ + + +<br />
+ + + +<br />
OHas2B<br />
+ +<br />
+ +<br />
P-<br />
asLam<br />
+ +<br />
+ +<br />
P-<br />
siLam<br />
+ +<br />
+ +<br />
OHasLam<br />
+ +<br />
+ +<br />
- -<br />
GST-hAgo2<br />
target RNA<br />
<strong>siRNA</strong><br />
t (min)<br />
IVT (140 nt)<br />
B<br />
100<br />
5’-Spaltprodukt<br />
(87 nt)<br />
80<br />
60<br />
100<br />
<strong>siRNA</strong>-Substrat max. Umsatz (%) k gesamt (s -1 )<br />
P-as2B 85,8 (± 3,8) 0,0005 (± 0,00007)<br />
40<br />
80<br />
OH-as2B<br />
78,4 (± 6,3) 0,0004 (± 0,0001)<br />
20<br />
60<br />
P-si2B<br />
27,6 (± 3,0) 0,0002 (± 0,00004)<br />
0<br />
0<br />
40<br />
2000 4000 6000 8000<br />
20<br />
Zeit (s)<br />
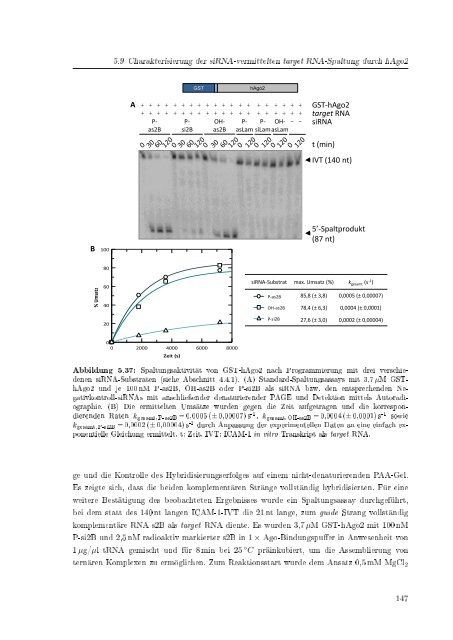
Abbildung 5.37: Spaltungsaktivität von GST-hAgo2 nach Programmierung mit drei verschiedenen<br />
<strong>siRNA</strong>-Substraten (siehe Abschnitt 4.4.1). (A) Standard-Spaltungsassays mit 3,7 µM GST-<br />
0<br />
hAgo2 und je 1000 nM P-as2B, 2000 4000 OH-as2B 6000 o<strong>der</strong>8000<br />
P-si2B als <strong>siRNA</strong> bzw. den entsprechenden Negativkontroll-<strong>siRNA</strong>s<br />
mit anschlieÿen<strong>der</strong><br />
Zeit (s)<br />
denaturieren<strong>der</strong> PAGE und Detektion mittels Autoradiographie.<br />
(B) Die ermittelten Umsätze wurden gegen die Zeit aufgetragen und die korrespondierenden<br />
Raten k gesamt, P-as2B = 0,0005 (± 0,00007) s -1 , k gesamt, OH-as2B = 0,0004 (± 0,0001) s -1 sowie<br />
k gesamt, P-si2B = 0,0002 (± 0,00004) s -1 durch Anpassung <strong>der</strong> experimentellen Daten an eine einfach exponentielle<br />
Gleichung ermittelt. t: Zeit. IVT: ICAM-1 in vitro Transkript als target RNA.<br />
ge und die Kontrolle des Hybridisierungserfolges auf einem nicht-denaturierenden PAA-Gel.<br />
Es zeigte sich, dass die beiden komplementären Stränge vollständig hybridisierten. Für eine<br />
weitere Bestätigung des beobachteten Ergebnisses wurde ein Spaltungsassay durchgeführt,<br />
bei dem statt des 140 nt langen ICAM-1-IVT die 21 nt lange, zum guide Strang vollständig<br />
komplementäre RNA s2B als target RNA diente. Es wurden 3,7 µM GST-hAgo2 mit 100 nM<br />
P-si2B und 2,5 nM radioaktiv markierter s2B in 1 × Ago-Bindungspuer in Anwesenheit von<br />
1 µg/µl tRNA gemischt und für 8 min bei 25 ◦ C präinkubiert, um die Assemblierung von<br />
ternären Komplexen zu ermöglichen. Zum Reaktionsstart wurde dem Ansatz 0,5 mM MgCl 2<br />
147